文摘gydF4y2Ba
神经元活动对自适应电路改造至关重要,但对基因组的稳定性构成一个固有风险postmitotic神经元的长寿命gydF4y2Ba1gydF4y2Ba,gydF4y2Ba2gydF4y2Ba,gydF4y2Ba3gydF4y2Ba,gydF4y2Ba4gydF4y2Ba,gydF4y2Ba5gydF4y2Ba。神经元是否有专门收购基因组保护机制,使他们能够承受几十年的潜在的破坏性刺激活动加剧的时期是未知的。我们确定一个活动依赖性DNA修复机制的一种新形式的NuA4-TIP60染色质修饰符组装在诱导激活神经元,neuronal-specific NPAS4转录因子。我们净化这个复杂的大脑并演示其功能引起依赖性活动改变神经元转录组和电路。通过描述景观activity-induced DNA双链断裂在大脑中,我们表明,NPAS4-NuA4循环结合破坏监管元素和招募额外的DNA修复机制来刺激他们的修复。基因调控受NPAS4-NuA4元素部分防止年龄相关性体细胞突变的积累。NPAS4-NuA4信号受损导致一连串的细胞缺陷,包括提供活动依赖性转录反应,失去控制神经抑制和基因组不稳定,减少生物的寿命达到高潮。此外,突变NuA4几个组件的复杂报告导致神经发育和自闭症谱系障碍。在一起,这些发现识别neuronal-specific复杂,夫妻神经活动直接基因组保存,中断可能导致发育障碍,神经细胞退化和老化。gydF4y2Ba
主要gydF4y2Ba
感官体验对适当的神经细胞成熟和电路可塑性至关重要gydF4y2Ba1gydF4y2Ba。信号级联由experience-driven神经元活动高潮的感应控制多样化的过程,如基因项目树突和突触增长,突触消除,抑制神经传递的招聘,适应的髓鞘形成gydF4y2Ba6gydF4y2Ba,gydF4y2Ba7gydF4y2Ba。然而,神经活动也威胁到基因组的完整性postmitotic神经元必须挺过一个生物体的生命周期。例如,加强代谢需求上升时期活动可能会增加氧化损伤积极基因组的转录区域gydF4y2Ba8gydF4y2Ba。Activity-induced转录本身对基因组稳定性进一步威胁,因为它与感应重复的DNA双链断裂(双边带)监管元素,比如stimulus-inducible基因的启动子gydF4y2Ba2gydF4y2Ba,gydF4y2Ba3gydF4y2Ba,gydF4y2Ba4gydF4y2Ba,gydF4y2Ba5gydF4y2Ba,gydF4y2Ba9gydF4y2Ba,gydF4y2Ba10gydF4y2Ba。尽管转录DNA断裂的耦合是观察到的细胞类型,这个过程神经元长期面临特殊的挑战,它不能使用replication-dependent DNA修复途径和拥有有限的再生机制来取代受损的细胞gydF4y2Ba11gydF4y2Ba。积累神经元基因组DNA损伤是神经退行性疾病的基本特性和生物的老化gydF4y2Ba12gydF4y2Ba,gydF4y2Ba13克ydF4y2Ba。因此,理解神经元的策略使用预防和修复损伤可能直接翻译人类长寿和衰老疗法。到目前为止,没有任何的例子neuronal-specific修理机械,减轻基因组不稳定的风险在加剧活动。通过调查活动依赖性转录项目特定神经元的特性,我们发现一个生化耦合神经元活动通过未知形式的DNA修复NuA4染色质remodeller-DNA维修复杂,组装在诱导neuronal-specific NPAS4转录因子。gydF4y2Ba
NPAS4-NuA4复杂的识别gydF4y2Ba
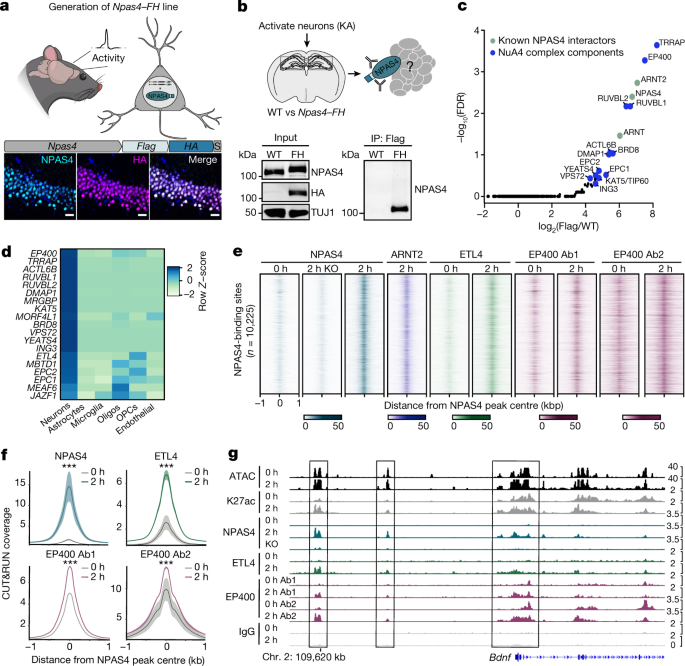
与大多数activity-inducible转录因子,广泛表达和引起的各种刺激,NPAS4选择性地表达在神经元膜depolarization-induced钙信号gydF4y2Ba14gydF4y2Ba。理解这个因素的函数,这是专门适应神经元活动,我们试图净化NPAS4-containing蛋白复合物从成年小鼠大脑。我们推断NPAS4可能组装成一个multisubunit复杂,扩大生化活动激活神经元。使用凝胶排阻层析法和non-denaturing凝胶电泳,我们观察到NPAS4驻留在高分子量约MDa的复杂。NPAS4的预测大小与异质二聚体伙伴(ARNT1和ARNT2)大约是175 kDa,这一发现表明,NPAS4与多个未知蛋白质伙伴(扩展数据图。gydF4y2Ba1gydF4y2Ba)。gydF4y2Ba
促进这个假定的NPAS4复杂的净化,我们生成的gydF4y2BaNpas4-Flag-HAgydF4y2Ba和gydF4y2BaArnt2-Flag-HAgydF4y2Ba敲入小鼠行表位标记的国旗和血凝素(HA)的羧基末端追加到NPAS4 ARNT2。在纯合子敲入小鼠,我们验证正确的标签和验证重叠基因插入内源性组织化学染色NPAS4 ARNT2和HA抗原决定基(无花果。gydF4y2Ba1 a, bgydF4y2Ba和扩展数据图。gydF4y2Ba1 b, cgydF4y2Ba)。我们还表明,野生型和标记NPAS4-Flag-HA (NPAS4-FH)表现出相似的表达水平和感应动力学(扩展数据图。gydF4y2Ba1 dgydF4y2Ba)。产生高水平的生化净化所需NPAS4,我们刺激海马的神经元gydF4y2BaNpas4-FHgydF4y2Ba老鼠通过低剂量的注射海人酸(KA),一个同步去偏光海马神经元谷氨酸受体激动剂。然后我们immunopurified NPAS4使用anti-Flag抗体和质谱(图执行。gydF4y2Ba1 cgydF4y2Ba和扩展数据图。gydF4y2Ba1 egydF4y2Ba)。质谱数据显示NPAS4和所有报告单元之间的相互作用的一个染色质修饰符,NuA4复杂,估计的大小大约是1.0 - -1.3的MDa(无花果。gydF4y2Ba1 cgydF4y2Ba和补充表gydF4y2Ba1gydF4y2Ba)gydF4y2Ba15gydF4y2Ba,gydF4y2Ba16gydF4y2Ba,gydF4y2Ba17gydF4y2Ba。gydF4y2Ba
一个gydF4y2Ba前,代的示意图gydF4y2BaNpas4gydF4y2Ba- - - - - -gydF4y2Ba跳频gydF4y2Ba小鼠模型。底,代表免疫组织化学(一式三份)执行NPAS4和海马体样本中HAgydF4y2BaNpas4-FHgydF4y2Ba老鼠2 h后KA刺激。规模的酒吧、25µm。gydF4y2BabgydF4y2Ba,NPAS4-FH和相关蛋白复合物与世隔绝anti-Flag免疫沉淀反应(IP)。代表免疫印迹(一式三份)执行anti-NPAS4抗体只证实了免疫沉淀反应gydF4y2BaNpas4-FHgydF4y2Ba老鼠。凝胶源数据,请参阅补充图。gydF4y2Ba1gydF4y2Ba。TUJ1处理控制运行在一个单独的凝胶。gydF4y2BacgydF4y2Ba,NPAS4-interacting蛋白质。日志gydF4y2Ba10gydF4y2Ba(错误发现率(罗斯福))与日志gydF4y2Ba2gydF4y2Ba改变折叠肽的变化得到anti-Flag在刺激免疫沉淀反应gydF4y2BaNpas4-FHgydF4y2Ba组织与野生型相比组织(gydF4y2BangydF4y2Ba= 3的8 - 10老鼠池),其次是质谱分析。绿点表示已知NPAS4扶少团团员。蓝色的点显示NuA4组件。gydF4y2BadgydF4y2Ba,表达水平的NuA4子单元在人类初级运动皮层细胞类型,显示为一行gydF4y2BaZgydF4y2Ba分数。snRNA-seq艾伦大脑研究所公布的数据gydF4y2Ba18gydF4y2Ba。寡核苷酸,少突胶质细胞;信息公开化,少突细胞前体细胞。gydF4y2BaegydF4y2BaNPAS4-NuA4组件,急忙逃走信号要么如果(0 h)或刺激(2 h)海马组织。每个NPAS4-binding网站表示为一条水平线高峰集中在峰会和扩展±1 kb。色彩强度代表阅读深度(归一化到1000万)所表示的每个因素的比例尺。数据绘制显示总信号从所有复制/因素。有所,抗体1(架a300型Bethyl - 541 a);Ab2,抗体2 (Abcam Ab5201)。为gydF4y2BaegydF4y2Ba- - - - - -gydF4y2BaggydF4y2Ba,gydF4y2BangydF4y2Ba每复制= 3 - 5老鼠汇集。补充表中复制数据提供gydF4y2Ba2gydF4y2Ba。gydF4y2BafgydF4y2Ba,总急忙逃走覆盖(片段深度/ bp /峰)NPAS4-binding网站。信号显示为均值±s.e.m。* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算的平均信号提取2 kb窗口集中在使用未配对NPAS4山峰,双尾Wilcoxon rank-sum测试。gydF4y2BaggydF4y2Ba综合基因组查看器(进口)跟踪NPAS4-NuA4急忙逃走activity-inducible基因信号gydF4y2Ba脑源性神经营养因子gydF4y2Ba。数据绘制显示总信号从所有复制/因素。的gydF4y2BaygydF4y2Ba轴显示标准化覆盖面扩展为每个因素选择的轨迹。gydF4y2Ba
我们首先证明co-immunoprecipitation NPAS4之间和几个NuA4子单元(TRRAP EP400和DMAP1)在视觉皮层使用曝光作为生理刺激诱导神经元活动(扩展数据图。gydF4y2Ba1 fgydF4y2Ba)。我们进一步通过免疫沉淀反应NPAS4或组件特征这一复杂的NuA4复杂,TIP60(也称为KAT5),其次是免疫印迹和质谱分析。这些实验证实,之间的交互NPAS4 NuA4复杂是互惠的。此外,NPAS4-ARNT2二聚体是最丰富的转录因子与大脑中的NuA4有关。此外,一个新的子单元的复杂,特征蛋白质ETL4不善,被确定(扩展数据无花果。gydF4y2Ba1 g-jgydF4y2Ba和gydF4y2Ba2 a, bgydF4y2Ba和补充表gydF4y2Ba1gydF4y2Ba)。我们观察到的几个单元NuA4刺激前复杂的相互作用,这表明NPAS4感应后,NPAS4-ARNT二聚体加入一个预先存在的复杂的(扩展数据图。gydF4y2Ba2 bgydF4y2Ba)。然而,我们不能排除这种可能性,其他子单元与,或转录后修饰被添加到NuA4复杂的活动。NPAS4是主要的诱导成分复杂的RNA水平(扩展数据图。gydF4y2Ba2摄氏度gydF4y2Ba)。无论是相关蛋白质NPAS3还是另一个activity-inducible因素,安全系数,co-immunoprecipitated NuA4组件在大脑中。这个结果强调了特异性的NPAS4-NuA4交互(扩展数据图。gydF4y2Ba2 bgydF4y2Ba)。此外,NPAS4,但不是其他activity-inducible转录因子,如安全系数和EGR1,与异源表达系统中组件NuA4 (HEK293T细胞)(扩展数据图。gydF4y2Ba2 d, egydF4y2Ba)。在人类和小鼠细胞,表达这些新19扶少团团员NPAS4浓缩在大脑与其他神经元细胞类型gydF4y2Ba18gydF4y2Ba(无花果。gydF4y2Ba1 dgydF4y2Ba和扩展数据图。gydF4y2Ba2 f, ggydF4y2Ba)。这一结果表明大脑内,NPAS4-NuA4复杂的神经元中具体的函数。gydF4y2Ba
确定NPAS4和NuA4硝唑在染色质,我们急忙逃走gydF4y2Ba19gydF4y2Ba获得的地图NPAS4-NuA4基因组绑定在刺激海马核分离小鼠注射低剂量的KA(无花果。gydF4y2Ba1 egydF4y2Ba和补充表gydF4y2Ba2gydF4y2Ba)。我们确认的特异性NPAS4急忙逃走信号通过执行NPAS4急忙逃走在核孤立如果大脑(没有NPAS4表示)和核独立于大脑的刺激gydF4y2BaNpas4gydF4y2Ba基因敲除小鼠。这个实验生成的列表10225年高信任度NPAS4-binding网站(无花果。gydF4y2Ba1 egydF4y2Ba和扩展数据图。gydF4y2Ba3得了gydF4y2Ba)。这些结合位点高度与NPAS4信号与测序(ChIP-seq)和染色质免疫沉淀反应化验显示浓缩的E-box和bHLH-PAS绑定图案(扩展数据图。gydF4y2Ba3 d, egydF4y2Ba)。NPAS4,其合作伙伴ARNT2 NuA4组件EP400和新发现的NuA4亚基ETL4也硝唑在基因组刺激神经元(无花果。gydF4y2Ba1比gydF4y2Ba和扩展数据图。gydF4y2Ba3 f, ggydF4y2Ba)。此外,绑定NPAS4和ETL4基因组高度诱导NPAS4地点(无花果。gydF4y2Ba1 fgydF4y2Ba)。相比之下,EP400出席NPAS4-binding网站之前刺激,这表明它可能是保留在这些网站缺乏NPAS4由于NuA4绑定到乙酰化组蛋白的能力gydF4y2Ba20.gydF4y2Ba或由EP400 NuA4-independent绑定(无花果。gydF4y2Ba1 f, ggydF4y2Ba)。然而,更多EP400急忙逃走信号观察到NPAS4网站缺乏安全系数比匡威(即安全系数的网站,但没有NPAS4)。这个结果表明NPAS4的特异性和EP400 co-binding而不是一个一般的招聘的EP400 activity-inducible转录因子(扩展数据图。gydF4y2Ba3 h,我gydF4y2Ba)。总之,我们的生化证据和基因组的绑定化验确定neuronal-specific形式NuA4复杂组装NPAS4在多个脑区活动依赖性的方式。gydF4y2Ba
NPAS4-NuA4-driven诱导基因项目gydF4y2Ba
我们下一个调查的功能NPAS4-NuA4复杂的大脑中。研究使用酵母、果蝇和non-neuronal细胞有两个活动归因于NuA4复杂:(1)控制通过染色质转录调控gydF4y2Ba15gydF4y2Ba,gydF4y2Ba16gydF4y2Ba,gydF4y2Ba17gydF4y2Ba和(2)协调修复DNA的双边带gydF4y2Ba21gydF4y2Ba,gydF4y2Ba22gydF4y2Ba,gydF4y2Ba23gydF4y2Ba,gydF4y2Ba24gydF4y2Ba,gydF4y2Ba25gydF4y2Ba,gydF4y2Ba26gydF4y2Ba。因此我们认为NPAS4的可能性,通过招聘NuA4,可能有两种用途。NPAS4的先前的研究表明,NPAS4-NuA4复杂可能在活动依赖性基因调控中起中心作用gydF4y2Ba14gydF4y2Ba,gydF4y2Ba27gydF4y2Ba。此外,双边带修复NuA4的作用表明,NPAS4可能有一个之前从未描述的功能神经元活动依赖性DNA修复启动子和增强子。我们检查了这两个函数的NPAS4-NuA4扰乱NPAS4或者TIP60, NuA4组蛋白乙酰转移酶的组成部分(参考文献。gydF4y2Ba15gydF4y2Ba,gydF4y2Ba16gydF4y2Ba)。gydF4y2Ba
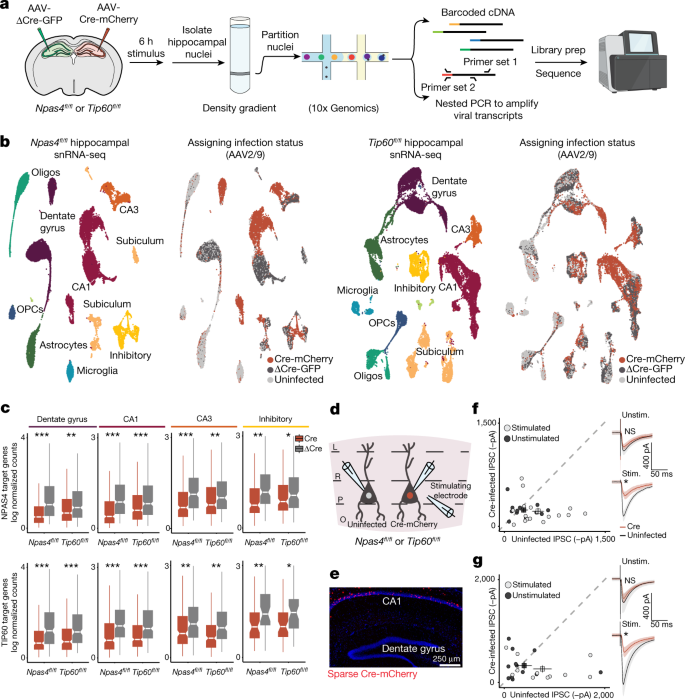
确定NPAS4 NuA4协调活动依赖性转录,我们注入gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba或gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba小鼠病毒表达Cre-mCherry或recombination-deficient版本的Cre(ΔCre-GFP)侧海马的单方面解除gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaTip60gydF4y2Ba(无花果。gydF4y2Ba2gydF4y2Ba和扩展数据图。gydF4y2Ba4得了gydF4y2Ba)。注意,损耗的gydF4y2BaTip60gydF4y2Ba不损害NPAS4感应(扩展数据图。gydF4y2Ba4 d, egydF4y2Ba)。我们服用低剂量的KA的神经元激活所有类出现在海马体中,收集核6 h后捕获最大感应NPAS4目标基因gydF4y2Ba14gydF4y2Ba和执行single-nucleus RNA-sequencing (snRNA-seq)(图。gydF4y2Ba2gydF4y2Ba和扩展数据图。gydF4y2Ba4外:我gydF4y2Ba)。在这两个gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba数据集,我们确定了10个主要细胞类型,包括5个神经元亚型(齿状回、CA1、CA3、菌丝层和抑制),和多个non-neuronal细胞类型。我们使用一个嵌套PCR策略作为一个额外的步骤在图书馆准备放大病毒记录。这个步骤使我们感染状况分配给每个原子核Cre-infected (cKO)ΔCre-infected(野生型)或未感染(无花果。gydF4y2Ba2 a, bgydF4y2Ba)。在这两个数据集,在每个神经元集群,细胞subclustered根据感染状况与ΔCre相比(Cre)。这种效果并不是由病毒成绩单(方法)的表达,而是反映了Cre-infected细胞无法充分诱导活动依赖性NPAS4或TIP60损耗后的基因。gydF4y2Ba
一个gydF4y2Ba、实验方案的设计。核是孤立的海马gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠表达Cre-mCherry或ΔCre-GFP snRNA-seq紧随其后。额外的PCR一步放大病毒记录在cDNA图书馆被用来分配每个核感染状况。gydF4y2BabgydF4y2Ba(左)统一歧管近似和投影(UMAP)的可视化gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2BasnRNA-seq数据集。对,UMAP感染状况的可视化。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba:32418核从2小鼠,12963 Cre-infected 8845ΔCre-infected。gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠:44511核从3 13536 Cre-infected 13461ΔCre-infected。gydF4y2BacgydF4y2Ba,箱线图显示平均表达式(修日志(e)规范化计数)NPAS4或TIP60目标基因(gydF4y2Ba方法gydF4y2Ba)比较Cre-infected和每个神经元celltypeΔCre-infected细胞核内。箱线图显示中值(线),内部四分位范围(差;箱)和1.5×差(胡须)和级距表明中值±1.58×差/√gydF4y2BangydF4y2Ba)。* * *gydF4y2BaPgydF4y2Ba< 5×10gydF4y2Ba−10gydF4y2Ba,* *gydF4y2BaPgydF4y2Ba< 5×10gydF4y2Ba−4gydF4y2Ba,*gydF4y2BaPgydF4y2Ba< 0.01。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。确切的gydF4y2BaPgydF4y2Ba价值观和细胞数量每个集群提供的源数据。gydF4y2BadgydF4y2Ba,记录配置的示意图,显示的刺激电极的中心层pyramidale测量到邻国Cre-infected和未感染的细胞则CA1锥体神经元gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba或gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba急性海马切片。L, lacunosum;O,方位;P, pyramidale;R, radiatum。gydF4y2BaegydF4y2Ba代表图像(一式三份)执行显示在CA1稀疏Cre-mCherry表达式。gydF4y2BafgydF4y2Ba,gydF4y2BaggydF4y2Ba散点图记录的IPSC振幅,如果对邻国和Cre-infected细胞无毒性(Unstim。生理盐水)或刺激(机枪兵。低剂量的KA)gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba(gydF4y2BafgydF4y2Ba)或gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba(gydF4y2BaggydF4y2Ba老鼠)。点代表一个uninfected-Cre-infected一对。方块代表平均值±s.e.m。正确的insets,或Cre-infected细胞无毒性的痕迹。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba刺激:gydF4y2BangydF4y2Ba从4 = 16双老鼠;如果:gydF4y2BangydF4y2Ba= 12双5老鼠。gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba刺激:gydF4y2BangydF4y2Ba= 11对老鼠从2;如果:gydF4y2BangydF4y2Ba从小鼠2 = 12双。*gydF4y2BaPgydF4y2Ba= 3.73×10gydF4y2Ba−3gydF4y2Ba为gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba;*gydF4y2BaPgydF4y2Ba= 0.0209gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba。数据均值±s.e.m。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾gydF4y2BatgydF4y2Ba测试。音序器的形象gydF4y2Ba一个gydF4y2Ba来自BioRender (gydF4y2Bahttps://biorender.comgydF4y2Ba)。gydF4y2Ba
我们确定了差异表达基因(gydF4y2Ba方法gydF4y2Ba;消极的褶皱变化(Cre /ΔCre);调整gydF4y2BaPgydF4y2Ba< 0.01)在每个主要神经元亚型和我们的分析集中在表达下调的基因更有可能直接目标的复杂。在每个神经元亚型基因表达下调由于gydF4y2BaNpas4gydF4y2Ba删除后也显著下调gydF4y2BaTip60gydF4y2Ba相应的细胞群gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba数据集,产生相同的结果(图相互比较。gydF4y2Ba2摄氏度gydF4y2Ba和扩展数据图。gydF4y2Ba5gydF4y2Ba)。除了捕获已知NPAS4目标基因等gydF4y2BaNptx2gydF4y2Ba,gydF4y2BaPlk2gydF4y2Ba和gydF4y2Ba脑源性神经营养因子gydF4y2Ba1766年,我们发现新目标的NPAS4海马细胞类型特异的表达模式和定义(补充表gydF4y2Ba3gydF4y2Ba)。在小鼠神经元的主要的文化,我们独立消息来源的证实,NuA4复杂的组件,NPAS4, TIP60 EP400,每个规范相同的诱导转录计划(扩展数据图。gydF4y2Ba6 a - cgydF4y2Ba)。进一步确证NPAS4-NuA4交互的重要性对于基因活化,截短形式的NPAS4不强烈的表达与NuA4(扩展数据图。gydF4y2Ba二维gydF4y2Ba)的能力明显受损NPAS4激活其目标在荧光素酶结合位点记者化验(扩展数据图。gydF4y2Ba6 d, egydF4y2Ba)。在一起,这些发现提供证据表明NPAS4和NuA4不仅是神经元活动依赖性的关键调节基因转录也激活基因表达作为一个功能单位。gydF4y2Ba
最后测试确认NPAS4和NuA4函数在一起作为一个复杂的神经元,我们问TIP60是否有相同的作用,激活神经元电路作为NPAS4观察。兴奋CA1锥体神经元NPAS4的关键功能是调解招聘体细胞抑制海马锥体神经元反应神经元的活动gydF4y2Ba7gydF4y2Ba,gydF4y2Ba28gydF4y2Ba。我们因此稀疏的CA1区注入gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠的腺相关病毒(AAV)编码Cre-mCherry和执行同步录音诱发抑制性突触后电流(万能)从邻近的野生型(Cre-mCherrygydF4y2Ba- - - - - -gydF4y2Ba)和cKO (Cre-mCherrygydF4y2Ba+gydF4y2Ba)在急性海马锥体神经元片(无花果。gydF4y2Ba2 d, egydF4y2Ba)。轴突内的地层pyramidale与所需的最小强度刺激产生万能野生型和cKO神经元。删除NPAS4或TIP60显著降低依赖性活动体抑制引起的低剂量KA刺激。相比之下,没有观察到Cre-infected和未感染的细胞之间的差异在saline-injected控制动物(图。gydF4y2Ba2 f, ggydF4y2Ba和扩展数据图。gydF4y2Ba外:我6gydF4y2Ba)。在一起,这些实验表明,NPAS4-NuA4复杂组装在协调诱导基因转录激活神经元和动态重组刺激大脑的神经回路。gydF4y2Ba
诱导DNA断裂NPAS4-NuA4地点gydF4y2Ba
NuA4在双边带的保守功能修复gydF4y2Ba21gydF4y2Ba,gydF4y2Ba22gydF4y2Ba,gydF4y2Ba23gydF4y2Ba,gydF4y2Ba24gydF4y2Ba,gydF4y2Ba25gydF4y2Ba,gydF4y2Ba26gydF4y2Ba促使我们去下一个调查NPAS4的可能性,通过融入NuA4复杂,可能扮演一个以前从未发现过的DNA损伤作用控制神经元。值得注意的是,stimulus-dependent基因诱导神经元的建议导致双边带,这可能是由拓扑异构酶的酶,如TOP2B暂停RNA聚合酶II是释放到生产伸长gydF4y2Ba3gydF4y2Ba,gydF4y2Ba4gydF4y2Ba,gydF4y2Ba9gydF4y2Ba,gydF4y2Ba10gydF4y2Ba,gydF4y2Ba29日gydF4y2Ba。然而,双边带的程度发生在体内神经活动和神经元的机制,可能使用修复这些优惠和减轻累积损伤仍不清楚。我们建议成立一个复杂NPAS4和NuA4之间可能代表一个神经元的机制有效地驱动activity-induced转录反应同时维持基因组稳定的下游神经元活动(图。gydF4y2Ba3gydF4y2Ba)。我们试图确定基因组位点进行破坏和修复反应活动。我们还研究了这些地区是否NPAS4-NuA4和测试的目标是否扰乱NPAS4-NuA4损害DNA修复这些网站。gydF4y2Ba
一个gydF4y2Ba的双重作用,模型NPAS4-NuA4在刺激转录活性神经元DNA修复。gydF4y2BabgydF4y2BaATAC-seq IGV跟踪显示总信号(gydF4y2BangydF4y2Ba= 3),NPAS4急忙逃走(gydF4y2BangydF4y2Ba= 5),ARNT2急忙逃走(gydF4y2BangydF4y2Ba= 2)和γH2AX ChIP-seq (gydF4y2BangydF4y2Ba= 3)activity-inducible基因gydF4y2Ba脑源性神经营养因子gydF4y2Ba。gydF4y2BangydF4y2Ba每复制= 3 - 5老鼠汇集。gydF4y2BacgydF4y2Ba箱线图的平均γH2AX ChIP-seq规范化计数(gydF4y2BangydF4y2Ba= 3的3 - 5个老鼠)池(左)和监管所有元素activity-inducible监管元素(右),四分位数的子集NPAS4急忙逃走信号(gydF4y2Ba方法gydF4y2Ba)。监管所有元素:Q1 = 44864网站,第四季度= 7378网站。Activity-inducible元素:Q1 = 1017网站,第四季度= 764网站。箱线图显示中值(线)、差(盒)和1.5×差(胡须)和级距表明中值±1.58×差/√gydF4y2BangydF4y2Ba)。* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。gydF4y2BadgydF4y2Ba,脑核sBLISS-seq映射双边带的示意图。组织从每个sBLISS-seq整除样本保存RNA-seq配对分析。gydF4y2BaegydF4y2Ba,火山情节描绘DeSeq2日志gydF4y2Ba2gydF4y2Ba改变了褶皱变化和日志gydF4y2Ba10gydF4y2Ba(Benjamini-Hochberg调整gydF4y2BaPgydF4y2BasBLISS-seq信号的值)介于0和2 h KA刺激。虚线表示调整gydF4y2BaPgydF4y2Ba< 0.1。元素测井gydF4y2Ba2gydF4y2Ba改变了褶皱变化> 0,调整gydF4y2BaPgydF4y2Ba在第四季度的< 0.1和NPAS4 IgG-normalized急忙逃走信号用蓝色表示。正确的插图,总sBLISS-seq IGV跟踪(gydF4y2BangydF4y2Ba= 8个人老鼠)和NPAS4急忙逃走(gydF4y2BangydF4y2Ba= 5的3 - 5池老鼠)gydF4y2BaCgref1gydF4y2Ba和gydF4y2BaRgs7bpgydF4y2Ba启动子。彩色酒吧代表统计定义的山峰。gydF4y2BafgydF4y2Ba,总情节显示sBLISS-seq覆盖率(片段深度/ bp /峰)activity-inducible监管元素,子集的四分位数NPAS4绑定。信号均值±s.e.m。(gydF4y2BangydF4y2Ba= 8个人老鼠)。* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算的平均信号提取500 bp窗口元素中心使用未配对,双尾Wilcoxon rank-sum测试。gydF4y2Ba
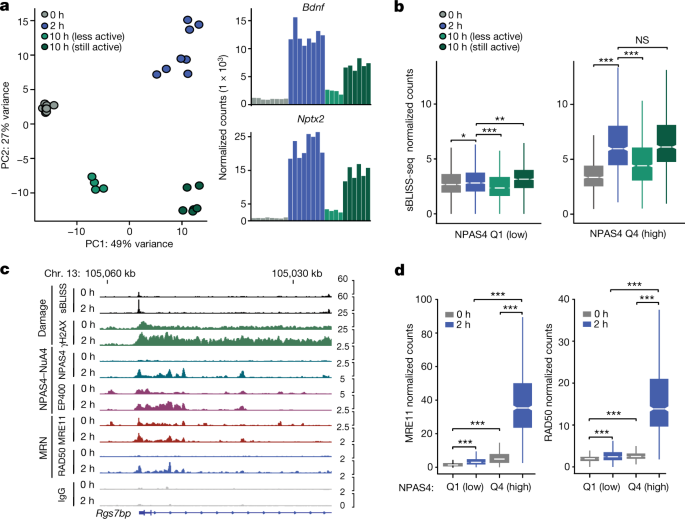
我们与测序分析用于transposase-accessible染色质(ATAC-seq)组蛋白的化学修饰,急忙逃走H3K27ac确定本构和activity-responsive基因组监管元素的景观在海马体。我们定义管理元素的基因组区域与一个ATAC-seq或H3K27ac急忙逃走的高峰,以后称为“监管所有元素”。我们进一步明确“activity-inducible监管元素”网站,表现出动态增加ATAC-seq信号(双重的增加;调整gydF4y2BaPgydF4y2Ba< 0.05)和/或增加H3K27ac急忙逃走信号(增长了1.5倍;调整gydF4y2BaPgydF4y2Ba< 0.05)经过2小时的低剂量KA刺激(扩展数据图。gydF4y2Ba7一个gydF4y2Ba- - - - - -gydF4y2BacgydF4y2Ba和补充表gydF4y2Ba4gydF4y2Ba)。在这个数据集,我们分类NPAS4-bound元素与我们列出的那些重叠的NPAS4峰值。我们第一次被问及神经刺激体内导致染色质的DNA损伤特征,尤其是在受NPAS4-NuA4元素。我们执行ChIP-seq DNA有关的组蛋白修饰γH2AX(组蛋白磷酸化Ser139 H2AX)如果和刺激神经元(图。gydF4y2Ba3 bgydF4y2Ba和扩展数据图。gydF4y2Ba7 d, egydF4y2Ba)。刺激后,我们观察到增加γH2AX水平NPAS4-bound网站,网站的最大信号和可诱导性的最高四分位数NPAS4绑定(图。gydF4y2Ba3 cgydF4y2Ba)。值得注意的是,我们观察到一个更大的提高在γH2AX水平在NPAS4-bound元素刺激后,在我们的景观activity-inducible元素(图。gydF4y2Ba3 cgydF4y2Ba,对吧)。因此,我们主要关注这些activity-inducible监管元素之间的关系最好,因为他们似乎捕捉activity-induced转录,NPAS4-NuA4绑定和DNA损伤。gydF4y2Ba
接下来,我们直接映射双边带体内使用暂停休息原位结扎和测序(sBLISS-seq) sequencing-based方法确定双边带通过结扎DNA测序DNA适配器上自由结束gydF4y2Ba30.gydF4y2Ba。经过验证的能力sBLISS-seq捕捉CRISPR-Cas9-induced双边带(扩展数据图。gydF4y2Ba7 f-hgydF4y2Ba),我们异形的双边带的景观出现在成年人的海马在基底条件或刺激。在平行,我们执行RNA-seq在同一样品检查如何双边带与转录动力学(无花果。gydF4y2Ba3 dgydF4y2Ba)。我们首先检查基本特征这些跨基因组DNA断裂的时间点。正如之前报道的gydF4y2Ba30.gydF4y2Ba,我们观察到的最大sBLISS-seq信号最高度表达基因的启动子(扩展数据图。gydF4y2Ba7 i (kgydF4y2Ba)。还有sBLISS-seq信号之间的显著相关性和γH2AX ChIP-seq信号刺激后在2 h。这个结果提供了一个独立的损害这些网站(扩展数据图。gydF4y2Ba7 lgydF4y2Ba)。主题丰富的统计定义山峰重现sBLISS-seq信号包括一些活动依赖性转录因子如ATF1、EGR NPAS4-ARNT,这表明这些优惠的一个子集是由转录诱导下游神经元活动增加(扩展数据图。gydF4y2Ba7米gydF4y2Ba)。gydF4y2Ba
我们下一个检查神经刺激如何影响双边带的景观。尽管神经活动并未改变sBLISS-seq信号(双边带)的总体布局整个基因组(扩展数据图。gydF4y2Ba7我gydF4y2Ba(调整后),我们发现1581年监管元素gydF4y2BaPgydF4y2Ba< 0.1),显著增加在双边带信号(图2 h后刺激。gydF4y2Ba3 egydF4y2Ba)。activity-inducible元素显示增加了双边带信号刺激后,在与non-inducible元素(扩展数据图。gydF4y2Ba7 ngydF4y2Ba)。此外,69%的元素有显著增加双边带信号刺激后在2 h的最高四分位数NPAS4急忙逃走的信号,和NPAS4-bound activity-inducible监管元素显示最重要的双边带信号刺激后的增加(图gydF4y2Ba3 e, fgydF4y2Ba)。我们证实了这些发现使用互补分析(END-seq)gydF4y2Ba31日gydF4y2Ba映射双边带在初级小鼠皮层神经元在0 h或2 h后刺激55毫米氯化钾。提高灵敏度,我们执行这些化验依托泊苷的存在,产生的双边带那块re-ligation拓扑异构酶的酶。之前报道gydF4y2Ba31日gydF4y2Ba我们观察到浓缩END-seq信号CTCF-bound地点(扩展数据图。gydF4y2Ba8gydF4y2Ba)。符合我们从海马体sBLISS-seq数据,END-seq结果显示增加stimulus-dependent DNA断裂NPAS4-bound地点在初级神经元(扩展数据图。gydF4y2Ba8 bgydF4y2Ba)。值得注意的是,双方的整体水平和可诱导性sBLISS-seq和END-seq信号高的网站有一个峰值急忙逃走NPAS4但不是依赖性活动的因素比匡威(扩展数据图”丛书。gydF4y2Ba8我gydF4y2Ba)。在一起,我们的独立的DNA损伤的措施γH2AX ChIP-seq, sBLISS-seq和END-seq证明NPAS4优先结合网站接受activity-inducible DNA破坏神经元。gydF4y2Ba
NPAS4-NuA4网站进行修复gydF4y2Ba
我们下一个被问及这些受损的元素,尤其是那些受NPAS4-NuA4也进行修复。为此,我们研究了双边带的水平在第三次点,10 h后KA刺激,推理的一个子集网站可能会返回对基线双边带信号activity-induced转录消退。因此我们使用RNA-seq从相同的组织收集的数据集sBLISS-seq活动依赖性转录的数据集来确定样本回到基线。主成分分析(PCA)和RNA-seq层次聚类样本的数据显示两个集群10 h时间点。一个集群显示activity-inducible基因表达水平显著低于2 h的时间点(称为“不活跃”),而其他10 h集群保持较高水平的诱导基因(称为“仍然活跃”)(无花果。gydF4y2Ba4gydF4y2Ba和扩展数据图。gydF4y2Ba9 a、bgydF4y2Ba)。PCA sBLISS-seq数据也表明,这些样品中聚集接近如果样品(扩展数据图。gydF4y2Ba9 cgydF4y2Ba)。值得注意的是,我们观察到如果和10 h中样本之间的分离,这表明样本中回到基线状态,而不是没有最初刺激。10 h样本中,双边带信号在activity-inducible监管元素显著降低相对于2 h时间点。这一结果表明,正在进行修复,解决双边带与转录活性下降。增加在DNA断裂信号2 h后刺激,加上10 h,减少最为明显,activity-inducible监管元素NPAS4绑定(图的最高水平。gydF4y2Ba4 bgydF4y2Ba和扩展数据图。gydF4y2Ba9 d, egydF4y2Ba)。我们证实NPAS4-bound网站进行活跃的DNA修复DNA通过检查地图出版synthesis-dependent修复人类神经元(SAR-seq)gydF4y2Ba32gydF4y2Ba。尽管这种方法没有专门检测双边带修复,它捕获的新核苷酸进入修复DNA链,从而出现nonhomologous加入结束gydF4y2Ba32gydF4y2Ba。我们观察到浓缩SAR-seq信号NPAS4-bound地点和更高水平的修复(SAR-seq信号)gydF4y2Ba32gydF4y2Ba在NPAS4-bound网站相对于FOS-bound网站(扩展数据图。gydF4y2Ba9 fgydF4y2Ba)。进一步探讨修复机制在NPAS4-bound网站,我们执行急忙逃走的组件MRE11-RAD50-NBS1 (MRN)复杂。这个复杂的双边带的早期应答网站,在加工中扮演一个重要部分破碎的结束并启动多个DNA修复途径gydF4y2Ba33gydF4y2Ba。我们检查MRE11亚基,介导的致命的拓扑异构酶裂解产品gydF4y2Ba34gydF4y2Ba并作为双边带修复整个基因组的标志gydF4y2Ba35gydF4y2Ba,RAD50便于装配的复杂和强化的核酸内切酶活动MRE11 (ref。gydF4y2Ba33gydF4y2Ba)。验证后的特异性MRE11急忙逃走信号使用gydF4y2BaMre11gydF4y2BacKO老鼠(扩展数据图。gydF4y2Ba10 a, bgydF4y2Ba),我们观察到一个强大的依赖性活动co-localization MRE11和RAD50 NPAS4-bound元素并不是由非特异性免疫球蛋白绑定,组蛋白乙酰化或染色质可访问性(图。gydF4y2Ba4 c, dgydF4y2Ba无花果和扩展数据。gydF4y2Ba10氟gydF4y2Ba和gydF4y2Ba11 a, bgydF4y2Ba)。值得注意的是,MRE11也出席NPAS4-bound元素缺乏刺激的情况下,这表明它可能是刺激后保留这些网站或者与其他修复启动因素。这些发现从多个独立化验表明,NPAS4-NuA4-bound网站热点的DNA损伤和修复激活神经元。gydF4y2Ba
一个gydF4y2BaPCA的配对RNA-seq准备从同一组织用于生成sBLISS-seq时间在海马体。样本集群按照国家刺激,刺激10 h样品分离与持续转录抑制或诱导组。DeSeq2-normalized项诱导基因gydF4y2Ba脑源性神经营养因子gydF4y2Ba和gydF4y2BaNptx2gydF4y2Ba所示为每个样本(0 h,gydF4y2BangydF4y2Ba= 8;2 h,gydF4y2BangydF4y2Ba= 8;10 h,gydF4y2BangydF4y2Ba= 10)。每复制一个鼠标。gydF4y2BabgydF4y2Ba箱线图的平均sBLISS-seq-normalized数0 h (gydF4y2BangydF4y2Ba= 8),2 h (gydF4y2BangydF4y2Ba= 8),10 h不活跃(gydF4y2BangydF4y2Ba= 4)和10 h仍然活跃的(gydF4y2BangydF4y2Ba= 6)样本activity-inducible监管元素,子集的四分位数NPAS4绑定。每复制一个鼠标。箱线图显示中值(线)、差(盒)和1.5×差(胡须)和级距表明中值±1.58×差/√gydF4y2BangydF4y2Ba)。Q1 = 1017网站,第四季度= 764网站。Q1, *gydF4y2BaPgydF4y2Ba= 0.03435,* *gydF4y2BaPgydF4y2Ba= 2.049×10gydF4y2Ba8gydF4y2Ba,* * *gydF4y2BaPgydF4y2Ba= 3.057×10gydF4y2Ba-13年gydF4y2Ba;第四季度,* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba-16年gydF4y2Ba不显著(NS) = 0.1742。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。gydF4y2BacgydF4y2BasBLISS-seq IGV追踪,γH2AX ChIP-seq, NPAS4, EP400, MRE11 RAD50急忙逃走的信号。数据绘制显示总信号从所有复制/因素。的gydF4y2BaygydF4y2Ba轴显示标准化覆盖面扩展为每个因素选择的轨迹。急忙逃走,γH2AX ChIP-seq,gydF4y2BangydF4y2Ba每复制= 3 - 5老鼠汇集。sBLISS-seq,gydF4y2BangydF4y2Ba= 1鼠标/复制。补充表中复制数据提供gydF4y2Ba2gydF4y2Ba。gydF4y2BadgydF4y2Ba平均MRE11和RAD50规范化计数的箱线图activity-inducible监管元素子集的四分位数NPAS4急忙逃走的信号。Q1 = 1017网站,第四季度= 764网站。箱线图显示中值(线)、差(盒)和1.5×差(胡须)和级距表明中值±1.58×差/√gydF4y2BangydF4y2Ba)。gydF4y2BangydF4y2Ba每复制= 3 - 5老鼠汇集。补充表中复制数据提供gydF4y2Ba2gydF4y2Ba。* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。gydF4y2Ba
NPAS4-NuA4破坏损害双边带修复gydF4y2Ba
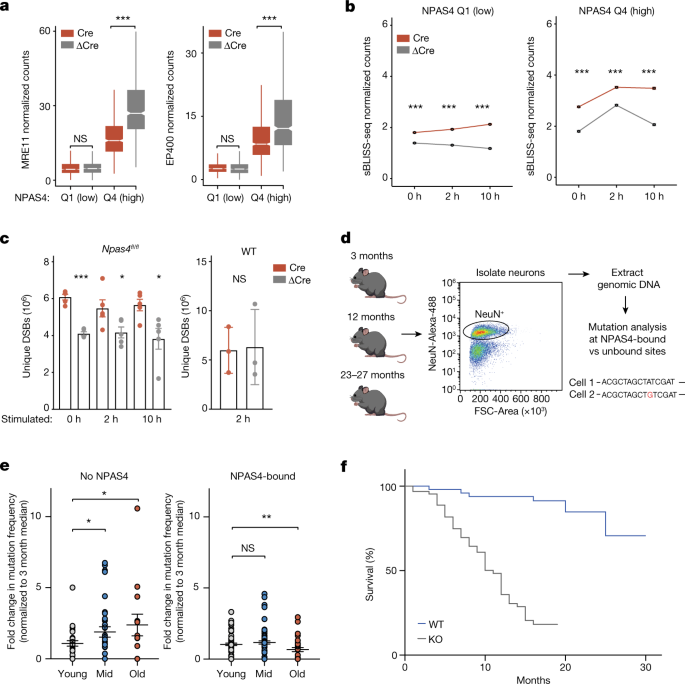
鉴于其目标网站的损害,我们下一个被问及NPAS4-NuA4刺激修复在这些网站的招聘额外双边带修理机械的基因组。通过执行急忙逃走NuA4组件EP400 MRE11,我们观察到损耗NPAS4导致显著减少蛋白质的绑定NPAS4-NuA4网站(无花果。gydF4y2Ba5gydF4y2Ba和扩展数据图。gydF4y2Ba11个碳氢键gydF4y2Ba)。尽管MRE11显著降低,这不是完全废除,这表明MRE11可能有额外的锁定机制,如直接互动与自由双边带结束或协会与转录机器gydF4y2Ba33gydF4y2Ba,gydF4y2Ba36gydF4y2Ba。如果NPAS4-NuA4刺激修复,NPAS4-NuA4子单元的损耗会导致双边带增加神经元。为了测试这个预测,我们注入gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba小鼠Cre-expressing或者ΔCre-expressing装甲防护,孤立的原子核(0,2到10 h后刺激和sBLISS-seq执行。NPAS4短期耗尽后,双边带activity-inducible监管元素的数量增加2和10 h后刺激。这个结果表明NPAS4呈现神经元的损失无法有效地修复这些transcription-coupled优惠(无花果。gydF4y2Ba5 bgydF4y2Ba)。我们还观察到的数量的增加优惠刺激之前,这可能反映了累积修复以前刺激(图中特异表达的影响。gydF4y2Ba5 bgydF4y2Ba和扩展数据图。gydF4y2Ba12个模拟gydF4y2Ba)。争端解决机构增加NPAS4-depleted核activity-inducible地点后没有观察到Cre表达野生型神经元(扩展数据图。gydF4y2Ba12 bgydF4y2Ba)。值得注意的是,删除NPAS4或NuA4组件TIP60也导致显著增加全基因组双边带没有观察到在野生型小鼠和不是一个次要的后果增加细胞凋亡gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaTip60gydF4y2BacKO细胞(图。gydF4y2Ba5度gydF4y2Ba和扩展数据图。gydF4y2Ba12 dgydF4y2Ba)。这增加了双边带的程度,整个基因组部分可能是由于神经元特异表达抑制NPAS4-NuA4造成破坏。然而,我们不能排除的可能性表达Cre,此前据报道导致脱靶基因组DNA断裂gydF4y2Ba37gydF4y2Ba,NPAS4有明显影响,TIP60突变体由于广泛提供修复的信号。gydF4y2Ba
一个gydF4y2Ba,箱线图的平均MRE11或EP400急忙逃走规范化Cre-infected或ΔCre-infected海马gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠activity-inducible地点,四分位数的子集NPAS4绑定。Q1 = 1017网站,第四季度= 764网站。箱线图显示中值(线)、差(盒)和1.5×差(胡须)和级距表明中值±1.58×差/√gydF4y2BangydF4y2Ba)。gydF4y2BangydF4y2Ba每复制= 2 - 3老鼠汇集。补充表中复制数据提供gydF4y2Ba2gydF4y2Ba。MRE11 Q1,gydF4y2BaPgydF4y2Ba= 0.2453;第四季度,* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。EP400 Q1,gydF4y2BaPgydF4y2Ba= 0.9962;第四季度,* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba−16gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算使用未配对,单侧Wilcoxon rank-sum测试(ΔCre > Cre)。gydF4y2BabgydF4y2Ba、线情节描绘平均±s.e.m。Cre-infected sBLISS-seq规范化数量或ΔCre-infected海马gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠,子集的四分位数NPAS4绑定。Q1 = 1017网站,第四季度= 764网站。数据从gydF4y2BangydF4y2Ba= 5每个Cre-infected和ΔCre-infected老鼠。* * *gydF4y2BaPgydF4y2Ba< 2.2×10gydF4y2Ba-16年gydF4y2Ba。gydF4y2BaPgydF4y2Ba值计算使用未配对,单侧Wilcoxon rank-sum测试(Cre >ΔCre)。看到扩展数据图。gydF4y2Ba12个一个gydF4y2Ba箱线图分布的数据。gydF4y2BacgydF4y2Ba在海马,全基因组核隔绝gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba(gydF4y2BangydF4y2Ba= 5)或野生型(gydF4y2BangydF4y2Ba= 3)老鼠Cre或ΔCre病毒感染。数据均值±s.e.m。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba:0 h,gydF4y2BaPgydF4y2Ba= 5.24×10gydF4y2Ba6gydF4y2Ba;2 h,gydF4y2BaPgydF4y2Ba= 0.044;10 h,gydF4y2BaPgydF4y2Ba= 0.022。野生型gydF4y2Ba:gydF4y2Ba2 h,gydF4y2BaPgydF4y2Ba= 0.906。gydF4y2BaPgydF4y2Ba使用双尾值计算,未配对gydF4y2BatgydF4y2Ba测试。gydF4y2BadgydF4y2Ba、收集的海马神经元核寿命。gydF4y2BaegydF4y2Ba,归一化突变频率在野生型老鼠NPAS4-bound和的网站。突变频率(基变化和插入和删除),年龄是计算每个站点和中值归一化频率的站点在年轻的动物。代表一个站点标准化率采样点从一个鼠标。数据均值±s.e.m。数据来自gydF4y2BangydF4y2Ba= 4(年轻),4(中年)和3(旧)老鼠。没有NPAS4网站:mid-young *gydF4y2BaPgydF4y2Ba= 0.03;年长年幼,*gydF4y2BaPgydF4y2Ba= 0.016。NPAS4-bound网站:mid-young NS = 0.18;年长年幼,* *gydF4y2BaPgydF4y2Ba= 0.0095。gydF4y2BaPgydF4y2Ba使用单侧值计算,未配对gydF4y2BatgydF4y2Ba测试。gydF4y2BafgydF4y2Ba、生存的gydF4y2BaNpas4gydF4y2Ba野生型(gydF4y2BangydF4y2Ba= 53个;28岁女性,25岁男性)和gydF4y2BaNpas4gydF4y2Ba击倒(gydF4y2BangydF4y2Ba= 64;37岁女性,男性27日)小鼠,缩写的使用寿命gydF4y2BaNpas4gydF4y2Ba基因敲除小鼠。gydF4y2BaPgydF4y2Ba= 4.09×10gydF4y2Ba-13年gydF4y2Ba由一个双尾Mantel-Cox测试,gydF4y2BaPgydF4y2Ba= 3.63×10gydF4y2Ba-11年gydF4y2Ba由一个双尾Gehan-Breslow-Wilcoxon测试。gydF4y2Ba
年龄相关性突变NPAS4地点gydF4y2Ba
神经元的一个独特的特征是他们长postmitotic寿命,提供充足的时间未解决的DNA断裂和突变的积累。我们想知道NPAS4-bound元素的重复激活可以使这些网站增加突变负荷在老化。评估突变负荷在NPAS4-bound元素,我们使用fluorescence-activated细胞排序(流式细胞仪)隔离NeuN-expressing原子核从年轻的海马体(3个月),中年(12个月)老(汽车个月大)小鼠和提取神经元DNA(图。gydF4y2Ba5 dgydF4y2Ba和扩展数据图。gydF4y2Ba13 a、bgydF4y2Ba)。然后我们进行有针对性的扩增子测序为敏感突变检测gydF4y2Ba38gydF4y2BaNPAS4-bound元素与负控制元素(也就是说,网站没有NPAS4绑定,称为NPAS4-unbound)。公司独特的分子标识符(umi)在启用PCR扩增检测突变归因于一个等位基因模板而不包括基础变化引起的测序错误gydF4y2Ba38gydF4y2Ba(扩展数据图。gydF4y2Ba13 cgydF4y2Ba)。我们首先验证这种技术来检测突变的能力介绍CRISPR-Cas9-induced减少网站的神经元(扩展数据图。gydF4y2Ba13 dgydF4y2Ba)。gydF4y2Ba
我们下一个定义一个脆弱的网站,进行小组日常减免或修复(γH2AX水平评估和/或MRE11绑定),NPAS4-NuA4绑定。我们将这个数据集与一组元素,不共享这些签名的伤害和不受NPAS4-NuA4,但匹配的诱导H3K27ac水平,诱导染色质可访问性和在/ GC(扩展数据图的内容。gydF4y2Ba13 e, fgydF4y2Ba)。年龄组之间的差异的代表性目标站点放大在我们的分析,这可能显示不同的基线率突变频率,我们归一化每个站点的突变率突变频率的中位数相同的站点在年轻的动物。值得注意的是,网站不受NPAS4突变积累随着年龄的增长,显示出一个大约两个增加12个月。相比之下,我们的小组NPAS4-bound网站似乎没有突变的频率随着年龄的增加(图gydF4y2Ba5 egydF4y2Ba)。这些数据表明,NPAS4-NuA4-bound网站相对防止额外的突变积累在生物的衰老。这些差异并不是由于异常高的速度突变的网站,当我们观察到更高的单核苷酸变异和插入和删除事件NPAS4-bound网站相对于non-bound网站在年轻的动物(扩展数据图。gydF4y2Ba13克gydF4y2Ba)。这些结果进一步证实,NPAS4-NuA4是针对脆弱的网站和提高的可能性NPAS4-NuA4复杂可能需要作为一个额外的保护层循环这些破碎的网站。gydF4y2Ba
NPAS4-NuA4中断减少寿命gydF4y2Ba
我们的数据表明,中断NPAS4-NuA4函数导致依赖性活动基因表达失调,增加DNA断裂activity-regulated启动子和增强子,本地化的保护修复受损机器和缺陷锥体神经元体抑制。因此,我们推断,最终会破坏NPAS4-NuA4复杂广泛,长期后果作为动物的年龄。这些变化可能包括有害影响基因组的完整性,兴奋性和抑制性的平衡和生物的寿命。值得注意的是,我们观察到损失的神经因素大大雄性和雌性老鼠的寿命缩短,导致平均寿命12和11个月,分别(无花果。gydF4y2Ba5 fgydF4y2Ba)。这个结果证实一个独立的结果gydF4y2BaNpas4gydF4y2Ba脱线gydF4y2Ba39gydF4y2Ba和明确表明了对寿命的影响小鼠的两性(扩展数据图。gydF4y2Ba13小时,我gydF4y2Ba)。生殖系的寿命减少gydF4y2BaNpas4gydF4y2Ba基因敲除小鼠是由于大脑中专门NPAS4的损失是由我们snRNA-seq数据证明NPAS4高度特定的神经元(扩展数据图。gydF4y2Ba2 fgydF4y2Ba)。此外,老鼠gydF4y2BaNpas4gydF4y2Ba删除在前脑gydF4y2BaCamk2agydF4y2Ba表达兴奋性神经元也降低了寿命(扩展数据图。gydF4y2Ba13 jgydF4y2Ba)。然而,我们不能排除的瞬时表达的可能性gydF4y2BaNpas4gydF4y2Banon-neuronal细胞有助于长寿表型。在一起,这些数据增加的可能性NPAS4-NuA4的保护作用在促进双边带修复有助于确保转录的长期忠诚对刺激的反应和适当的抑制控制的大脑可能是至关重要的正常寿命。gydF4y2Ba
讨论gydF4y2Ba
的程度不同的细胞在体内专门化其DNA修复机制了解甚少。新出现的证据表明,神经元不断修复DNA基因组中选择地点gydF4y2Ba32gydF4y2Ba,gydF4y2Ba40gydF4y2Ba,但是修复的优先目标的机制仍不清楚。这可能是由于部分地破坏网站的异质性造成的大量的神经元细胞类型不同细胞类型特异的转录活动模式和项目。使用新的小鼠模型的组合、生物化学、单细胞基因组学和电生理学,我们发现了一个专门的神经的NuA4复杂形式组装在NPAS4激活神经元细胞类型特异的诱导转录调节和抑制DNA损伤。我们的研究表明,神经元已经进化出一个特定的染色质调节机制,夫妻突触活动基因组保存。这种机制可以减少累积的损伤在关键监管元素在每个神经元细胞类型和安装适当的保持能力对环境因素的反应。gydF4y2Ba
机制,导致双边带的形成和修复NPAS4-bound地点仍有待阐明。正如前面建议gydF4y2Ba4gydF4y2Ba,这些优惠可能源自pre-bound拓扑异构酶酶你修改下游神经元的活动。此外,双边带可能形成的过程中解决dna rna混合动力车(R-loops)或释放停滞转录复合物发生之前迅速诱导静止的监管元素。值得注意的是,NuA4已经绑定R-loops报道gydF4y2Ba41gydF4y2Ba,这表明R-loop形成可能导致DNA损伤和修复活动依赖性监管元素。神经系统以外的研究表明,RNA本身可以通过服务促进修复这些转录区域作为模板代替postmitotic细胞的姐妹染色单体gydF4y2Ba42gydF4y2Ba,gydF4y2Ba43gydF4y2Ba。虽然可能规范nonhomologous结束加入途径调解争端解决机构的维修在激活神经元,NPAS4-NuA4可能涉及到多个修复途径。未来的研究神经元探针的精确机制用来修复activity-induced损伤,包括那些由NPAS4-NuA4,将调查的重要领域。gydF4y2Ba
这项工作提供了一个示例染色质机械专业的大脑和增加了的神经外遗传性特征经常在神经发育和神经退行性疾病特异表达。几个组件NPAS4-NuA4 (gydF4y2BaEp400gydF4y2Ba,gydF4y2BaTrrapgydF4y2Ba,gydF4y2BaActl6bgydF4y2Ba和gydF4y2BaTip60gydF4y2Ba)在神经发育突变和自闭症谱系障碍gydF4y2Ba44gydF4y2Ba,gydF4y2Ba45gydF4y2Ba,gydF4y2Ba46gydF4y2Ba。我们发现神经活动之间的联系和DNA修复由NPAS4-NuA4表明,损害依赖性活动监管元素可能是一个神经功能障碍在这些疾病的来源。gydF4y2Ba
失去了在生物基因组完整性是老化的一个特点gydF4y2Ba12gydF4y2Ba,gydF4y2Ba13克ydF4y2Ba,并且能够有效地修复双边带与寿命延长哺乳动物的进化gydF4y2Ba47gydF4y2Ba。然而,仍然未知的神经活动如何影响基因组稳定性随着年龄的增长和对细胞和生物的寿命。维持神经元活力随着时间的推移,似乎需要小心平衡的兴奋和抑制的适当比例gydF4y2Ba48gydF4y2Ba。除了NPAS4在DNA修复的作用,抑制复合损失的gydF4y2BaNpas4gydF4y2Ba基因敲除小鼠可能影响他们的寿命缩短。随着时间的推移,受损NPAS4-NuA4信号可能会破坏一个关键监管反馈回路中删除NPAS4影响基因的表达,调节招聘体细胞的抑制,进而导致过度兴奋,进一步威胁到基因组的稳定性。未来实验,分离的角色NPAS4转录和维修需要理解这两个过程的相对贡献在神经细胞和有机体的寿命。鉴于NPAS4-NuA4 neuronal-specific表达模式,在人类的大脑是守恒的,在神经元受到周期性activity-induced DNA断裂在许多年里,NPAS4-NuA4信号轴也可以作为一个重要的入口点理解认知和感觉处理的故障在人类衰老和神经退行性疾病。gydF4y2Ba
方法gydF4y2Ba
实验模型gydF4y2Ba
小鼠模型gydF4y2Ba
动物使用批准,由哈佛大学制度动物保健和使用委员会和哈佛比较医学中心。以下使用鼠标线:野生型C57 / BL6(杰克逊实验室,000664);gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba14gydF4y2Ba;gydF4y2BaNpas4 -gydF4y2Ba基因敲除gydF4y2Ba14gydF4y2Ba;gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba49gydF4y2Ba;gydF4y2BaNpas4-Flag-HAgydF4y2Ba(手稿);gydF4y2BaArnt2-Flag-HAgydF4y2Ba(手稿),gydF4y2BaTip60-H3FgydF4y2Ba50gydF4y2Ba;gydF4y2BaMre11gydF4y2Bafl / flgydF4y2Ba51gydF4y2Ba,gydF4y2Ba52gydF4y2Ba;gydF4y2BaB6; 129 - gt (ROSA) 26 sor < tm5 CAG-Sun1 / sfGFP Nat > / JgydF4y2Ba(杰克逊实验室,021039)gydF4y2Ba53gydF4y2Ba;和gydF4y2BaB6.Cg-Tg (Camk2a-cre) T29-1Stl / JgydF4y2Ba(杰克逊实验室,005329)gydF4y2Ba54gydF4y2Ba。老鼠被安置在温度和湿度环境中使用通风microisolator笼子。老鼠在一个标准的12 h光暗周期,与随意提供食物和水。男性和女性同窝出生仔畜老鼠中使用类似的比例,分为实验组和对照组的实验。没有统计方法被用来预先确定样本大小。动物生物化学和基因组实验,收集整个手稿在4 - 6周的年龄。生理学实验中,动物解剖和修补24 (P24) P28产后的一天。老化实验,动物被收集在3 - 4个月、12个月和汽车几个月的年龄。动物年龄和性别是详细的细节在每个协议。gydF4y2Ba
一代的gydF4y2BaNpas4-Flag-HAgydF4y2Ba和gydF4y2BaArnt2-Flag-HAgydF4y2Ba敲入小鼠行gydF4y2Ba
受精卵注入哈佛大学基因组进行修改设施依照他们的实践和指导原则。指导RNA序列接近的3′末端gydF4y2BaNpas4gydF4y2Ba和gydF4y2BaArnt2gydF4y2Ba位点选择基于预测切削效率和较低的脱靶效应。NPAS4指导RNA序列(5′-cacagacttattcaaaacgt-3′)和ARNT2 (5′-gagtagcttcaggcaaagcc-3′)被克隆到一个包含引导序列上游tracrRNA FUGW骨干(5′-gttttagagctagaaatagcaagttaaaataaggctagtccgttatcaacttgaaaaagtggcaccgagtcggtggtgcttttttt-3′)。为体外转录生成模板,使用这些FUGW PCR进行质粒将一个T7启动子使用以下引物:gydF4y2BaNpas4gydF4y2Ba转发(F): 5′-taatacgactcactataggcacagacttattcaaaacgtgttttagag-3′;gydF4y2BaNpas4gydF4y2Ba反向(R): 5′-aaaaaaagcaccaccgactcgg-3′;gydF4y2BaArnt2gydF4y2BaF: 5′-taatacgactcactataggagtagcttcaggcaaagcc-3′;和gydF4y2BaArnt2gydF4y2BaR: 5′-aaaaaaagcaccaccgactcgg-3′。gydF4y2Ba
PCR产品DNA凝胶上验证,以确保一个单一产品和使用试剂盒纯化PCR清理设备。体外转录(溶)使用400 ng纯化RNA模板执行16 h在37°C使用Megascript短记录诊断工具包(热费希尔,AM1354)。使用MEGAclear转录RNA进行清理清理工具(Ambion AM190)。最后,RNA的大小和质量评估通过运行200 ng此种凝胶纯化产品的10%。HDR模板被命令200个基点,从IDT单链片剂,75个基点的同源性的网站。CRISPR指导RNA, Cas9 RNA和片剂捐赠者模板被注入混合背景DBA / C57BL6小鼠受精卵根据哈佛基因组的指导方针和程序修改工具。DNA创始人和FgydF4y2Ba1gydF4y2Ba后代筛选利用Sanger测序,以确保适当的插入的标记和DNA侧翼地区没有发生突变。gydF4y2BaNpas4-Flag-HAgydF4y2Ba和gydF4y2BaArnt2-Flag-HAgydF4y2Ba老鼠被随后backcrossed C57BL6 / J小鼠和可按照客户要求定制。gydF4y2Ba
老鼠神经元文化gydF4y2Ba
胚胎皮质胚胎16.5天(-17)从5 - 6混合胚胎切割性和合并为一个复制的文化。木瓜蛋白酶(Sigma-Aldrich, 10108014001)被用来分离组织通过一个10分钟孵化在37°C。消化是终止的卵类粘蛋白(胰蛋白酶抑制剂,沃辛顿)。消化组织通过P1000吸管轻轻磨碎释放细胞和通过一个40µm过滤器。神经元是镀上与保利预涂在一夜之间——细胞培养盘子gydF4y2BadgydF4y2Ba赖氨酸(20µg毫升gydF4y2Ba1gydF4y2Ba)和层粘连蛋白(4µg毫升gydF4y2Ba1gydF4y2Ba)。神经元生长在neurobasal介质(Gibco)包含B27补充(2%)、penicillin-streptomycin (50 U mlgydF4y2Ba1gydF4y2Ba青霉素和50 U mlgydF4y2Ba1gydF4y2Ba链霉素)和glutaMAX(1毫米)。神经元生长在孵化器维持在37°C公司gydF4y2Ba2gydF4y2Ba浓度为5%。收集神经元在体外7天为所有实验(DIV),和新鲜的培养基在3 - 4添加DIV(总量50%),除非另有指示。独立复制生成的准备主要培养的胚胎切割池在不同的日子在文化和维护7 DIV。镀RNA-seq实验,细胞的密度每厘米156250个细胞gydF4y2Ba2gydF4y2Ba(每个)150万个神经元在6-well文化菜肴。荧光素酶检测,细胞被镀的密度210526厘米gydF4y2Ba2gydF4y2Ba(400000细胞/)24-well文化菜肴。去偏光神经元,神经元接受55毫米氯化钾。治疗与不同的刺激(扩展数据图。gydF4y2Ba1 dgydF4y2Ba),7 DIV神经元接受50µM NMDA ng或50毫升gydF4y2Ba1gydF4y2Ba脑源性神经营养因子。螯合钙,神经元使用5毫米EGTA 15分钟前刺激与55毫米氯化钾溶液。gydF4y2Ba
实验程序gydF4y2Ba
集合时间点gydF4y2Ba
在癫痫发作被诱导实验,KA(5 - 8毫克公斤gydF4y2Ba1gydF4y2Ba(电生理学)或12 - 15毫克公斤gydF4y2Ba1gydF4y2Ba(基因表达,急忙逃走,sBLISS-seq和免疫沉淀反应)(Sigma-Aldrich K0250)腹腔注射。基因组层面分析小鼠安乐死2 6到10 h后注入,表示,基于以前的工作表明,即早期基因转录因子和延迟反应基因计划在2和6 h后诱导刺激开始,分别gydF4y2Ba1gydF4y2Ba,gydF4y2Ba14gydF4y2Ba,gydF4y2Ba28gydF4y2Ba。如果或基底时间点表明小鼠注射生理盐水控制和被切割和并行处理刺激组织。在CA1锥体神经元电生理实验,小鼠死亡18 - 24 h后注射KA水平较低,允许足够的时间NPAS4的表达,其关联依赖性活动目标基因和潜在的突触的执行监管。蛋白质组学分析,老鼠被杀后3小时以内NPAS4注入允许足够的时间来生产和相关的蛋白质复合体的组装。gydF4y2Ba
Stereotaxically引导手术gydF4y2Ba
基因组分析,包括snRNA-seq,急忙逃走,sBLISS-seq P21-P24gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠被吸入异氟烷麻醉(感应3 - 5%,1 - 3%维护)和定位在一个立体定位框架(科夫)鼠标的温度保持在37°C加热垫。所有手术都是根据协议执行批准的哈佛大学动物保健和常务委员会依照联邦指导方针。皮草在头皮上被使用剃须刀和消毒三种betadine交替洗和70%的乙醇。海马体的基因化验需要广泛的感染,钻是一个磨孔通过上面的骷髅海马体,和一个玻璃吸管充满AAV降低海马的中部地区,使广泛的感染的各种条件(medial-lateral:±2.5;前后:−2.5;dorsal-ventral:−2.5)。AAV (1000 nl,稀释到1.0×10gydF4y2Ba12gydF4y2Ba基因组拷贝/毫升)在150 nl分钟注射gydF4y2Ba1gydF4y2Ba和吸管替代了5分钟完成后的病毒注入允许病毒蔓延。所有的动物被给予术后镇痛(buprenophine缓释配方,1毫克公斤gydF4y2Ba1gydF4y2Ba)依照制度动物保健和使用委员会的协议。对于需要稀疏的电生理检测感染海马的CA1区,好小白鼠注射如上所述,但是玻璃针尖端位置在不同坐标限制感染CA1 (medial-lateral:±3.4;前后:−2.9;dorsal-ventral:−2.8),病毒注入的滴定度较低(1.0×10gydF4y2Ba10gydF4y2Ba基因组拷贝/毫升)。gydF4y2Ba
急性切片制备gydF4y2Ba
横向海马切片准备gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba岁的C57BL / 6小鼠P21-P28。异氟烷用于使麻醉动物,大脑很快被删除,沿着中线一分为二的,放在冰冷的choline-containing人工脑脊液(choline-ACSF)包含(毫米):110 choline-Cl 25 NaHCOgydF4y2Ba3gydF4y2Ba1.25不gydF4y2Ba2gydF4y2Ba阿宝gydF4y2Ba4gydF4y2Ba2.5氯化钾7 MgClgydF4y2Ba2gydF4y2Ba0.5,25葡萄糖,CaClgydF4y2Ba2gydF4y2Ba3.1、11.6抗坏血酸和丙酮酸。Choline-ACSF平衡与95%阿gydF4y2Ba2gydF4y2Ba和5%的公司gydF4y2Ba2gydF4y2Ba。这两个脑半球被转移到一个包含冰冷的choline-ACSF切片室,和300 -μm厚片被削减使用徕卡VT1200S vibratome。片被转移到控股室充满ACSF饱和O为95%gydF4y2Ba2gydF4y2Ba和5%的公司gydF4y2Ba2gydF4y2Ba和包含(毫米):127氯化钠,25 NaHCOgydF4y2Ba3gydF4y2Ba1.25不gydF4y2Ba2gydF4y2Ba阿宝gydF4y2Ba4gydF4y2Ba2.5氯化钾2 CaClgydF4y2Ba2gydF4y2Ba1 MgClgydF4y2Ba2gydF4y2Ba和25个葡萄糖。片在34°C孵化为30分钟,然后平衡至室温录音前20分钟。所有记录都在室温下进行,并在6小时内完成片的准备。这项工作是用来识别片稀疏感染与Cre-mCherry CA1锥体层,和片> 30%感染CA1锥体神经元没有用于录音。片也被丢弃如果Cre-mCherry表达式CA3或齿状回中可观察到的地区。gydF4y2Ba
电生理学gydF4y2Ba
CA1锥体神经元与红外可视化微分干涉对比显微镜进行全细胞电压钳记录。相邻的未感染和Cre-mCherry-infected神经元被确定使用这项工作由一个发光二极管。神经元对所有实验−举行70 mV。记录硼硅玻璃制成的吸量管(打开2和4之间的电阻MΩ)充满了一个内部解决方案包含(毫米):147中海,NagydF4y2Ba2gydF4y2Ba磷酸肌酸,10玫瑰,2 MgATP 0.3 NagydF4y2Ba2gydF4y2Ba三磷酸鸟苷,2 EGTA和5 qx - 314 (Sigma-Aldrich)。内部解决方案是准备在单个批处理,与渗透性调整到290 mOsm CsOH重蒸馏的水和pH值调整到7.3,并储存在−20°C。记录万能,抑制电流通过浴应用药物隔离10µM (gydF4y2BaRgydF4y2Bacpp (Tocris生物科学)和10µM NBQX二钠盐(Tocris生物科学)。细胞外的刺激perisomatic抑制轴突是通过使用一个同心双极电极(FHC)放置在层的中心pyramidale和在100 - 200年μm外侧的一对voltage-clamped细胞。刺激强度使用所需的最小刺激产生一个可靠的IPSC在两个神经元。gydF4y2Ba
电生理数据采集和分析gydF4y2Ba
录音是使用Multiclamp 700 b放大器(轴突仪器),过滤3千赫和采样10 kHz。数据分析与MatLab编写的定制软件。实验丢弃如果保持电流低于600−pA或串联电阻大于25 MΩ。跨同时记录单元串联电阻是每一对在25%以内。在室温下进行录音(19°C)。万能的振幅计算平均振幅0.5女士之前2女士之后的峰值电流。无符号级的突触电流显示清晰。gydF4y2Ba
组织学gydF4y2Ba
男性和女性在平等的比例。小鼠腹腔内注射麻醉的10毫克毫升gydF4y2Ba1gydF4y2Ba氯胺酮和1毫克毫升gydF4y2Ba1gydF4y2Ba甲苯噻嗪。麻醉后,小鼠灌注transcardially至少10毫升的冰冷的PBS,其次是至少20毫升的4%多聚甲醛(PFA) PBS。大脑被移除,放置在4% PFA在4°C 24 h,紧随其后的是三个连续洗冷PBS。大脑被转移到cryoprotection蔗糖为30%,并在4°C的环境,直到组织平衡并沉没。大脑被嵌入在NEG-50冰冻切片中储存在−80°C到分组(30μm厚)在低温恒温器(徕卡CM1950)。部分存储在PBS在4°C到进一步使用。permeabilized,免疫组织化学,部分被孵化PBS中含0.1% Triton x - 100和5%正常山羊血清(屏蔽解决方案)在室温下1 h。下面列出主要抗体染色(稀释)进行一夜之间在4°C (16 h)温和的颤抖。部分被洗了三次5分钟每个在PBS含有0.1% Triton x - 100。二次抗体染色是由稀释一个Alexa萤石dye-conjugated二级抗体(生命技术; rat Alexa Fluor 555 (A21434), rabbit Alexa Fluor 647 (A31573); 1:250) and incubating slices for 2 h at room temperature. Sections were then washed again three times for 5 min each in PBS containing 0.1% Triton X-100, and then mounted in DAPI Fluoromount-G (Southern Biotech) and imaged on a slide-scanning microscope (Olympus VS120, VS ASW-FL). Antibodies were diluted in blocking solution as follows: rat anti-HA (Sigma-Aldrich, ROAHAHA; 1:250); rabbit anti-NPAS4 (in house; 1:1,000)14gydF4y2Ba;兔子anti-ARNT2(房子;1:1,000)gydF4y2Ba28gydF4y2Ba;兔子anti-KAT5 (TIP60) (10827 - 1 - ap Proteintech;摘要);兔子anti-cleaved caspase-3(细胞信号技术,9664年代;1:1,000)。gydF4y2Ba
NPAS4-NuA4复合物的免疫沉淀反应gydF4y2Ba
隔离与NPAS4相关蛋白复合物,8 - 12海马分离得到6gydF4y2BaNpas4-Flag-HAgydF4y2Ba和gydF4y2BaArnt2-Flag-HAgydF4y2Ba小鼠注射15毫克公斤gydF4y2Ba1gydF4y2BaKA (Sigma-Aldrich K0250)诱导高水平的NPAS4表达式。男性和女性在平等的比例合并复制样品。野生型老鼠相同的年龄和性别分布并行处理作为控制。海马区域被解剖后3小时注射KA允许足够的时间NPAS4表达式和组装成潜在的复合物。海马是收集和dounced 20×10毫升NE1缓冲区(20毫米消息灵通的pH值7.9,10毫米氯化钾,MgCl 3毫米gydF4y2Ba2gydF4y2Ba,0.1% EDTA Triton和0.1毫米)含有蛋白酶抑制剂鸡尾酒(罗氏)和磷酸酶抑制剂鸡尾酒2和3 (Sigma-Aldrich P5726和P0044)。细胞核被释放到10分钟的孵化NE1缓冲区,然后由温柔的颗粒状离心(1000 - 1500年gydF4y2BaggydF4y2Ba)。核丸resuspended 1核体积NE1缓冲包装。促进释放chromatin-associated蛋白质、核孵化了30分钟在4°C benzonase核酸内切酶(Sigma-Aldrich、E1014 > 25 KU(1每1000万核µl)其次是氯化钠的添加最后一个300毫米的浓度。后高速离心除去不溶性物质,溶解产物实现最终的盐浓度被稀释的200毫米。事先批准非特异性相互作用,溶解产物孵化为30分钟在4°C 50µl ms-IgG-coated琼脂糖珠(Sigma-Aldrich A0919)。事先批准后,溶解产物是孵化为1.5 h和60µl anti-M2-Flag树脂(Sigma-Aldrich A2220) / 1毫升的稀释溶解产物。样本洗4×NE1缓冲区包含250毫米氯化钠5分钟的旋转在4°C。NPAS4-interacting或ARNT2-interacting蛋白质竞争性筛选了在50 - 100平方米树脂通过孵化µlµg 500毫升gydF4y2Ba1gydF4y2Ba3×标志肽(Sigma-Aldrich F4799)稀释在NE1缓冲区在室温下30分钟。质谱分析,筛选了蛋白质与三氯乙酸沉淀。复制图所示。gydF4y2Ba1 cgydF4y2Ba由3个独立的8 - 12老鼠从野生型或收集池gydF4y2BaNpas4-FHgydF4y2Ba线条和处理在不同的日子。验证免疫沉淀反应化验使用gydF4y2BaNpas4-Flag-HAgydF4y2Ba老鼠或gydF4y2BaTip60-H3FgydF4y2Ba老鼠是通过免疫印迹分析在相同条件下进行如上所述。为验证实验老鼠视觉皮层光刺激后,20 V1皮层海马是孤立的gydF4y2BaNpas4-Flag-HAgydF4y2Ba或野生型控制。老鼠被安置在黑暗中1星期后跟2 h的光刺激。数据扩展数据图所示。gydF4y2Ba1 fgydF4y2Ba。gydF4y2Ba
隔离高分子量复合物包含完整NPAS4-NuA4质谱,8 - 10 6周gydF4y2BaNpas4-Flag-HAgydF4y2Ba,gydF4y2BaTip60-H3FgydF4y2Ba和野生型控制老鼠注射KA和解剖2 h后注入。男性和女性在平等的比例合并复制样品。复制由独立的8 - 10老鼠池运行在独立的梯度和天。两个进行复制。全前脑-海马和纹状体,被剁碎,转移NE1缓冲区,和核溶解产物是如上所述。大约6毫升梯度是准备使用BIOCOMP梯度大师108(科学服务)使用的长10 - 40%甘油梯度SW41贝克曼转子。样品浓度归一化2毫克毫升左右gydF4y2Ba1gydF4y2Ba,1毫升加载的10 - 40%甘油梯度。样本为16 h 37000 r.p.m离心机。在4°C。收集一毫升分数在4°C。分数是运行在sds - page凝胶NuA4评估分数包含组件的复杂。从分数1 - 3免疫沉淀反应分析被执行,这包含大多数TRRAP和EP400溶解产物。从分数事先批准非特异性相互作用,溶解产物孵化了30分钟在4°C 100µl ms-IgG-coated琼脂糖珠(Sigma-Aldrich A0919)。事先批准后,溶解产物为1.5 h和100µl孵化anti-M2-Flag树脂(每1毫升Sigma-Aldrich A2220)分数。样本NE1包含4×250毫米生理盐水冲洗5分钟旋转在4°C。相互作用的蛋白质被筛选了500年M2树脂通过孵化µg毫升gydF4y2Ba1gydF4y2Ba3×标志肽(Sigma-Aldrich F4799)。洗出液从免疫沉淀反应化验进行分数1 - 3池有足够的材料质谱分析,筛选了蛋白质与三氯乙酸沉淀。gydF4y2Ba
在HEK293T细胞免疫沉淀反应的NPAS4截断突变体gydF4y2Ba
质粒(与哥伦比亚大学启动子FUW)包含序列Flag-HA-tagged”丛书,小君,EGR1 NPAS4或各种截短形式的NPAS4(补充表gydF4y2Ba1gydF4y2Ba)被CaCl HEK293T细胞中表达gydF4y2Ba2gydF4y2Babbs转染(2μg DNA, 6×10gydF4y2Ba6gydF4y2Ba细胞)。HEK293T细胞获得热费希尔科学(50188404 fp)。HEK293T细胞没有认证或检测支原体。除了核GFP-FH控制样本,GFP-IRES-NPAS4可视化表达的质粒转染效率。Flag-HA标签附加到氨基酸的NPAS4标记差异最小的可访问性NPAS4变体c端尽头截断。收集的细胞被轻轻刮进冰冷的PBS含有蛋白酶抑制剂鸡尾酒(罗氏)和被温柔的离心(2000颗粒状gydF4y2BaggydF4y2Ba)。细胞核被孤立,国旗免疫沉淀反应进行如上所述。第二次免疫沉淀反应步骤使用HA是由收集国旗肽洗出液,增加体积为1毫升NE1缓冲区,添加50μl anti-HA树脂(圣克鲁斯生物技术、sc - 7392 AC),轻轻旋转在4°C 1.5 h。样本洗4×NE1缓冲区包含250毫米氯化钠5分钟的旋转在4°C。蛋白质被孵化筛选了树脂与HA肽(热费希尔26184)稀释NE1缓冲区在室温下为30分钟。筛选了与三氯乙酸沉淀蛋白质质谱分析。复制由独立转染文化和免疫沉淀反应化验进行单独的天。gydF4y2Ba
凝胶排阻层析法和蓝色本机凝胶gydF4y2Ba
全细胞溶解产物(Triton x - 100 2%, 50毫米三,150毫米氯化钠和1毫米EDTA)从海马组织或海马和纹状体组织是分次使用400小时1分馏器设置为0.5毫升分gydF4y2Ba1gydF4y2Ba。缓冲区的列和分馏器由20毫米Tris-HCl pH值7.4,100毫米氯化钠,MgCl EDTA 1毫米,3毫米gydF4y2Ba2gydF4y2Ba和特里同0.02%。每个收集17分数组成的6毫升,分裂到8 - 16个被加载到本地和分数Novex NuPAGE 4 - 16%凝胶(热费希尔,BN1002BOX)估计的近似大小NPAS4-containing蛋白复合物。本地页面标记(1µl;表达载体,LC0725)被用来估计大小的复合物。蛋白质被转移到PVDF膜和免疫印迹NPAS4(1:1,000)使用内部抗体。gydF4y2Ba
免疫印迹gydF4y2Ba
全细胞或核提取物主要神经元或脑组织被解决在3 - 8% Tris-acetate凝胶(热费希尔,EA0375BOX)或10% Tris-glycine凝胶和转移到硝化纤维膜。一夜之间,膜被孵化在以下主要抗体:EP400(架a300型Bethyl实验室- 541 a;Abcam Ab5201;Abcam, 70301;1:1,000);DMAP1(细胞信号技术,13326;圣克鲁斯,sc - 373949;1:50 0或1:1,000);TRRAP (Bethyl a301 - 132 a;1:50 0或1:1,000); ARNT2 (in house; 1:1,000)28gydF4y2Ba;1:1,000 NPAS4(房子)gydF4y2Ba14gydF4y2Ba;安全系数(在房子;1:1,000);β-tubulin3 (Covance, mms - 435 p;1:5,000);GAPDH (Sigma-Aldrich G9545;1:5,000);组蛋白H3 (Abcam, 1791;1:10,000);NPAS3(来自美国麦克奈特的礼物; 1:1,000)55gydF4y2Ba;和HA(细胞信号技术,C29F4;1:1,000)。洗后,膜与二次孵化抗体共轭IRdye 700或800,使用LiCOR奥德赛仪器成像。gydF4y2Ba
质谱分析gydF4y2Ba
样本处理根据标准程序的近代质谱设备(哈佛大学)。患者蛋白质与50 mM孵化包含12.5 ngµl碳酸氢铵溶液gydF4y2Ba1gydF4y2Ba修改sequencing-grade胰蛋白酶(Promega)在4°C 45分钟。删除多余的胰蛋白酶溶液后,样品被放置在37°C在50 mM碳酸氢铵溶液。肽通过移除碳酸氢铵恢复解决方案,随后在50%乙腈和1%甲酸清洗脱水。gydF4y2Ba
慢病毒生产gydF4y2Ba
生成慢病毒成分表达式构造,21日英国石油公司目标序列的委员会(Sigma-Aldrich) subcloned FUW向量U6启动子的下游。以下序列使用:控制/新成分(5′-gcgcgatagcgctaataattt-3′);gydF4y2BaNpas4gydF4y2BashRNA-1 (5′-ggttgaccctgataattta-3′);gydF4y2BaTip60gydF4y2BashRNA-1 TRCN0000039299 (5′-cctcctatcctaccgaagtta-3′);gydF4y2BaTip60gydF4y2BashRNA-2 TRCN0000039300 (5′-cggagtatgactgcaaaggtt-3′);gydF4y2BaEp400gydF4y2BashRNA-1 TRCN0000109315 (5′-ccgtgaacattagctttgatt-3′);和gydF4y2BaEp400gydF4y2BashRNA-2 TRCN0000305480 (5′-gtcgtcagaaggccttatatg-3′)。gydF4y2Ba
生成LentiCRISPR构造用于测试sBLISS-seq在培养的神经元,以下指导序列克隆到LentiCRISPRv2GFP (Addgene, 82416)使用上市引物序列:(1)gydF4y2BaScg2gydF4y2Ba5′-cggcccgagccctcactca-3′:底漆F: 5′-caccgcggcccgagccctcactcag-3′;底漆R: 5′-aaacctgagtgagggctcgggccgc-3′;(2)gydF4y2BaInhbagydF4y2Ba增强器5′-gagcagccactagcgaaccc-3′:底漆F: 5′-caccggagcagccactagcgaaccc-3′;底漆R: 5′-aaacgggttcgctagtggctgctcc-3′;(3)gydF4y2Ba脑源性神经营养因子gydF4y2Ba5′-tgatagtggaaattgcatg-3′:底漆F: 5′-caccgtgatagtggaaattgcatgg-3′;底漆R: 5′-aaacccatgcaatttccactatcac-3′;(4)gydF4y2Ba”丛书gydF4y2Ba5′-gcgcggtcactgctcgttc-3′:底漆F: 5′-caccggcgcggtcactgctcgttcg-3′;底漆R: 5′-aaaccgaacgagcagtgaccgcgc-3′。gydF4y2Ba
生产慢病毒NPAS4 shRNA-mediated损耗,EP400 TIP60在原代神经元培养或表达LentiCRISPR构造,10µg慢病毒质粒转染到HEK293T细胞随着第三代包装质粒pMDL(5µg), RSV(2.5µg), VSVG(2.5µg)。LentiCRISPR池,2.5µg LentiCRISPRgydF4y2Ba”丛书gydF4y2BagRNA, LentiCRISPRgydF4y2BaScg2gydF4y2BagRNA, LentiCRISPRgydF4y2Ba脑源性神经营养因子gydF4y2BagRNA和LentiCRISPRgydF4y2BaNptx2gydF4y2BagRNA转染,总共10µg的质粒。在转染后12到16小时,转染中换取新鲜培养基,上层清液含有病毒转染48 h后收集。的成分结构,上层清液含有病毒颗粒的转染HEK293T细胞汇集,10 - 15的盘子和病毒粒子被高速离心(25000 r.p.m孤立。90分钟)。颗粒状病毒resuspended一夜之间在100 - 150年在4°Cµl 1×PBS。LentiCRISPR结构,上层清液含有病毒颗粒的转染HEK293T细胞10的盘子收集。粒子被添加沉淀1体积的4×挂钩方案(40% PEG - 8000 1×1.2 M氯化钠PBS pH值7.4)3卷的病毒上清液和存储1 h在4°C。孵化后的挂钩和病毒混合,粒子被离心沉淀,享年1500岁gydF4y2BaggydF4y2Ba45分钟。颗粒状病毒是500年在4°C resuspended隔夜µl 1×PBS。单个病毒滴定度,实现所需的最少的病毒感染约85 - 100%,作为评估GFP花期,决心为每个慢病毒(1 - 10µl每150万个神经元的成分结构,和60µl每150万个神经元LentiCRISPR构造)。神经元DIV shRNA 3日被感染病毒和收集7点DIV RNA-seq分析。神经元与LentiCRISPR DIV 2日被感染病毒和收集7点DIV sBLISS-seq分析。gydF4y2Ba
AAV骨干都是由使用标准的克隆和分子生物学技术。AAV2/9准备在波士顿儿童医院病毒核心。gydF4y2Ba
神经细胞转染和荧光素酶记者化验gydF4y2Ba
荧光素酶诱导被定位NPAS4监管目标增强荧光素酶基因的上游。序列在荧光素酶测试记者化验的基础上选择NPAS4绑定的力量培养神经元如前所述gydF4y2Ba28gydF4y2Ba。高亲和性NPAS4网站包括地区从100强中选择高信任度NPAS4-binding峰值。区域扩增小鼠基因组DNA和subcloned菌进行入pGL4.11向量使用标准的吉布森组装。引物序列见下文。gydF4y2Ba
进行荧光素酶化验,400000小鼠海马神经元被镀上24-well文化菜肴和转染质粒用Lipofectamine 2000(英杰公司)根据制造商的协议。5 DIV,神经元与1µg总DNA转染450 ng的萤火虫荧光素酶组成的记者在pGL4.11 DNA, 50 ng pGL4.74 renilla荧光素酶记者DNA (Promega)和500 ng NPAS4超表达结构。Lipofectamine(2µl,英杰公司)是用于每个1µg的DNA。DNA-lipofectamine复合物添加一滴一滴地为2 h,神经元和孵化后转染介质条件神经介质所取代。神经元沉默DIV 6日一夜之间通过添加1µM TTX (Abcam ab120055)和100年µM AP5(热费舍尔,01-061-0)。7点DIV,神经元被收集。总之,神经元洗2×PBS和细胞溶解通过添加500µl被动裂解缓冲(Dual-Luciferase记者分析系统、Promega E1910)。接下来,20μl每个溶菌产物被添加到一个好配角的白色聚苯乙烯96 -好试验板(康宁)。荧光素酶检测试剂二世(LARII)和Stop &如果试剂(Dual-luciferase试验系统,Promega)添加到神经细胞溶解产物,和荧光素酶/ renilla测量是用协同4混合标(BioTek)。gydF4y2Ba
控制变化的转染效率和细胞溶解产物生成,荧光素酶/ renilla比率首次计算出每个独立转染。荧光素酶活性(荧光素酶/ renilla)当时规范化荧光素酶活动的平均价值在核GFP-expressing控制样品收集在同一天同一文化。数据收集从至少三个独立的初级神经元文化生成在分开的日子里,除了峰1 npas4_1 - 699(来自两个独立实验)。对于每个实验文化,两到四个独立的井被转染。所有实验数据从每个独立转染显示。误差在±s.e.m。gydF4y2BaPgydF4y2Ba使用双尾值计算,未配对gydF4y2BatgydF4y2Ba测试使用棱镜(v.8.4.2)。Benjamini-Hochberg修正多重假设检验在R (v.3.6.1)执行。gydF4y2Ba
引物用上市的基因位点克隆进pGL4.11下面列出:gydF4y2Ba
峰1:染色体5:103753620 - 103754119gydF4y2Ba
F: 5′-ggaaacagtgtctcacacaacctgcagggtttctgggcactttcaaaact-3′gydF4y2Ba
R: 5′-caatgccaactgttactagctggcgcgcccgggcaccgggggcagccgggcgag-3′gydF4y2Ba
峰2:染色体7:112679812 - 112680311gydF4y2Ba
F: 5′-ggaaacagtgtctcacacaacctgcaggagcggccccgccgccct-3′gydF4y2Ba
R: 5′-caatgccaactgttactagctggcgcgccttttttggggtcctcctggg-3′gydF4y2Ba
3:峰值染色体8:84197485 - 84197984gydF4y2Ba
F: 5′-ggaaacagtgtctcacacaacctgcaggtgcctgctcgcttgttttacctcc-3′gydF4y2Ba
R: 5′-caatgccaactgttactagctggcgcgcctaccagggcgctgttggggtgggtg-3′gydF4y2Ba
4:峰值染色体1:118,825,347 - 118825846gydF4y2Ba
F: 5“-ggaaacagtgtctcacacaacctgcagggcaggttgatttggtaggaa-3”gydF4y2Ba
R: 5′-caatgccaactgttactagctggcgcgccgtgcaaggagagccgcgggcg-3′gydF4y2Ba
峰5:染色体2:94243619 - 94244238gydF4y2Ba
F: 5′-ggaaacagtgtctcacacaacctgcagggcgggtgtgcaacgggcagagag-3′gydF4y2Ba
R: 5′-caatgccaactgttactagctggcgcgcctcatgtcccacccctaggcttcctc-3′gydF4y2Ba
峰6:染色体12:104415550 - 104416049gydF4y2Ba
F: 5′-agtgtctcacacaacctgcaggcactgcagccagcgtccaccatgctt-3′gydF4y2Ba
R: 5′-aactgttactagctggcgcgcccgactccatctttgacaaaag-3′gydF4y2Ba
验证的定量逆转录聚合酶链反应gydF4y2Ba
RNA提取使用试剂盒RNeasy微工具包(试剂盒,74004),和等量的RNA (100 - 200 ng)所有样本转化为互补使用高容量cDNA工具包(热费舍尔,4368813)根据制造商的指示。互补脱氧核糖核酸是由至少三倍稀释之前运行标准定量PCR (qPCR)与反转录方法使用Sybr绿色主人混合。qPCR进行技术使用QuantStudio 3 qPCR机一式三份(应用生物系统公司)。为每个qPCR目标基因表达规范化看家基因gydF4y2BaGapdhgydF4y2Ba或gydF4y2BaTubb3gydF4y2Ba表示。以下引物被用来增强感兴趣的基因集。gydF4y2Ba
引物组:gydF4y2Ba
GapdhgydF4y2BaF: 5′-AGGTCGGTGTGAACGGATTTG-3′gydF4y2Ba
GapdhgydF4y2BaR: 5′-GGGGTCGTTGATGGCAACA-3′gydF4y2Ba
Tubb3gydF4y2BaF: 5′-TAGACCCCAGCGGCAACTAT-3′gydF4y2Ba
Tubb3gydF4y2BaR: 5′-GTTCCAGGTTCCAAGTCCACC-3′gydF4y2Ba
S100bgydF4y2BaF: 5′-TGGTTGCCCTCATTGATGTCT-3′gydF4y2Ba
S100bgydF4y2BaR: 5′-CCCATCCCCATCTTCGTCC-3′gydF4y2Ba
MoggydF4y2BaF: 5′-ACCTCTACCGAAATGGCAAGG-3′gydF4y2Ba
MoggydF4y2BaR: 5′-TCACGTTCTGAATCCTAAGGGT-3′gydF4y2Ba
Aldh1l1gydF4y2BaF: 5′-CAGGAGGTTTACTGCCAGCTA-3′gydF4y2Ba
Aldh1l1gydF4y2BaR: 5′-CACGTTGAGTTCTGCACCCA-3′gydF4y2Ba
PdgfragydF4y2BaF: 5′-AGAGTTACACGTTTGAGCTGTC-3′gydF4y2Ba
PdgfragydF4y2BaR: 5′-GTCCCTCCACGGTACTCCT-3′gydF4y2Ba
GfapgydF4y2BaF: 5′-CGGAGACGCATCACCTCTG-3′gydF4y2Ba
GfapgydF4y2BaR: 5′-AGGGAGTGGAGGAGTCATTCG-3′gydF4y2Ba
Grin1gydF4y2BaF: 5′-AGAGCCCGACCCTAAAAAGAA-3′gydF4y2Ba
Grin1gydF4y2BaR: 5′-CCCTCCTCCCTCTCAATAGC-3′gydF4y2Ba
Rbfox3gydF4y2BaF: 5′-ATCGTAGAGGGACGGAAAATTGA-3′gydF4y2Ba
Rbfox3gydF4y2BaR: 5′-GTTCCCAGGCTTCTTATTGGTC-3′gydF4y2Ba
Grin2bgydF4y2BaF: 5′-GCCATGAACGAGACTGACCC-3′gydF4y2Ba
Grin2bgydF4y2BaR: 5′-GCTTCCTGGTCCGTGTCATC-3′gydF4y2Ba
Synapsin1gydF4y2BaF: 5′-AGCTCAACAAATCCCAGTCTCT-3′gydF4y2Ba
Synapsin1gydF4y2BaR: 5′-CGGATGGTCTCAGCTTTCAC-3′gydF4y2Ba
Npas4gydF4y2BaF: 5′-ACCTAGCCCTACTGGACGTT-3′gydF4y2Ba
Npas4gydF4y2BaR: 5′-CGGGGTGTAGCAGTCCATAC-3′gydF4y2Ba
Tip60gydF4y2BaF: 5′-GTCACCCGGATGAAGAACAT-3′gydF4y2Ba
Tip60gydF4y2BaR: 5′-GGAAACACTTGGCCAGAAGA-3′gydF4y2Ba
Ep400gydF4y2BaF: 5′-CAGCTCCTCCTAAGCCACAG-3′gydF4y2Ba
Ep400gydF4y2BaR: 5′-CCTCTTGAAGCTTTGGCAAC-3′gydF4y2Ba
流式细胞仪染色和排序神经元细胞核DNA隔离gydF4y2Ba
神经元细胞核DNA进行排序隔离,切割海马组织放置在1毫升的缓冲区HB (0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺)和dounced 5×0.5毫米松与紧杵杵和10×。IGEPAL ca - 630(5%, 32µl)添加之前douncing又紧杵5 - 8倍。细胞核悬挂在HB 40-µm过滤器的过滤。细胞核被离心500然后颗粒状gydF4y2BaggydF4y2Ba5分钟和400年resuspendedµl流式细胞仪块/污点缓冲区(1% BSA, 0.05% IGEPAL ca - 630, 3毫米MgClgydF4y2Ba2gydF4y2Ba在1×PBS)。核与温柔孵化15分钟旋转在4°C。这个阻塞步骤后,核是颗粒状和resuspended在流式细胞仪块/污点缓冲区包含1:1,000稀释的鼠标anti-NeuN-Alexa488(微孔,MAB377X cloneA60)。设置盖茨,同形像控制鼠标IgG-Alexa488(生活技术,MA518167)作为消极的控制以及一个清白的样本。在抗体混合样本孵化1 h和温柔的旋转在4°C。核与流式细胞仪块/污点洗1×缓冲区,和DRAQ5核染料(Abcam ab108410)添加排序前(1:50 0)。NeuN high-expressing核是分开NeuN使用索尼SH800 low-expressing核。核排序直接到ATL裂解缓冲QIAamp DNA微工具包中提供。DNA提取使用QIAamp DNA微工具包(试剂盒,56304)根据制造商的协议和存储在−80°C到扩增子库的准备。流式细胞仪分析在控制数据显示整个手稿进行了使用FlowJo (10.0.8rl)。gydF4y2Ba
流式细胞仪分选AAV-infected神经元细胞核急忙逃走gydF4y2Ba
切割海马组织检查下荧光检测范围GFP(ΔCre)或mCherry (Cre)。未受感染的组织,或在极少数情况下显示感染的荧光团在一个半球,被丢弃。海马被放置在0.5毫升的缓冲区HB (0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺)和dounced 5×0.5毫米松与紧杵杵和10×。IGEPAL ca - 630(5%, 32µl)添加在douncing紧杵5 - 8次通过40-µm过滤器和过滤。DRAQ5核染料(Abcam ab108410)添加(1:50 0)和核表达mCherry或索尼SH800 GFP是排序。-盖茨决定使用未受感染的组织。核收集1毫升急忙逃走包含2毫米EDTA清洗缓冲。流式细胞仪分析在控制数据显示整个手稿进行了使用FlowJo (10.0.8rl)。gydF4y2Ba
RNA-seq图书馆准备gydF4y2Ba
神经元控制shRNA病毒感染或病毒攻击gydF4y2BaNpas4gydF4y2Ba,gydF4y2BaEP400gydF4y2Ba或gydF4y2BaTip60gydF4y2Ba洗两次了PBS立即去除死细胞和刮成试剂盒。在海马体搭配sBLISS-seq野生型次microdissected组织当时flash冻结和解冻的试剂盒。RNA提取使用RNAeasy工具包(试剂盒)根据制造商的指示。总RNA (1000 ng)是用于生成库后核糖体RNA损耗(NEBNext E6310X)根据制造商的指示(NEBNext E7420)。为培养神经元,读取85个基点上生成一个Illumina公司NextSeq 500,随后分析了与我们的标准化RNA-seq数据分析管道(下图)。野生型次样本,40 bp paired-end读取得到的Illumina公司NextSeq 500。gydF4y2Ba
ATAC-seq图书馆准备gydF4y2Ba
为ATAC-seq库生成的海马神经元亚型体内,gydF4y2BaCamkIIagydF4y2Ba表达CA1锥体神经元被隔绝gydF4y2BaCamk2agydF4y2BaCregydF4y2Ba;Sun1gydF4y2Bafl / +gydF4y2Ba老鼠使用完整的方法gydF4y2Ba53gydF4y2Ba。总之,海马在缓冲区HB (dounced 15×0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺0.5毫米)释放核。细胞核被旋转通过纯化iodixanol梯度在10000gydF4y2BaggydF4y2Ba(见描述核隔离在急忙逃走的实验)。核核膜上表达SUN1-GFP Cre-dependent的方式被孵化孤立的核悬挂10μg anti-GFP抗体(表达载体,G10362) 30分钟在4°C。Antibody-coated核随后被孵化与磁性蛋白质G Dynabeads(热费希尔)。核隔离和计算后,大约30000 - 40000核条件在L1 resuspended裂解缓冲(100毫米HEPES-NaOH pH值7.5,280毫米氯化钠,EGTA 2毫米,2毫米EDTA,特里同x - 100 0.5%,甘油NP-40 1%和20%),其次是5分钟孵化在L2裂解缓冲(10毫米Tris-HCl pH值8.0,200毫米氯化钠)和5分钟孵化ATAC裂解缓冲(10毫米Tris-HCl pH值7.4,10毫米氯化钠,MgCl 3毫米gydF4y2Ba2gydF4y2Ba和0.1% IGEPAL ca - 630)。gydF4y2Ba
细胞核被调换使用Nextera DNA库准备工具包(Illumina公司,fc - 121 - 1030)如前所述gydF4y2Ba56gydF4y2Ba。进行换位为30分钟37°C。转置从单个样本纯化DNA片段,第8 - 11独立编码和放大周期。ATAC-seq库选择碎片从200到1000个基点的凝胶电泳和测序Illumina公司NextSeq 500与75 bp单头读取。gydF4y2Ba
急忙逃走gydF4y2Ba
急忙逃走实验如前所述gydF4y2Ba6gydF4y2Ba。NuA4组件的映射4-6-week-old野生型小鼠(无花果。gydF4y2Ba1gydF4y2Ba),复制由池4 - 5小鼠分别处理。看到补充表gydF4y2Ba2gydF4y2Ba复制数据。男性和女性在平等的比例合并复制样品。总之,新鲜的海马组织汇集从4 - 5老鼠放入5毫升的缓冲区HB (0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺)和dounced 15×0.5毫米的杵。IGEPAL ca - 630(5%, 320µl)添加之前douncing杵5次,样品是透过40-µm过滤器变成15毫升锥形管集合。5毫升的工作解决方案(iodixanol 50%,氯化钾25毫米,5毫米MgClgydF4y2Ba2gydF4y2Ba7.8,Tricine-KOH 20毫米,pH值,补充蛋白酶抑制剂,德勤,精胺和亚精胺)添加到样本。均质组织之上轻轻添加2毫升30/40% iodixanol层。样本离心机,享年10000岁gydF4y2BaggydF4y2Ba18分钟,1毫升的原子核收集30/40% iodixanol接口。核数和均匀分布在以下数量:如果和刺激条件”丛书(房子),H3K27ac (Abcam ab4729): 75000核;NPAS4(房子),EP400(架a300型Bethyl实验室- 541 a;Abcam Ab5201) ARNT2(房子),RAD50(罗福斯生物制品,nb100 - 154): 1000000核;MRE11(罗福斯生物制品,nb100 - 142), CTCF(活动主题,61311),ETL4 (Bethyl实验室、a304 - 928 a): 500000核。的样品FACS-isolatedgydF4y2BaNpas4gydF4y2BacKO老鼠,MRE11和EP400急忙逃走了100000核。复制的感染,FACS-sorted样品由独立池两到三只老鼠。gydF4y2Ba
相同数量的核之间如果(PBS-injected老鼠)和刺激条件(2 h KA-injected老鼠)整除进1毫升急忙逃走洗缓冲区(20毫米消息灵通的pH值7.5,150毫米氯化钠,Tween-20 0.2%, 1毫克毫升gydF4y2Ba−1gydF4y2BaBSA、丁酸钠10毫米和0.5毫米亚精胺与蛋白酶抑制剂补充)。磁concanavalin-A (ConA)珠子(刘海实验室),洗急忙逃走绑定缓冲(20毫米HEPES-KOH pH值7.9,10毫米氯化钾,CaCl 1毫米gydF4y2Ba2gydF4y2Ba和1毫米MnClgydF4y2Ba2gydF4y2Ba)被添加到每个样本结合细胞核。ConA-bead-bound一夜之间,细胞核被孵化在4°C洗缓冲区(20毫米消息灵通的pH值7.5,150毫米氯化钠,Tween-20 0.2%, 1毫克毫升gydF4y2Ba−1gydF4y2BaBSA, 0.1% Triton x - 100, 2毫米EDTA, 10毫米丁酸钠和0.5毫米亚精胺与蛋白酶抑制剂补充)包含上述1:50稀释的抗体。gydF4y2Ba
与抗体隔夜孵化后,ConA-bead-bound核与急忙逃走的抗体洗缓冲和resuspended急忙逃走Triton-wash缓冲区(急忙逃走洗缓冲补充Triton x - 100)为0.1%。Protein-A-MNase添加在最后700 ng毫升的浓度gydF4y2Ba−1gydF4y2Ba在4°C,样本孵化1 h。ConA-bead-bound核下洗两次,急忙逃走Triton-wash缓冲区和100年resuspendedμl急忙逃走Triton-wash缓冲区。之后的3μl CaCl 100毫米gydF4y2Ba2gydF4y2Ba在冰上,样本孵化了30分钟。停止MNase反应,2×100μl停止缓冲(340毫米氯化钠20毫米EDTA 4毫米EGTA, 0.04% Triton x - 100 pg 20毫升gydF4y2Ba−1gydF4y2Ba酵母在DNA和0.1μg毫升gydF4y2Ba−1gydF4y2Ba核糖核酸酶A)被添加到每个样本在孵化前20分钟的37°C。孵化后,一块磁铁是用来捕捉Con-A-beads,上层清液含有DNA片段protein-A-MNase发布的收集。2毫升10% SDS和2μl 20毫克gydF4y2Bal−1gydF4y2Ba蛋白酶K被添加到上层的其次是孵化65°C与温柔的摇晃1 h。使用标准phenol-chloroform提取乙醇沉淀沉淀DNA。gydF4y2Ba
从沉淀DNA测序库生成暂停在TE缓冲(如前所述)gydF4y2Ba57gydF4y2Ba,用以下的变化:快速T4 DNA连接酶(酶)被用来执行适配器连接到end-repaired和A-tailed DNA。适配器二聚体被从扩增库使用菌进行1.1×AMPure比XP珠子。急忙逃走库测序在Illumina公司NextSeq 500使用40-bp paired-end读取。gydF4y2Ba
ChIP-seqgydF4y2Ba
ChIP-seq,复制由四到五池老鼠进行独立的日子。ChIP-seq NPAS4从海马组织,从15个老鼠dounced海马5毫升1×PBS含有蛋白酶抑制剂鸡尾酒(罗氏,11836153001)。甲醛(1%)被添加到组织匀浆和孵化10分钟在室温下,紧随其后的是0.125米的甘氨酸在室温下为5分钟。γH2AX的芯片gydF4y2BaCamk2agydF4y2Ba表达CA1锥体神经元,细胞核被隔绝gydF4y2BaCamk2agydF4y2BacregydF4y2Ba;Sun1gydF4y2Bafl / +gydF4y2Ba老鼠使用完整的方法gydF4y2Ba53gydF4y2Ba(有关详细信息,请参阅ATAC-seq图书馆准备部分核隔离)。隔离后,核与附加珠子与1%的甲醛交联1毫升1×PBS在室温下10分钟。交联就熄了的0.125米甘氨酸在室温下为5分钟。交联核冻结并存储在−80°C在继续之前的协议下面。gydF4y2Ba
原子核释放组织了10分钟孵化裂解缓冲1(两)(100毫米HEPES-NaOH pH值7.5,280毫米氯化钠,EDTA 2毫米,2毫米EGTA,特里同x - 100 0.5%,甘油NP-40 1%和20%)之后,洗在缓冲区包含10毫米Tris-HCl pH值8.0,氯化钠和200毫米。染色质是剪使用Bioruptor (Diagenode)高功率模式与30年代40-42周期脉冲声波降解法缓冲区(10毫米Tris-HCl pH值8.0,100毫米氯化钠,EDTA 1毫米,0.5毫米EGTA,脱氧胆酸盐钠0.1%和0.5%gydF4y2BaNgydF4y2Ba-lauroylsarcosine)。gydF4y2Ba
声波降解法后,1.5毫升的染色质从海马组织(约60µg)补充1% Triton和孵化一夜之间在4°C 4µg NPAS4(房子)耦合到15µl蛋白质Dynabeads(表达载体,10001 d)。γH2AX芯片,1.5毫升的染色质释放约100000纯化细胞核是孵化2µl反γH2AX (Abcam ab2893)耦合到15µl Dynabeads蛋白质。珠子在0.5毫升以下顺序洗两次缓冲区:低盐缓冲(20毫米三pH值8,150毫米氯化钠,2毫米EDTA, 1% Triton x - 100和0.1% SDS),高盐缓冲(20毫米三pH值8,500毫米氯化钠,2毫米EDTA, 1% Triton x - 100和0.1% SDS),氯化锂洗缓冲区(10毫米三羟甲基氨基甲烷pH值8液,1毫米EDTA, NP-40 1%, 250毫米氯化锂和钠脱氧胆酸盐1%),其次是用1毫升的TE缓冲。Protein-DNA复合物被孵化筛选了掉珠子200μl TE + 1% SDS 30分钟在65°C。DNA交联被孵化了一夜之间在65°C。第二天,RNA和蛋白质被消化掉的10μg核糖核酸酶A和5 - 7μl蛋白酶K(新英格兰生物学实验室,P8107S)。DNA是由标准phenol-chloroform提取纯化。ChIP-seq库生成使用一个鼓掌超低V2工具包(Nugen, 0344 - 32)根据制造商的指示和PCR扩增为13 - 16周期,这取决于抗体。图书馆质量评估使用安捷伦2100生物分析仪(安捷伦科技)。读(75个基点)是使用一个生成Illumina公司NextSeq 500。gydF4y2Ba
snRNA-seqgydF4y2Ba
分离海马核,我们把瞬间冷冻海马组织0.5毫升的缓冲区HB (0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺)和dounced 5×0.5毫米松与紧杵杵和10×。IGEPAL ca - 630(5%, 32µl)添加在douncing紧杵5 - 8次通过40-µm过滤器和过滤到一个15毫升锥形管集合。缓冲HB(3.5毫升)和5毫升工作方案(iodixanol 50%,氯化钾25毫米,5毫米MgClgydF4y2Ba2gydF4y2Ba7.8,Tricine-KOH 20毫米,pH值,补充蛋白酶抑制剂,德勤,精胺和亚精胺)补充道。均质组织之上轻轻1毫升30% iodixanol之上的一层1毫升40% iodixanol从工作的解决方案(稀释)。样本离心机,享年10000岁gydF4y2BaggydF4y2Ba18分钟,70µl的原子核收集30/40% iodixanol接口。每个样本的整除与锥虫蓝孵化,使用标准的血球计和核数。gydF4y2Ba
snRNA-seq使用10倍基因组学进行铬单细胞工具包(v.3)。每个反应巷满载着10000核从一个海马半球(感染Cre-mCherry或ΔCre-GFP)从一个鼠标。互补脱氧核糖核酸扩增和图书馆准备进行后续步骤根据制造商的协议(10倍基因组学)。样本测序使用Illumina公司NextSeq 500年28日英国石油公司(R1), 56个基点(R2)和8个基点(索引)。gydF4y2Ba
促进病毒的检测记录,剩余2µl UMI-barcoded cDNA是放大在一个单独的组pcr增加大量的UMI-labelled病毒记录。自定义引物被用来放大mCherry或者GFP记录出现在编码cDNA库。嵌套PCR策略使用Q5高保真酶被用来减少非特异性产物,与正向引物在第二反应也添加序列Illumina公司Read2 (R2)放大产品(引物:GFP放大1:5′-CGCCGACCACTACCAGCAGAACACC-3′;GFP放大2:5′-GTGACTGGAGTTCAGACGTGTGCTCTTCCGATCTgctgganttcgtgaccgccgcc-3′;mCherry放大1:5′- CACTACGACGCTGAGGTCAAGACCACC-3′;mCherry放大2:5′-GTGACTGGAGTTCAGACGTGTGCTCTTCCGATCTgcgccgagggccgccactcc-3′)。PCR产品分离后的第一和第二步骤嵌套PCR与SPRIselect试剂使用0.6×大小选择。最终产品从嵌套PCR 1:10稀释,然后放入一个示例使用示例索引索引PCR引物和铬i7样本分度盘,所述的10倍基因组学图书馆准备协议。这些病毒转录sample-indexed飙升到测序运行用于相应的互补脱氧核糖核酸数据库。我们的最终数据集包括两个独立的收集的32418个核gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠和三个独立收集的44511个核gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠。最终,我们发现12963 Cre-infected和8845ΔCre-infected核gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2BasnRNA-seq数据集,以及13536 Cre-infected和13461ΔCre-infected核gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba数据集(扩展数据图。gydF4y2Ba4gydF4y2Ba)。gydF4y2Ba
sBLISS-seq培养神经元和孤立的海马核gydF4y2Ba
核孤立、固定和适配器结扎gydF4y2Ba
sBLISS-seq进行培养的神经元细胞核或核分离海马组织根据先前描述的协议gydF4y2Ba30.gydF4y2Ba。复制由个人为野生型小鼠时间进程。Cre和ΔCre数据集,一个复制的一个受感染的半球从一个鼠标。样本配对,这样2 h KA_CRE1和2 h KA_ΔCre1来自相同的老鼠。对于sBLISS-seq上执行gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaTip60gydF4y2Ba野生型或cKO核感染装甲防护、海马组织解剖并迅速检查下荧光检测范围GFP(ΔCre)或mCherry (Cre)。未受感染的组织,或在极少数情况下显示感染的荧光团在一个半球,被丢弃。AAV-infected海马,组织没有排序,以减少压力可以诱发异位的核DNA断裂。未感染的海马核用于野生型sBLISS-seq次课程中,海马是切割和加工如下所述。gydF4y2Ba
为sBLISS-seq过程海马组织,海马被放置在1毫升的缓冲区HB (0.25 M蔗糖,25毫米氯化钾,MgCl 5毫米gydF4y2Ba2gydF4y2Ba,20毫米Tricine-KOH, pH值7.8,德勤1毫米,0.15毫米精胺和亚精胺)和dounced 5×0.5毫米松与紧杵杵和10×。IGEPAL ca - 630(5%, 32µl)添加在douncing紧杵5 - 8次通过40-µm过滤器和过滤。保护DNA减免协议的其余部分,细胞核被固定为2% PFA(电子显微镜科学,15710)淬火与125毫米甘氨酸紧随其后。500年离心法在轻轻固定核颗粒状gydF4y2BaggydF4y2Ba。删除多余的碎片和髓鞘,固定核运行通过修改iodixanol梯度。颗粒状核resuspended iodixanol 1毫升的22%,100µl 43% iodixanol之上。核离心机在1500gydF4y2BaggydF4y2Ba15分钟的埃普多夫斗摆动转子离心5804 r。核(100µl)结算43/22%接口,收集和转移到蛋白质Low-Bind管。核与冰冷的PBS洗一次加1% BSA与冰冷的1×2洗PBS紧随其后。固定核数(715000核野生型次课程,大约250000个核gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和野生型CreΔCre数据集,和大约100000核gydF4y2BaTip60gydF4y2Bafl / flgydF4y2BaCre和ΔCre数据集)和被转移到新的管开始适配器结扎。gydF4y2Ba
注意,野生型时间进程在两批样品进行刺激时间点跨越这两个批次。我们观察一批效果处理的样品,这是计算删除(见sBLISS-seq样本的分析)。的批处理相关样品补充表中列出gydF4y2Ba2gydF4y2Ba。还请注意,野生型样品时间进程包括激增2%人类HEK293T细胞表达减少guide-RNA-induced网站。激增正常化并不是表现在最后数据处理由于低表达的指导和低覆盖率减少读取的网站/样品。gydF4y2Ba
从培养分离核神经元镀在6-well菜Cas9控制实验中,神经元与冰冷的PBS洗清除残骸和1毫升的HB,和32µl 5% IGEPAL ca - 630添加到每个。细胞培养10分钟在HB温柔旋转在4°C去除由温柔的抓取和转移到埃普多夫管。原子核从培养神经元是固定的2% PFA(电子显微镜科学,15710)其次是淬火与125毫米甘氨酸和轻轻颗粒状离心法在500年gydF4y2BaggydF4y2Ba。上述梯度是省略了由于缺乏碎片和髓鞘神经文化。核与冰冷的PBS洗一次加1% BSA与冰冷的1×2洗PBS紧随其后。约1×10gydF4y2Ba6gydF4y2Ba培养核被用于体外CRISPR-Cas9数据集。gydF4y2Ba
固定核孵化1 h在LB2 37°C(10毫米Tris-HCl, 150毫米氯化钠和0.3% SDS)。原子核在CutSmart洗两次洗缓冲区(1×CutSmart(新英格兰生物学实验室,B7204)和0.1% Triton x - 100)。在室温下,原子核钝化使用快速削弱工具包(新英格兰生物学实验室,E1201) 1 h。后两个洗CutSmart洗缓冲区,适配器被绑定到免费使用T4 DNA以完整的核DNA连接酶(5 U mlgydF4y2Ba1gydF4y2Ba;热费希尔科学、EL0011)。结扎反应进行了约18 h全能料理机在16°C。第二天,核与CutSmart洗两次清洗缓冲和孵化一夜之间100年µl DNA提取缓冲(10毫米Tris-HCl, 100毫米氯化钠,10毫米EDTA和0.5% SDS)包含10µl蛋白酶K(20毫克毫升gydF4y2Ba1gydF4y2Ba;新英格兰生物学实验室)。DNA提取使用标准phenol-chloroform超纯的提取和在18µl resuspended DNase / RNase-free水随后的碎片。gydF4y2Ba
DNA碎片,早期诊断和库生产gydF4y2Ba
体外和野生型时间课程样本使用Bioruptor支离破碎,30年代,60年代,高强度,35 - 40周期。由于有限的输入CreΔCre样本,我们发现使用酶碎片保存DNA片段比声波降解法。因此,所有样本海马组织分散使用内Fragmentase 40 - 50分钟在37°C。这种治疗导致400 - 800 bp大小的碎片,平均库大小约650个基点。碎片和清理后,100 ng(培养神经元样本),200 ng(野生型时间课程样本)或35 ng (Cre和ΔCre样本)进行反向转录MegaClear诊断工具包(热费希尔,AMB13345)。图书馆从早期产品生产没有偏离协议如前所述gydF4y2Ba30.gydF4y2Ba。总之,模板DNA被孵化溶产品2μl DNaseI(热费希尔,AM2222) 15分钟,和RNA是纯化使用RNAXP干净的珠子。RA3中适配器(/ 5拉普/ TGGAATTCTCGGGTGCCAAGG / 3 spc3 /)使用T4结扎在RNA RNA连接酶2,截断(新英格兰生物学实验室,M0242L)。RNA被反向转录使用反向引物RTP (5′-GCCTTGGCACCCGAGAATTCCA-3′)和一个上标IV逆转录酶工具包(热费舍尔,18090200)。最后,DNA被放大使用NEBNext超二世Q5大师混合(新英格兰生物学实验室,M0544L) 8 50μl的反应。图书馆是测序用单头75个基点读取Illumina公司NextSeq 500。gydF4y2Ba
END-seqgydF4y2Ba
文化小鼠皮层神经元END-seq被感染的新成分慢病毒DIV 3日7日之前收集DIV。复制由文化上生成独立的日子。为END-seq分离培养小鼠皮层神经元,木瓜蛋白酶(卫氏生化,LK003178)溶解在TrypLE表达酶解决方案在37°C 20分钟前样本集合。培养基轻轻吸气,细胞被轻轻洗一次与PBS 37°C。木瓜蛋白酶解(500µl)被添加到每个神经元在6-well盘子和孵化的37°C 1分钟。木瓜蛋白酶的解决方案是使用吸管,和500年µl研碎的解决方案(与新鲜培养基补充溶解DNase)补充道。细胞与大孔吸管轻轻磨碎5—10次,转移到锥形管和颗粒状。细胞被轻轻resuspended冰冷的PBS中含0.1% BSA和0.5毫米EDTA计数。细胞被存储在冰而整除很快使用血球计算。接下来,150万个神经元为每个实验条件被添加到一个新的锥形管和颗粒状。 Cells were then embedded in agarose plugs using a CHEF Mammalian Genomic DNA Plug kit (Bio-Rad, 1703591) and processed for END-seq as previously described32gydF4y2Ba,gydF4y2Ba58gydF4y2Ba。实验组连续处理,收集细胞在一个治疗组和嵌入在琼脂糖插头之前收集在未来治疗组细胞减少overdigestion细胞分裂之间的样品和减少时间和嵌入在琼脂糖。我们观察到更好的信噪比和依托泊苷(50µM)细胞治疗。依托泊苷被加入到细胞收集和前6小时50µM包含在所有的解决方案应用于细胞直到嵌入琼脂糖。gydF4y2Ba
扩增子PCR测序(SiMSen-seq)gydF4y2Ba
选择站点进行突变分析gydF4y2Ba
选择网站检查期间为突变负荷老化,宇宙可能的网站检查是由所有访问地区的联盟gydF4y2BaCamkIIagydF4y2Ba表达神经元(主要在CA1海马区细胞类;在我们完整的定义gydF4y2BaCamkIIagydF4y2Ba数据集)和所有地区,在海马H3K27ac细胞核。这生成一组179841个可能的地区,我们认为windows 500个基点的这些山峰的中心。我们计算ATAC-seq规范化阅读强度,H3K27ac急忙逃走,γH2AX ChIP-seq使用函数DeSeq2计数(dds,规范化= TRUE)gydF4y2Ba59gydF4y2Ba每一种可能的地区在所有条件。我们还为NPAS4提取规范化信号强度和MRE11使用荷马(荷马/ 4.9)annotatePeaks急忙逃走。pl函数默认正常化1000万测序读。最后,我们决定区域重叠NPAS4和/或MRE11峰值至少1 bp。这些网站被认为是“绑定”。gydF4y2Ba
使用前面提到的地区,我们选择网站查询基于以下标准:(1)最高的网站受NPAS4和MRE11规范化NPAS4信号;(2)网站受NPAS4和MRE11显示增加γH2AX ChIP-seq信号后神经元激活。我们还包括一组站点没有重叠NPAS4或MRE11高峰,作为一个群体的GC含量没有显著差异,染色质易访问性或H3K27ac水平。然而,我们注意到在我们最后的选址,有些网站没有这些条件相匹配的有效放大在我们的分析,因此排除了由于技术因素。最后一组的网站化验补充表中被发现gydF4y2Ba5gydF4y2Ba。gydF4y2Ba
引物设计使用自定义脚本调用Primer3,与来自Primer3格式gydF4y2Bahttp://bioinfo.ut.ee/primer3-0.4.0/input-help.htmlgydF4y2Ba。以下序列附加到正向引物的5′端GGACACTCTTTCCCTACACGACGCTCTTCCGATCTNNNNNNNNNNNNATGGGAAAGAGTGTCC,其中12 Ns随机核苷酸组成一个UMI代表。以下序列附加到反向引物的5′端GTGACTGGAGTTCAGACGTGTGCTCTTCCGATCT。引物序列的扩增子有针对性的补充表中可以找到gydF4y2Ba5gydF4y2Ba。引物被命令200点或4海里Ultramers踊跃参与。gydF4y2Ba
生产有针对性的扩增子库gydF4y2Ba
扩增子库生成使用先前描述的协议gydF4y2Ba38gydF4y2Ba与一些细微的修改。对所有样本,感兴趣的网站被分成15个引物池集(见补充表gydF4y2Ba5gydF4y2Ba底漆池)。对于每个引物池,20 - 30 ng的DNA分离FACS-isolated NeuNgydF4y2Ba+gydF4y2Ba核是第一次放大Phusion热起动II高保真DNA聚合酶(热费希尔,f - 549 l)附加UMI序列DNA模板。每个引物的最终浓度的反应是40 nM。聚合酶链反应参数对这些4周期如下:98°C, 30年代;4周期98°C, 10 s, 62°C, 6分钟72°C, 30年代;其次是65°C 15分钟;95°C, 15分钟。在65°C孵化,孵化的PCR反应终止与10µl蛋白酶(Sigma-Aldrich p5147 - 100毫克;使用0.06的最终浓度µgµlgydF4y2Ba1gydF4y2Ba)。对于每个引物池,10µl初始产品下一个放大使用Phusion热起动II高保真DNA聚合酶用以下参数:98°C, 3分钟;2-35周期98°C, 10 s 80°C, 1 s;72°C, 30年代;76°C, 30年代。所有与增加0.2°CgydF4y2Ba1gydF4y2Ba。重复反应进行每个引物池增加UMI抽样的多样性在最后的库。样本size-selected包括产品在长度约275 - 650个基点。分析了使用Debarcer v.0.3.1 (gydF4y2Bahttps://github.com/oicr-gsi/debarcer/releases/tag/v0.3.1gydF4y2Ba)gydF4y2Ba38gydF4y2Ba。gydF4y2Ba
寿命分析和组织NPAS4击倒队列的集合gydF4y2Ba
Npas4gydF4y2Ba野生型或敲除的同胞被安置在符合协议批准的哈佛大学动物保健常务委员会。同窝出生被安置在一起,由训练有素的技术人员监控整体健康。任何不良动物或那些显示健康状况不佳是安乐死在数据收集和审查。动物被用于组织收集的目的最终收集日期前被审查的最终寿命分析。由于COVID-19关闭强加的限制,最后研究了2020年3月,当所有剩余动物解剖。出于这个原因,的寿命gydF4y2BaNpas4gydF4y2Ba野生型的同胞不去完成。生存曲线的意义决定使用一个log-rank (Mantel-Cox)和Gehan-Wilcoxon-Breslow使用棱镜(v.8.4.2)软件测试。gydF4y2Ba
量化和统计分析gydF4y2Ba
统计分析和样本大小的决心gydF4y2Ba
每个实验的统计分析中详细图传说。电生理检测盲法的方式进行,这样条件(saline-injected与KA-injected)分析完成后才显示。统计方法是不习惯预先确定样本大小,但复制数字通常坚持编码协会的指导方针gydF4y2Ba60gydF4y2Ba。样本随机化不执行。所有统计分析了棱镜(v.8.4.2)或R (v.3.6.1)。为多个假设修正扩展数据无花果所示。gydF4y2Ba6 egydF4y2Ba和gydF4y2Ba13 bgydF4y2Ba,gydF4y2BaPgydF4y2Ba值获得使用棱镜(v.8.4.2)纠正使用padjust()函数R (v.3.6.1)在基地。gydF4y2Ba
肽定量质谱gydF4y2Ba
质谱和肽进行了量化的标准实践近代生物质谱设备,哈佛医学院。数据收集使用LTQ Orbitrap Velos精英离子阱质谱仪(热费希尔科学)。简言之,程序Sequest(热费希尔科学)被用来比较多肽和蛋白质数据库获得分散的模式。数据被过滤肽错误发现率1%和2%之间(罗斯福)和数据库包括了版本的所有序列。一式三份NPAS4 immunoprecipitation-mass谱实验从海马组织执行。重复实验进行高分子量分数使用NPAS4-Flag-HA和TIP30-H3-Flag皮质溶解产物。所有质谱肽计数实验提供了补充表gydF4y2Ba1gydF4y2Ba。3.6.1 (R)包磨边机gydF4y2Ba61年gydF4y2Ba(edgeR_3.28.1; limma_3.42.2)是用于识别蛋白质显著富集NPAS4或TIP60免疫沉淀物样本相对于野生型样品,没有表达Flag-tagged蛋白质。蛋白质被识别至少2/3的复制被包含在刨边机分析。肽在NPAS4发现野生型控制样品和不严格或TIP60样本(即与M2树脂相关背景)被移除之前运行磨边机glmFit()和glmLRT()函数。gydF4y2Ba
测序和比对gydF4y2Ba
所有实验测序Illumina公司NextSeq 500 (Illumina公司Next-Seq控制软件v.4.0.2)。测序数据中提供补充信息表gydF4y2Ba2gydF4y2Ba。单头读取(75个基点)获得ATAC-seq, ChIP-seq, RNA-seq(培养神经元)和sBLISS-seq。Paired-end读取(40 bp)所有急忙逃走的实验中,均获得snRNA-seq实验和海马KA时间进程RNA-seq实验。单头读取(162个基点)获得扩增子库用于突变分析。gydF4y2Ba
ATAC-seq和ChIP-seq样本(即NPAS4芯片和γH2AX芯片),质量调整的执行顺序读取trimmomatic / 0.36 (ref。gydF4y2Ba62年gydF4y2Ba使用以下命令:java jar trimmomatic - 0.33。jar SE线程1 -phred33 [FASTQ_FILE] ILLUMINACLIP: [ADAPTER_FILE]: 2:30:10领先:5落后:5 SLIDINGWINDOW: 4:20 MINLEN: 35。Nextera适配器指定ATAC-seq, TruSeq适配器被指定为ChIP-seq样本。样本随后使用领结mm10基因组排列对齐软件(vbowtie2/2.2.9)非常敏感的设置。读取映射到线粒体基因组被移除。重复的读取是标有皮卡德/ 2.8.0命令java jar皮卡德/ picard-2.8.0美元。jar MarkDuplicates REMOVE_DUPLICATES = false。重复使用samtools随后被删除/ 1.3.1 samtools视图- b - f 1796。gydF4y2Ba
急忙逃走样品,质量读执行削减使用trimmomatic / 0.36使用以下命令:java jar trimmomatic - 0.33。jar PE -phred33 [FASTQ_FILE] ILLUMINACLIP: / n / app / trimmomatic / 0.36 / bin /适配器/ TruSeq3-PE。费尔南多-阿隆索:2:15:4:4:真正的领导:20后:20 SLIDINGWINDOW: 15 MINLEN: 25。根据管道和适配器进一步削减脚本(kseq_test)如前所述gydF4y2Ba63年gydF4y2Ba。Paired-end读取映射到鼠标基因组使用下面的命令:bowtie2/2.2.9 bowtie2——当地very-sensitive-local——no-unal - x mm10——燕尾——没有混合——no-discordant phred33我10 - x 700。酵母在读取映射使用以下命令:bowtie2——当地very-sensitive-local——no-unal - x sacCer3 no-dovetail没有重叠,没有混合——no-discordant phred33我10 - x 700。阅读深度(归一化到100万)或峰值(1)标准化规范化bedgraph Spike_in_Calibration_v2文件创建使用自定义脚本修改。csh如前所述gydF4y2Ba63年gydF4y2Ba。最后,bedGraphToBigWig (ucsc-tools / 363)是用于生成大佬文件从阅读深度规范化bedgraph文件。文件上显示的IGV浏览器显示读取depth-normalized要人。映射sBLISS-seq样本根据执行先前描述的协议gydF4y2Ba30.gydF4y2Ba。管道从git克隆,克隆的映射gydF4y2Bahttps://github.com/BiCroLab/blissNP.gitgydF4y2Ba。gydF4y2Ba
为扩增子库分析,适配器对NeuN污染是一个严重的问题gydF4y2Ba+gydF4y2Ba排序的数据集。样本因此修剪与以下修剪命令删除这些适配器:java jar trimmomatic - 0.33。jar SE线程1 -phred33 [FASTQ_FILE] ILLUMINACLIP: [ADAPTER_FILE]: 2:30:10领先:5落后:5 SLIDINGWINDOW: 15 MINLEN: 120。FASTQ文件只包含修剪,adapter-removed读取基因表达提供了综合(GEO)提交。满FASTQ文件将根据要求提供。使用默认参数映射使用BWA进行概述在包Debarcer v.0.3.1 (gydF4y2Bahttps://github.com/oicr-gsi/debarcer/releases/tag/v0.3.1gydF4y2Ba)gydF4y2Ba38gydF4y2Ba。gydF4y2Ba
END-seq读取被对齐参考基因组mm10使用subread (v.1.5.1)参数subread-align 1 - t - t 6 - m 3。Samtools (v.1.13)功能,markdup用于创建索引和索引是本文件删除了重复的读取。文件downsampled最低数量的读入任何样本内复制,和标记目录编译使用makeTagDirectory荷马(v.4.9)命令。标记目录是用于生成聚合情节集中在各种使用荷马annotatePeaks基因感兴趣的网站。造10000嘘50 pl与参数。对于统计测试,信号提取窗口内的基因组使用荷马annotatePeaks感兴趣的网站。pl参数造500。gydF4y2Ba
SAR-seq分析gydF4y2Ba
先前发表的gydF4y2Ba32gydF4y2BaSAR-seq数据集从GEO数据库下载,加入号码gydF4y2BaGSE167259gydF4y2Ba。三个复制中执行的SAR-seq iNeurons (postmitotic glutamatergic神经元来自诱导多能干细胞)检索(gydF4y2BaGSM5100400gydF4y2Ba,gydF4y2BaGSM5100401gydF4y2Ba和gydF4y2BaGSM5100402gydF4y2Ba)。标记目录是用于生成聚合情节集中在各种使用荷马annotatePeaks基因感兴趣的网站。造10000嘘50 pl与参数。对于统计测试,信号提取窗口内的基因组网站使用“annotatePeaks荷马的兴趣。pl 500年造的参数。站点列表生成的老鼠(mm10)被取消在人类与人类SAR-seq hg19使用数据,使用UCSC基因组浏览器liftOver工具。与不重叠的信号来生成网站NPAS4”丛书,NPAS4和安全系数峰会都扩展为1 kb。NPAS4-bound网站(FOS)提交生成使用bedtools / 2.27.1相交床- v选项来生成峰没有NPAS4,反之亦然。gydF4y2Ba
有重大影响的可视化gydF4y2Ba
为ATAC-seq生成大佬文件,ChIP-seq急忙逃走的数据集,所有对齐bam文件为每个复制给定试验条件的汇集和转换为床上格式bedtools / 2.27.1 bamtobed。ATAC-seq和ChIP-seq数据,75个基点读取3′方向扩大到200个基点(平均片段长度ChIP-seq和ATAC-seq实验以生物分析仪)与bedtools污水命令使用以下参数:0 - r 125 - l - s。sBLISS-seq库,映射管道生成一个碱基对削减网站。因此,对于可视化的目的,读取扩展75个基点的3′方向匹配最初的阅读顺序。Mm10黑名单地区被过滤掉使用以下命令:bedops -not-element-of 1 (BLACKLIST_BED)gydF4y2Ba60gydF4y2Ba。过滤床文件转换为coverageBED格式使用bedtools genomecov命令使用以下选项:剂量[NORM_FACTOR每个库规模为20米读取芯片,ATAC 20米,10米sBLISS-seq,急忙逃走)和1米bg。最后,bedGraphToBigWig (ucsc-tools / 363)被用来生成有重大影响的文件显示在浏览器使用IGV浏览器追踪整个手稿。gydF4y2Ba
大部分基因表达体外RNA-seq RNA-seq量化gydF4y2Ba
featureCounts包gydF4y2Ba64年gydF4y2Ba被用来计算读入培养神经元RNA-seq数据使用一个自定义过滤注释文件(gencode.v17.annotation。gtffiltered for feature_type=“gene”, gene_type=“protein_coding” and gene_status=“KNOWN”) to obtain read counts along genes for each sample. For differential gene expression analysis, read count tables were TMM-normalized using the EdgeR software analysis package61年gydF4y2Ba。没有任何基因表达在至少三个样本TMM-normalized CPM > 1被进一步分析。轰,limma (edgeR_3.28.1; limma_3.42.2)分析软件包被用来量化(要求FDR-corrected基因差异表达gydF4y2Ba问gydF4y2Ba< 0.01)。RNA-seq配对样本的分析,匹配sBLISS-seq DeSeq2包是用于生成规范化。运行标准DeSeq2管道后,归一化计算生成函数项(dds,规范化= TRUE)gydF4y2Ba59gydF4y2Ba。gydF4y2Ba
基因本体论富集分析gydF4y2Ba
基因本体论(去)富集分析使用gProfiler2 R (v.0.2.0)gydF4y2Ba65年gydF4y2Ba,自定义背景expression-filtered来自所有scRNA-seq神经元细胞类型的基因数据集在这个手稿和罗斯福< 0.05。选择去显示在扩展数据图。gydF4y2Ba5 egydF4y2Ba和丰富的完整列表为每个细胞类型和数据集可以补充表中找到gydF4y2Ba3gydF4y2Ba。gydF4y2Ba
snRNA-seq分析gydF4y2Ba
FASTQ文件使用标准bcl2fastq管道Illumina公司创建的。为每一个核基因表达表条形码生成使用CellRanger 3.0.0管道设计的10倍基因组学。样本去复用,所有gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba或gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba样本合并使用CellRanger aggr函数使用默认参数。数据集被加载到R和分析使用修(v.3)gydF4y2Ba66年gydF4y2Ba和Monocle3gydF4y2Ba67年gydF4y2Ba包。核被移除的数据集是否包含少于500检测到基因,显示超过5%的读取映射到线粒体基因或RNA计数检测水平大于2个标准差的平均值高于他们指定的细胞类型(这可能反映出紧身衣和多胎)。消除潜在的数据集的对比更严格的方式,我们在R DoubletFinder包使用,评估条形码的数据集是最可能基于转录相似性对比不同的集群gydF4y2Ba68年gydF4y2Ba。估计我们使用默认参数和紧身上衣的7%基于指导从10 x基因组铬单细胞3′试剂盒v3用户指南和核的数量在每个反应的车道。gydF4y2Ba
所有核在gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba或gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba样品被认为是一起聚类和降维。2000强变量在核基因被确定使用修的(v.3) FindVariableFeatures函数,是用来执行使用RunPCA函数PCA(使用默认参数)。共享近邻图构建使用FindNeighbors函数(考虑到前30名主成分)和聚类被分配使用FindClusters函数(决议gydF4y2BangydF4y2Ba= 0.02)。下面的标记基因用于细胞类型分配给校长十集群标识:pan-neuronal (gydF4y2BaRbfox3gydF4y2Ba);pan-excitatory神经元(gydF4y2BaSlc17a7gydF4y2Ba);pan-inhibitory神经元(gydF4y2BaGad2gydF4y2Ba);兴奋齿状回神经元(gydF4y2BaProx1gydF4y2Ba和gydF4y2BaC1ql2gydF4y2Ba);兴奋性神经元CA3 (gydF4y2BaCpne4gydF4y2Ba和gydF4y2BaSpock1gydF4y2Ba);兴奋性神经元CA1 (gydF4y2BaMpped1gydF4y2Ba);神经元兴奋性菌丝层(gydF4y2BaTshz2gydF4y2Ba);少突胶质细胞(gydF4y2BaMoggydF4y2Ba和gydF4y2Ba玛格gydF4y2Ba);少突细胞前体细胞(gydF4y2BaPdgfragydF4y2Ba);星形胶质细胞(gydF4y2BaGfapgydF4y2Ba);小胶质细胞(gydF4y2BaCx3cr1gydF4y2Ba和gydF4y2BaC1qcgydF4y2Ba);和内皮细胞(gydF4y2BaCldn5gydF4y2Ba)(扩展数据图。gydF4y2Ba4gydF4y2Ba)。分配每个核感染状况,我们设置一个阈值检测超过8 mCherry或GFP记录在一个给定的核,它代表一个拐点的比率高于背景检测这些成绩单/核的分布,基于已知的和反映预期的感染模式取向AAV2/9病毒用于这些实验。微分CreΔCre-infected细胞之间的基因表达分析在每个集群进行使用Wilcoxon rank-sum测试使用FindMarkers函数(logfc.threshold = 0.25),和重要的基因被定义为那些有一个调整gydF4y2BaPgydF4y2Ba< 0.01。热图生成使用自定义函数写在r .小提琴情节生成使用修VlnPlot函数使用默认参数。gydF4y2Ba
我们注意到,在这两个数据集,在每个神经元集群,根据感染细胞subclustered状态(Cre与ΔCre),这种效果并没有受到病毒转录的表达式,因为所有病毒特性从基因表达矩阵中删除。这可能subclustering反映了Cre-infected细胞无法完全耗尽后产生依赖性活动的基因gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaTip60gydF4y2Ba。在刺激后6 h,这些activity-induced基因中最高度表达基因和神经细胞类型不同,因此在很大程度上造成了主成分降维使用的程控集群。我们使用两个独立的分析软件包,修拉(v.3)和Monocle3,打电话和只考虑重要基因的差异表达基因(调整gydF4y2BaPgydF4y2Ba< 0.01)分析。尽管我们发现基因调节和急性后表达下调gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaTip60gydF4y2Ba损耗,我们关注下游分析表达下调的基因更有可能直接被这个复杂的激活。假定的目标基因的差别,以确保我们的观察对这些不仅仅是由于更高的表达或基因的检测ΔCre-infected组织,我们随机抽样从顶尖的10%的最高表达基因(占目标基因高表达整体)和计算ΔCre - Cre组随机选择的基因差异。我们执行10000次迭代分析,使用随机生成一个样本分布差异的基因。实际观察到的差异(使用NPAS4-NuA4目标基因中确定每个神经元亚型)远远超出这个分布(扩展数据图。gydF4y2Ba5度gydF4y2Ba)。gydF4y2Ba
一般来说,NPAS4诱发细胞类型特异的效应不同组pan-neuronal和基因。许多目标被发现普遍2或3细胞类型,和大约10%的目标是特定于一个细胞类。广泛地说,所有NPAS4目标基因的集合丰富的基因功能信息粘附,细胞间信号和轴突引导,以及一组不同的metabotropic ionotropic神经递质受体亚基。除了捕获已知NPAS4目标基因等gydF4y2BaNptx2gydF4y2Ba,gydF4y2BaPlk2gydF4y2Ba和gydF4y2Ba脑源性神经营养因子gydF4y2Ba1766年,我们发现潜在的新目标NPAS4海马体的分析(补充表gydF4y2Ba3gydF4y2Ba)。gydF4y2Ba
ATAC-seq ChIP-seq峰打电话gydF4y2Ba
ATAC-seq丰富峰值测定使用MACS2 (v.2.1.1)参数转变100 - p e-5——nolambda keep-dup——slocal 10000,如前所述gydF4y2Ba56gydF4y2Ba,gydF4y2Ba69年gydF4y2Ba。ATAC-seq山峰从个人黑名单地区被如前所述gydF4y2Ba60gydF4y2Ba。sBLISS-seq山峰UMI减少床上被称为文件单切的网站被延长的长度测序读(75个基点)。山峰被称为使用MACS2 (v.2.1.1)使用以下参数:峰值MACS2 callpeak——nomodel keep-dup床- p - g毫米1 e-5——格式。可再生的山峰被认为是那些重叠5 8中复制。峰映射到线粒体基因组被移除。最终峰值集扩展500 bp的最大sBLISS-seq峰会上的高峰。峰呼吁芯片样品进行使用MACS2 (macs2/2.1.1)gydF4y2Ba70年gydF4y2Ba使用以下命令macs2 callpeak - t实验(bam) - c(输入bam) - f - p - g的bam毫米1 e-5。gydF4y2Ba
急忙逃走峰打电话gydF4y2Ba
所有调用都使用SEACR_1.1.sh峰值gydF4y2Ba71年gydF4y2Ba。”丛书,H3K27ac CTCF和RAD50急忙逃走数据集,峰值呼吁个人复制使用激增规范化bedgraph文件执行基于片段1 - 1000 bp的长度与以下命令:SEACR_1.1。sh(目标bedgraph][控制bedgraph]规范严格。配对控制样品(免疫球蛋白或敲除控制)补充表中列出gydF4y2Ba2gydF4y2Ba。确定可再生的峰值集,SEACR山峰中发现3的3 H3K27ac复制(0和2 h KA刺激),3的3”丛书(0和2 h KA刺激),复制3的3 CTCF复制(0和2 h KA刺激),3的3 RAD50复制(0 h)和3的4 RAD50复制(2 h KA刺激)交叉使用bedtools / 2.27.1相交的床。高峰在150年英国石油公司合并。NPAS4、ARNT2 EP400, MRE11 ETL4急忙逃走数据集,峰值呼吁个人使用SEACR_1.1进行复制。sh (ref。gydF4y2Ba71年gydF4y2Ba)使用激增规范化bedgraph文件基于片段1 - 1000 bp的长度与以下命令:SEACR_1.1。sh(目标bedgraph][控制bedgraph]规范放松。配对控制样品(免疫球蛋白或敲除控制)补充表中列出gydF4y2Ba2gydF4y2Ba。确定可再生的峰值集,SEACR山峰中发现4的5 NPAS4复制(2 h KA刺激),3的3 NPAS4复制(0 h KA刺激),两块ARNT2复制(2 h KA刺激),两块EP400复制(0和2 h KA刺激;Abcam抗体),两块MRE11复制(0和2 h KA刺激),两块ETL4复制(0 h KA刺激)和3的4 ETL4复制(2 h KA刺激)交叉使用bedtools / 2.27.1相交的床。高峰在150年英国石油公司合并。最后,急忙逃走信号的最大值在100 bp windows为每个峰值计算从激增规范化权贵文件使用自定义脚本。”丛书、ARNT2 EP400, ETL4 MRE11,最后呼吁延长峰值200个基点上游和下游从这个峰maxima生成500个基点峰要求每个因素和时间点。Mm10列入黑名单的地区gydF4y2Ba60gydF4y2Ba被过滤掉使用以下命令:bedops / 2.4.30 -not-element-of 1 [BLACKLIST_BED]。NPAS4山峰被扩展到1 kb,作为上述信息我们发现最大的浓缩(CAGATG)主题和bHLH-PAS主题(CGTG)从峰值最大值1 kb地区扩展。在修订过程中,一个额外的三个复制NPAS4急忙逃走被添加为确认最初的五个复制。这些额外NPAS4急忙逃走复制可以要人GEO提交文件和原始FASTQ文件但没有用于NPAS4峰的分析调用。gydF4y2Ba
峰注释和主题的发现gydF4y2Ba
峰注释作为增强剂,促进剂或其他确定使用annotatePeaks.pl荷马(v.4.9)功能。NPAS4峰值注释进行区域扩展1 kb的峰值最大,随着这些地区最丰富NPAS4图案。安全系数峰值注释进行区域扩展从峰值最大值500个基点。积极监管元素被定义为可再生的ATAC-seq联盟(3的3复制)和H3K27ac山峰(3 3复制)扩展500个基点从监管的最大ATAC-seq信号元素。增强剂被定义为基因间的联盟和intronic结合位点注释。找到丰富图案,每个峰值提取序列潜在使用bedtools / 2.27.1 getfasta命令。相同长度的序列(1000个基点NPAS4和MRE11 sBLISS-seq 500个基点)处理使用Meme-ChIP (gydF4y2Bahttps://meme-suite.org/meme/tools/meme-chipgydF4y2Ba)gydF4y2Ba72年gydF4y2Ba和测试的主题背景(HOCOMOCO v11)意义的报道gydF4y2BaEgydF4y2Ba价值。gydF4y2Ba
峰重叠gydF4y2Ba
确定NPAS4重叠和附加因素,NPAS4峰会被扩展为1 kb。峰重叠测定使用bedtools / 2.27.1相交床允许至少1 bp重叠。生成网站NPAS4不重叠的信号和安全系数,NPAS4和安全系数峰会都扩展为1 kb。NPAS4-bound网站(FOS)提交生成使用bedtools / 2.27.1相交床- v选项来生成峰没有NPAS4,反之亦然。gydF4y2Ba
代的固定线路情节和总情节gydF4y2Ba
固定线路图生成使用荷马(v4.9) annotatePeaks。pl (PEAK_BED) mm10 - d [INPUT_TAG_DIRS]造2000 -ghist嘘25 -noann -nogene。固定线情节从标签生成目录包含合并bam信息复制。总情节生成使用荷马(v4.9) annotatePeaks。除非另有pl函数使用默认参数嘘25日指出的传奇。信号强度是绘制使用自定义脚本R (3.6.1)。总情节显示平均信号在复制s.e.m.绘制。总情节的统计分析,提取信号的所有复制整个窗口中指定图使用荷马(v4.9) ' s annotatePeaks传说。pl (PEAK_BED) mm10 - d (INPUT_TAG_DIRS)与标准化1000万读荷马的默认阅读深度。信号平均在所有复制,Wilcoxon rank-sum测试被用来比较不同条件之间的平均信号在指定的窗口。gydF4y2Ba
海马体神经元监管环境的识别gydF4y2Ba
定义一组监管元素在海马神经元组织样本,我们使用ATAC-seq (gydF4y2BaCamkIIagydF4y2Ba+gydF4y2Ba海马神经元),加上积极的组蛋白修饰H3K27ac急忙逃走,描述本构和activity-responsive基因组监管海马的景观元素。我们在基底异形海马组织状态和2 h后的神经元活动同步感应低剂量KA管理。可再生的ATAC-seq山峰被定义为MACS2山峰中确定所有3 3复制/时间点。网站如果和刺激样本连接和合并生成所有可能的列表ATAC-seq山峰在任何刺激条件。可再生的H3K27ac山峰被定义为SEACR山峰中确定所有3 3复制/时间点。网站如果和刺激样本连接和合并生成所有可能的列表H3K27ac山峰在任何刺激条件。最后的景观元素包含179841个元素,定义为可再生的联盟ATAC-seq和H3K27ac峰急忙逃走,ATAC-seq数据集在所有时间点后删除mm10黑名单地区。注意,删除黑名单进行H3K27ac和ATAC-seq网站的结合。产生相同大小的区域,我们确定最大ATAC-seq信号在每个监管元素和扩展这个最大的地区500个基点染色质易访问性峰会。gydF4y2Ba
发现诱导ATAC-seq H3K27ac山峰,我们进行了一次微分表达式分析使用DeSeq2 (v.DESeq2_1.26.0)gydF4y2Ba59gydF4y2Ba地区,非零项的至少两个样品。我们定义“诱导元素”在这个设置为这些网站展示增加ATAC信号(双重的增加;调整gydF4y2BaPgydF4y2Ba< 0.05 DeSeq2;gydF4y2BaPgydF4y2Ba价值观决定了测试的褶皱变化阈值2)和/或增加H3K27ac急忙逃走信号(增长了1.5倍;调整gydF4y2BaPgydF4y2Ba< 0.05 DeSeq2;gydF4y2BaPgydF4y2Ba价值观决定了测试的褶皱变化阈值1.5)刺激后(11114网站)。监管元素提供了补充表gydF4y2Ba4gydF4y2Ba。注意,没有达到阈值的元素截止至少两个非零项的样品将不会被包括在各自DeSeq2分析选项卡在这个表。gydF4y2Ba
急忙逃走和sBLISS-seq信号的量化基因调控元素gydF4y2Ba
量化转录因子结合强度、软件包荷马(v4.9)首先用于创建标记目录复制每个因素对于一个给定的时间点与命令makeTagDirectory(输入床或BAM)。sBLISS-seq样品、床文件来自先前描述的管道gydF4y2Ba30.gydF4y2Ba扩大,这样每个UMI在每个位置是单独计算。sBLISS-seq样本,len 0标记添加到创建标记目录占这一事实sBLISS-seq映射生成床上单碱基对减少网站的文件。信号提取/套监管区域使用以下命令:annotatePeaks。pl(床文件)mm10造-noann。转录因子(NPAS4 MRE11、ETL4 EP400,安全系数和RAD50),信号read-depth-normalized使用荷马(v4.9)的默认正常化1000万读。绘制各种基因的信号特性的函数NPAS4绑定力量,我们排在所有监管元素数据集的定义(见上图179841 ATAC / H3K27ac海马体中的元素)根据NPAS4 IgG-normalized急忙逃走信号和区域分割成四分位数在此基础上排名。我们确定NPAS4-normalized信号在每个站点的基础上除以总信号NPAS4急忙逃走(合并NPAS4复制1 - 5)的总信号免疫球蛋白(合并复制f)在任何给定的网站在我们的监管环境。NPAS4第四季度(高)确定网站的网站SEACR-defined峰的重叠NPAS4,最高四分位数的NPAS4 IgG-normalized急忙逃走的信号。NPAS4 Q1(低)网站没有SEACR-defined高峰,在最低四分位数的NPAS4 IgG-normalized急忙逃走的信号。gydF4y2Ba
比较γH2AX, ATAC-seq、H3K27ac MRE11和sBLISS-seq信号在179841中定义的集合我们的监管环境在时间点和条件(例如,不同基因型),提取原始读计数用荷马(v4.9) annotatePeaks。pl函数使用下面的命令:annotatePeaks。pl(床文件)mm10造给-noann -noadj。sBLISS-seq信号,len 0参数只包含量化减少站点结束(1 bp)和防止阅读转变基于估计片段大小。原始信号计数在运行前r .进口DeSeq2 (v.1.26.0),较低的地区数量被排除在外:ATAC-seq, H3K27acγH2AX,我们需要非零项至少在两个样本。sBLISS-seq(野生型时间进程和Cre和ΔCre数据集),这比ATAC-seq稀疏的,H3K27ac急忙逃走,γH2AX,我们只消除零计数所有的地区样本。DeSeq2-normalized计数使用DeSeq2函数生成计数(dds,规范化= TRUE)gydF4y2Ba59gydF4y2Ba我们的监管区域设置在所有条件(0和2 h ATAC KA, H3K27acγH2AX和0,2、10 h sBLISS-seq KA)。我们为众多的野生型观测到批处理的效果时间样本。样本来自所有时间点都包含在每一批。然而,去除这些影响计算,我们在DeSeq2包括批处理设计使用下面的命令:DESeqDataSetFromMatrix(设计~ Seq_Batch +条件)。此外,当出口标准化方面,我们使用了limma (3.42.2) limma:: removeBatchEffect(计数(dds对象,规范化= TRUE)。批次处理样品补充表中可以找到gydF4y2Ba2gydF4y2Ba。信号计数的箱线图绘制ATAC-seq纸,H3K27ac,γH2AX和野生型sBLISS-seq时间课程是基于DeSeq2-normalized值平均在所有复制对于一个给定的高峰。gydF4y2Ba
处理的CreΔCre数据集,DeSeq2正常化计数进行在每个基因型(即原始计数Cre与ΔCre数据集gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba从Cre独立规范化和ΔCre野生型数据集)。我们选择这个设计,因为这些实验进行单独的时候和比较了Cre和ΔCre之间在每个基因型而不是在基因型。占变化sBLISS-seq数据集产生很低的细胞数量Cre与ΔCre数据集,复制受感染动物组成的独立并不平均每个峰上,而是所有复制信息保留在策划信号(无花果。gydF4y2Ba5 bgydF4y2Ba和扩展数据图。gydF4y2Ba12个模拟gydF4y2Ba)。gydF4y2Ba
量化独特的整个基因组gydF4y2Ba
输入读取整个基因组比较优惠,downsampled最低数量的读取了所有样品相比(NPAS4 Cre和ΔCre以及野生型Cre和ΔCre: 21036891读;TIP60 Cre与ΔCre 14262877读)。然后我们每个样本中量化的umi总数,绘制在图。gydF4y2Ba5度gydF4y2Ba和扩展数据图。gydF4y2Ba12 egydF4y2Ba。注意,我们量化信号在不同监管元素显示在所有其他人物,曾经DESeq2-normalized计数,我们没有downsample输入运行DESeq2前。DESeq2算法占测序深度的差异规范化管道。gydF4y2Ba
量化的突变积累gydF4y2Ba
Debarcer输出(bamPositionComposition)表得到的包Debarcer_v.0.3.1 (gydF4y2Bahttps://github.com/oicr-gsi/debarcer/releases/tag/v0.3.1gydF4y2Ba)gydF4y2Ba38gydF4y2Ba。这些表文档共识十家庭数量(即十组读取相同的UMI所有十读取显示相同的基本变化(或缺乏))在给定的扩增子为每个基地。这些表的总数也算UMI家庭匹配参考基因组或显示变化的参考。包括一个给定的扩增子在我们的分析中,我们要求一致的平均数量十家庭所有基地扩增子> 100。引物信息池和扩增子包括在最终的分析中,看到补充表gydF4y2Ba5gydF4y2Ba。gydF4y2Ba
在R使用脚本,我们计算一个给定的扩增子的突变频率总计从参考和基础变化的总和除以总数基地评估的扩增子(也就是说,共识深度的和十个家庭在所有基地在我们的表)。第一个22个碱基的序列,其中包含的区域底漆放大免疫印迹,被排除在分析避免错误在底漆生产复杂的结果。这个计算了单个突变率为给定的扩增子在一个给定的样本。总变异率包括插入和删除和单核苷酸的变化。计算选择点突变的频率,我们统计的总数选择变化(C > / (G > T)除以总数量的扩增子中给定的基地。因为它是不可能知道链发生了突变,互补碱基变化倒塌成一个单一的类别(例如,C > T结合G >)。插入和删除频率也计算作为一个单独的类别。我们也计算每个扩增子规范化突变率我们每个动物的总变异率除以平均总突变频率在年轻的老鼠。梯度样品老化,野生型老鼠岁3个月大的时候被认为是年轻,12个月大的时候被认为是中年和汽车个月大的时候被认为是老了。极端异常点的归一化突变频率和非规范化频率必须执行哪些操作是删除所有样品使用溃败的测试在0.1%信心(无花果。gydF4y2Ba5 egydF4y2Ba和扩展数据图。gydF4y2Ba13克gydF4y2Ba)。离群值去除突变和统计测试样本在棱镜(v.8.4.2)。gydF4y2Ba
报告总结gydF4y2Ba
进一步研究信息设计是可用的gydF4y2Ba自然投资组合报告总结gydF4y2Ba与这篇文章有关。gydF4y2Ba
数据可用性gydF4y2Ba
所有测序数据被存入的GEO加入号码gydF4y2BaGSE175965gydF4y2Ba。质谱数据被存入ProteomeXchange财团通过骄傲数据库加入号码gydF4y2BaPXD038718gydF4y2Ba。原始凝胶图像提供了补充图。gydF4y2Ba1gydF4y2Ba。gydF4y2Ba源数据gydF4y2Ba本文提供的。gydF4y2Ba
代码的可用性gydF4y2Ba
本研究中使用自定义代码可用。gydF4y2Ba
引用gydF4y2Ba
狂吠,e . l . &格林伯格·m·e·Activity-regulated转录:桥接神经活动和行为之间的差距。gydF4y2Ba神经元gydF4y2BaOne hundred.gydF4y2Ba,330 - 348 (2018)。gydF4y2Ba
Suberbielle、大肠等。生理大脑活动导致神经元DNA双链断裂,由amyloid-β恶化。gydF4y2BaNat。>。gydF4y2Ba16gydF4y2Ba,613 - 621 (2013)。gydF4y2Ba
Madabhushi, r . et al . Activity-induced DNA断裂控制神经早反应基因的表达。gydF4y2Ba细胞gydF4y2Ba161年gydF4y2Ba,1592 - 1605 (2015)。gydF4y2Ba
Delint-Ramirez, et al .钙调磷酸酶脱去磷酸拓扑异构酶IIβ和调节neuronal-activity-induced DNA断裂的形成。gydF4y2Ba摩尔。细胞gydF4y2Ba82年gydF4y2Ba,3794 - 3809。e8 (2022)。gydF4y2Ba
Crowe, s . L。,Movsesyan, V. A., Jorgensen, T. J. & Kondratyev, A. Rapid phosphorylation of histone H2A.X following ionotropic glutamate receptor activation.欧元。j . >。gydF4y2Ba23gydF4y2Ba,2351 - 2361 (2006)。gydF4y2Ba
狂吠,e . l . et al .双向perisomatic抑制可塑性”丛书的神经网络。gydF4y2Ba自然gydF4y2Ba590年gydF4y2Ba,115 - 121 (2021)。gydF4y2Ba
红枫叶片,b . L。沙玛,N。,Browne, H. A., Trepman, A. Z. & Greenberg, M. E. The activity-dependent transcription factor NPAS4 regulates domain-specific inhibition.自然gydF4y2Ba503年gydF4y2Ba,121 - 125 (2013)。gydF4y2Ba
陆,t . et al .基因调控和DNA损伤人类大脑老化。gydF4y2Ba自然gydF4y2Ba429年gydF4y2Ba,883 - 891 (2004)。gydF4y2Ba
群,h . et al .转录延伸需要DNA断路感应信号。gydF4y2BaCommun Nat。gydF4y2Ba6gydF4y2Ba10191 (2015)。gydF4y2Ba
桔多琪b . g . et al .拓扑异构酶IIbeta-mediated dsDNA打破调控转录所需。gydF4y2Ba科学gydF4y2Ba312年gydF4y2Ba,1798 - 1802 (2006)。gydF4y2Ba
Iyama t & Wilson, d . m . 3日在分裂和非区分细胞DNA修复机制。gydF4y2BaDNA修复(Amst)。gydF4y2Ba12gydF4y2Ba,620 - 636 (2013)。gydF4y2Ba
Lodato, m . a . et al .衰老和神经退行性变是人类神经元与变异单增加有关。gydF4y2Ba科学gydF4y2Ba359年gydF4y2Ba,555 - 559 (2018)。gydF4y2Ba
舒马赫,B。Pothof, J。,Vijg, J. & Hoeijmakers, J. H. J. The central role of DNA damage in the ageing process.自然gydF4y2Ba592年gydF4y2Ba,695 - 703 (2021)。gydF4y2Ba
林,y . et al .依赖性活动的监管由Npas4抑制性突触的发展。gydF4y2Ba自然gydF4y2Ba455年gydF4y2Ba,1198 - 1204 (2008)。gydF4y2Ba
Doyon y &象牙海岸,j .高度保守的和多功能NuA4帽子复杂。gydF4y2Ba咕咕叫。当今。麝猫。Dev。gydF4y2Ba14gydF4y2Ba,147 - 154 (2004)。gydF4y2Ba
Galarneau, l . et al .多个链接NuA4组蛋白乙酰转移酶之间复杂的转录和表观遗传控制。gydF4y2Ba摩尔。细胞gydF4y2Ba5gydF4y2Ba,927 - 937 (2000)。gydF4y2Ba
Allard, s . et al . NuA4必不可少的适配器/转录组蛋白H4乙酰转移酶复杂包含Esa1p ATM-related代数余子式Tra1p。gydF4y2BaEMBO J。gydF4y2Ba18gydF4y2Ba,5108 - 5119 (1999)。gydF4y2Ba
艾伦大脑地图,细胞类型数据库:RNA-Seq数据。gydF4y2Bahttps://celltypes.brain-map.org/rnaseq/human_m1_10xgydF4y2Ba(2020)。gydF4y2Ba
弧拱,p . j . & Henikoff美国一个有效的目标核酸酶的高分辨率的映射策略的DNA结合位点。gydF4y2BaeLifegydF4y2Ba6gydF4y2Bae21856 (2017)。gydF4y2Ba
普拉丹,s . k . et al . EP400存款H3.3启动子和增强子在基因激活。gydF4y2Ba摩尔。细胞gydF4y2Ba61年gydF4y2Ba27-38 (2016)。gydF4y2Ba
鸟,a . w . et al .乙酰化组蛋白H4的Esa1需要DNA双链断裂修复。gydF4y2Ba自然gydF4y2Ba419年gydF4y2Ba,411 - 415 (2002)。gydF4y2Ba
Ikura, t . et al . TIP60组蛋白乙酰基转移酶复杂参与DNA修复和细胞凋亡。gydF4y2Ba细胞gydF4y2Ba102年gydF4y2Ba,463 - 473 (2000)。gydF4y2Ba
太阳,y . et al .组蛋白H3甲基化DNA损伤检测肿瘤抑制基因的激活链接Tip60。gydF4y2BaNat,细胞生物。gydF4y2Ba11gydF4y2Ba,1376 - 1382 (2009)。gydF4y2Ba
库施,t . et al。由需要Tip60选择性乙酰化组蛋白变体交换DNA损伤。gydF4y2Ba科学gydF4y2Ba306年gydF4y2Ba,2084 - 2087 (2004)。gydF4y2Ba
唐,j . et al .乙酰化作用限制了53 bp1与受损的染色质促进同源重组。gydF4y2BaNat。结构。摩尔。杂志。gydF4y2Ba20.gydF4y2Ba,317 - 325 (2013)。gydF4y2Ba
Jacquet, k . et al . TIP60复杂调节二价染色质识别通过直接H4K20me绑定和53 bp1 H2AK15乙酰化作用。gydF4y2Ba摩尔。细胞gydF4y2Ba62年gydF4y2Ba,409 - 421 (2016)。gydF4y2Ba
Brigidi g . s . et al .基因组解码的神经元去极化stimulus-specific NPAS4形成。gydF4y2Ba细胞gydF4y2Ba179年gydF4y2Ba,373 - 391。e27(2019).
沙玛:et al . ARNT2曲调依赖性活动通过NCoR2-nediated压迫和NPAS4-mediated激活基因表达。gydF4y2Ba神经元gydF4y2Ba102年gydF4y2Ba,390 - 406。e9 (2019)。gydF4y2Ba
Dellino, g . i . et al .发布暂停RNA聚合酶II在特定位点支持DNA double-strand-break形成和促进癌症易位。gydF4y2BaNat,麝猫。gydF4y2Ba51gydF4y2Ba,1011 - 1023 (2019)。gydF4y2Ba
Bouwman, b . a . m . et al .全基因组检测DNA双链断裂的悬浮幸福。gydF4y2BaProtoc Nat。gydF4y2Ba15gydF4y2Ba,3894 - 3941 (2020)。gydF4y2Ba
婆婆,a . et al .基因组组织驱动染色体脆弱。gydF4y2Ba细胞gydF4y2Ba170年gydF4y2Ba,507 - 521。e18(2017).
吴,w . et al .神经增强剂是DNA单链断裂修复的热点。gydF4y2Ba自然gydF4y2Ba593年gydF4y2Ba,440 - 444 (2021)。gydF4y2Ba
Paull, t . t . 20年Mre11生物学:看不到尽头。gydF4y2Ba摩尔。细胞gydF4y2Ba71年gydF4y2Ba,419 - 427 (2018)。gydF4y2Ba
阿花,n . n . et al . Mre11至关重要的致命的拓扑异构酶2共价乳沟复合物。gydF4y2Ba摩尔。细胞gydF4y2Ba64年gydF4y2Ba1010 (2016)。gydF4y2Ba
Wienert, b . et al .公正检测CRISPR使用DISCOVER-Seq不相干的体内。gydF4y2Ba科学gydF4y2Ba364年gydF4y2Ba,286 - 289 (2019)。gydF4y2Ba
Salifou, k . et al . Chromatin-associated MRN复杂保护高度抄录基因从基因组不稳定性。gydF4y2Ba科学。睡觉。gydF4y2Ba7gydF4y2Baeabb2947 (2021)。gydF4y2Ba
Loonstra, a . et al .生长抑制和在哺乳动物细胞Cre重组酶引起的DNA损伤。gydF4y2BaProc。《科学。美国gydF4y2Ba98年gydF4y2Ba,9209 - 9214 (2001)。gydF4y2Ba
Stahlberg, et al。简单的多路复用pcr进行超灵敏检测突变的DNA条码技术的下一代测序。gydF4y2BaProtoc Nat。gydF4y2Ba12gydF4y2Ba,664 - 682 (2017)。gydF4y2Ba
Ooe, N。,Motonaga, K., Kobayashi, K., Saito, K. & Kaneko, H. Functional characterization of basic helix-loop-helix-PAS type transcription factor NXF in vivo: putative involvement in an “on demand” neuroprotection system.生物。化学。gydF4y2Ba284年gydF4y2Ba,1057 - 1063 (2009)。gydF4y2Ba
里德·d·a . et al .核苷模拟地图整合基因组修复网站postmitotic人类神经元。gydF4y2Ba科学gydF4y2Ba372年gydF4y2Ba,91 - 94 (2021)。gydF4y2Ba
陈,p . B。,Chen, H. V., Acharya, D., Rando, O. J. & Fazzio, T. G. R loops regulate promoter-proximal chromatin architecture and cellular differentiation.Nat。结构。摩尔。杂志。gydF4y2Ba22gydF4y2Ba,999 - 1007 (2015)。gydF4y2Ba
沈,y . et al . RNA-driven基因变化在细菌和人类细胞。gydF4y2BaMutat。Res。gydF4y2Ba717年gydF4y2Ba,91 - 98 (2011)。gydF4y2Ba
Keskin是h . et al . Transcript-RNA-templated DNA重组和修复。gydF4y2Ba自然gydF4y2Ba515年gydF4y2Ba,436 - 439 (2014)。gydF4y2Ba
查,m . h . et al . Whole-exome测序和纯合性分析表明depolarization-regulated神经元基因在孤独症。gydF4y2Ba公共科学图书馆麝猫。gydF4y2Ba8gydF4y2Bae1002635 (2012)。gydF4y2Ba
亨伯特,j . et al .新创KAT5变异原因和可辨认的面部先天性畸形综合征,小脑萎缩,睡眠障碍和癫痫。gydF4y2Ba点。j .的嗡嗡声。麝猫。gydF4y2Ba107年gydF4y2Ba,564 - 574 (2020)。gydF4y2Ba
贝尔,s . et al .突变gydF4y2BaACTL6BgydF4y2Ba导致神经发育缺陷和癫痫,导致人类神经元树突的损失。gydF4y2Ba点。j .的嗡嗡声。麝猫。gydF4y2Ba104年gydF4y2Ba,815 - 834 (2019)。gydF4y2Ba
田,x et al . SIRT6负责更高效长寿物种的DNA双链断裂修复。gydF4y2Ba细胞gydF4y2Ba177年gydF4y2Ba,622 - 638。e22(2019).
Zullo, j . m . et al .寿命由神经调节励磁和休息。gydF4y2Ba自然gydF4y2Ba574年gydF4y2Ba,359 - 364 (2019)。gydF4y2Ba
费舍尔,j . b . et al .损耗的Tip60体内心肌细胞肌细胞密度增加,其次是心脏功能障碍、肌细胞影响和杀伤力。gydF4y2Ba《公共科学图书馆•综合》gydF4y2Ba11gydF4y2Bae0164855 (2016)。gydF4y2Ba
陈,p . b . et al . Hdac6调节Tip60-p400功能干细胞。gydF4y2BaeLifegydF4y2Ba2gydF4y2Bae01557 (2013)。gydF4y2Ba
中方,J。,Stoneham, T., Spehalski, E. & Ferguson, D. O. Mre11 regulates CtIP-dependent double-strand break repair by interaction with CDK2.Nat。结构。摩尔。杂志。gydF4y2Ba19gydF4y2Ba,246 - 252 (2012)。gydF4y2Ba
中方,j . et al . Mre11核酸酶活性在DNA修复有重要作用,不同于ATM激活基因稳定。gydF4y2Ba细胞gydF4y2Ba135年gydF4y2Ba,85 - 96 (2008)。gydF4y2Ba
密苏里州,a . et al。哺乳动物大脑的神经元多样性外遗传性签名。gydF4y2Ba神经元gydF4y2Ba86年gydF4y2Ba,1369 - 1384 (2015)。gydF4y2Ba
戴瑟罗斯,K。,Bito, H. & Tsien, R. W. Signaling from synapse to nucleus: postsynaptic CREB phosphorylation during multiple forms of hippocampal synaptic plasticity.神经元gydF4y2Ba16gydF4y2Ba,89 - 101 (1996)。gydF4y2Ba
Erbel-Sieler, c . et al .小鼠异常行为和监管缺乏NPAS1 NPAS3转录因子。gydF4y2BaProc。《科学。美国gydF4y2Ba101年gydF4y2Ba,13648 - 13653 (2004)。gydF4y2Ba
Buenrostro, j . D。、Giresi p·G。、Zaba l . C。,Chang, H. Y. & Greenleaf, W. J. Transposition of native chromatin for fast and sensitive epigenomic profiling of open chromatin, DNA-binding proteins and nucleosome position.Nat方法。gydF4y2Ba10gydF4y2Ba,1213 - 1218 (2013)。gydF4y2Ba
海纳,s . j . & Fazzio t . g .高分辨率染色质分析使用急忙逃走。gydF4y2Ba咕咕叫。Protoc。摩尔。杂志。gydF4y2Ba126年gydF4y2Ba,e85燃料(2019)。gydF4y2Ba
Wong N。,John, S., Nussenzweig, A. & Canela, A. END-seq: an unbiased, high-resolution, and genome-wide approach to map DNA double-strand breaks and resection in human cells.摩尔。生物方法。gydF4y2Ba2153年gydF4y2Ba9-31 (2021)。gydF4y2Ba
爱,我。,Huber, W. & Anders, S. Moderated estimation of fold change and dispersion for RNA-seq data with DESeq2.基因组医学杂志。gydF4y2Ba15gydF4y2Ba550 (2014)。gydF4y2Ba
财团,e . p .综合性百科全书在人类基因组中DNA的元素。gydF4y2Ba自然gydF4y2Ba489年gydF4y2Ba57 - 74 (2012)。gydF4y2Ba
罗宾逊,m D。,McCarthy, D. J. & Smyth, G. K. edgeR: a Bioconductor package for differential expression analysis of digital gene expression data.生物信息学gydF4y2Ba26gydF4y2Ba,139 - 140 (2010)。gydF4y2Ba
博尔格、a . M。,Lohse, M. & Usadel, B. Trimmomatic: a flexible trimmer for Illumina sequence data.生物信息学gydF4y2Ba30.gydF4y2Ba,2114 - 2120 (2014)。gydF4y2Ba
弧拱,p . J。,Henikoff, J. G. & Henikoff, S. Targeted in situ genome-wide profiling with high efficiency for low cell numbers.Protoc Nat。gydF4y2Ba13克ydF4y2Ba,1006 - 1019 (2018)。gydF4y2Ba
廖,Y。,Smyth, G. K. & Shi, W. featureCounts: an efficient general purpose program for assigning sequence reads to genomic features.生物信息学gydF4y2Ba30.gydF4y2Ba,923 - 930 (2014)。gydF4y2Ba
Kolberg, L。,R一个udvere, U., Kuzmin, I., Vilo, J. & Peterson, H. gprofiler2—an R package for gene list functional enrichment analysis and namespace conversion toolset g:Profiler.F1000ResgydF4y2Bahttps://doi.org/10.12688/f1000research.24956.2gydF4y2Ba(2020)。gydF4y2Ba
斯图亚特,t . et al .单细胞数据综合集成。gydF4y2Ba细胞gydF4y2Ba177年gydF4y2Ba,1888 - 1902。e21 (2019)。gydF4y2Ba
杰尔et al。细胞命运决定的动力学和监管者pseudotemporal排序显示的单个细胞。gydF4y2Ba生物科技Nat。》。gydF4y2Ba32gydF4y2Ba,381 - 386 (2014)。gydF4y2Ba
麦金尼斯,c . S。,Murrow, L. M. & Gartner, Z. J. DoubletFinder: doublet detection in single-cell RNA sequencing data using artificial nearest neighbors.电池系统gydF4y2Ba8gydF4y2Ba,329 - 337。e4 (2019)。gydF4y2Ba
Buenrostro, j . D。吴,B。,Chang, H. Y. & Greenleaf, W. J. ATAC-seq: a method for assaying chromatin accessibility genome-wide.咕咕叫。Protoc。摩尔。杂志。gydF4y2Ba109年gydF4y2Ba21.29.1-21.29.9 (2015)。gydF4y2Ba
张y等。基于模型分析ChIP-Seq (mac)。gydF4y2Ba基因组医学杂志。gydF4y2Ba9gydF4y2BaR137 (2008)。gydF4y2Ba
密尔兹,m . P。,Tenenbaum, D. & Henikoff, S. Peak calling by Sparse Enrichment Analysis for CUT&RUN chromatin profiling.表观遗传学染色质gydF4y2Ba12gydF4y2Ba42 (2019)。gydF4y2Ba
Machanick p &贝利,t . l . MEME-ChIP:主题分析DNA的大型数据集。gydF4y2Ba生物信息学gydF4y2Ba27gydF4y2Ba,1696 - 1697 (2011)。gydF4y2Ba
确认gydF4y2Ba
我们感谢所有格林伯格实验室成员有价值的输入;年代。号与生物化学实验寻求建议和帮助;J。湖的gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠;T。Fazzio为gydF4y2BaTip60-H3FgydF4y2Ba老鼠;D。弗格森对gydF4y2BaMre11gydF4y2Bafl / flgydF4y2Ba老鼠;N。Crosetto和B。Bouwman访问sBLISS-seq协议;T。戈弗雷的建议扩增子库生产;T。Vierbuchen, J。绿色,J。Tycko和。岩手稿评论和有用的洞察力在整个课程的项目; and J. Luquette for advice and assistance on mutational analysis. E.A.P. acknowledges a Good Ventures Life Sciences Research Fellowship and K99 from NIA 1K99AG064042-01A1. D.T.G. was supported by a Harvard Department of Neurobiology Graduate fellowship. C.P.D. was supported by NIH fellowships T32-NS007473 and F32-NS112455. E.-L.Y. was supported by a Stuart H. Q. and Victoria Quan fellowship, a Harvard Department of Neurobiology Graduate fellowship and an Aramont Fund for Emerging Science Research fellowship. M.A.N. acknowledges NIH fellowship T32GM007753. E.E.D. was supported by the Damon Runyon Cancer Research Foundation and a Warren Alpert Distinguished Scholar Fellowship Award. Histology imaging was performed through the Harvard Medical School Neuro Imaging Facility (NINDS P30 Core Center grant number NS072030). This work was supported by R01 NS028829, the Lefler Faculty Small Grant to M.E.G. and the Carol and Gene Ludwig Family Foundation through the Ludwig Neurodegenerative Disease Seed Grants Program at Harvard Medical School. The Greenberg Laboratory is supported by the Allen Discovery Center Program, a Paul G. Allen Frontiers Group advised programme of the Paul G. Allen Family Foundation and the Tang-Yang Autism Center at Harvard Medical School.
作者信息gydF4y2Ba
作者和联系gydF4y2Ba
贡献gydF4y2Ba
E.A.P.,D。T。G. and M.E.G. conceived and designed the study and wrote the manuscript. E.A.P. and D.T.G. designed, executed and analysed the majority of experiments performed in the paper. Specifically, E.A.P. designed and characterized theNpas4-FHgydF4y2Ba和gydF4y2BaArnt2-FHgydF4y2Ba行,执行和分析生物化学、质谱分析、RNA-seq, ATAC-seq,急忙逃走,ChIP-seq, sBLISS-seq,寿命,流式细胞仪分选,扩增子和突变库的准备和分析。D.T.G.执行和生物化学分析,质谱,RNA-seq, snRNA-seq, sBLISS-seq, END-seq,扩增子和突变库生产、立体定位手术和辅助电生理学实验。A.T.L.进行电生理学实验。中一段进行生化检测、RNA-seq和协助扩增子库生产。N.P.进行生化检测,RNA-seq和扩增子图书馆协助生产。D.A.H.执行额外的突变分析。E.-L.Y.每日成本执行的安全系数和H3K27ac急忙逃走实验。每日成本提供代码急忙逃走的数据分析。I.R.V.协助sBLISS-seq库生产。M.A.N.辅助设计和生产的gydF4y2BaNpas4-FHgydF4y2Ba和gydF4y2BaArnt2-FHgydF4y2Ba标记线。E.L.执行安全系数和EGR1 immunoprecipitation-mass谱实验。E.E.D.协助snRNA-seq数据的分析。E.C.G.导致项目方向和手稿写作。C.J.W.提供知识指导和试剂NPAS4复合物的生物净化。B.L.S.知识提供电生理学实验指导。gydF4y2Ba
相应的作者gydF4y2Ba
道德声明gydF4y2Ba
相互竞争的利益gydF4y2Ba
作者宣称没有利益冲突。gydF4y2Ba
同行评审gydF4y2Ba
同行审查的信息gydF4y2Ba
自然gydF4y2Ba由于Jan Hoeijmakers伊兰Mukamel,另,匿名的,审稿人(s)为他们的贡献的同行评审工作。gydF4y2Ba同行审查报告gydF4y2Ba是可用的。gydF4y2Ba
额外的信息gydF4y2Ba
出版商′年代注意gydF4y2Ba施普林格自然保持中立在发表关于司法主权地图和所属机构。gydF4y2Ba
扩展数据数据和表gydF4y2Ba
扩展数据图1与NuA4 NPAS4形式复杂的大脑区域。gydF4y2Ba
从KA-stimulated老鼠的海马。溶菌产物,分离的分子量(MW)使用凝胶过滤和non-denaturing尺寸排阻色谱法。西方墨点法对不同MW NPAS4分数确认NPAS4驻留在一个高MW复杂~ 1 MDa的大小达到顶峰。代表图像从3实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。b。国旗HA抗原决定基的序列验证标签附加到的糖gydF4y2BaNpas4gydF4y2Ba或gydF4y2BaArnt2gydF4y2BaP0或F1代gydF4y2BaNpas4-FHgydF4y2Ba或gydF4y2BaArnt2-FHgydF4y2Ba老鼠。NPAS4 c。左:免疫组织化学和HA抗体染色的海马gydF4y2BaNpas4-FHgydF4y2Ba老鼠,6 h丰富的环境。酒吧规模:100μm。右:验证gydF4y2BaArnt2-FHgydF4y2Ba兄弟鼠标线在CA1免疫组织化学。25μm比例尺。代表图像从3实验。d。验证通过免疫印迹NPAS4和NPAS4-FH相同的感应膜depolarization-induced钙信号的动力学和特异性。刺激培养皮层神经元,55毫米氯化钾是申请指定的时间点。代表图像从一个实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。e。确认NPAS4-FH表达的免疫印迹和标记免疫沉淀反应(IP)从野生型或培养皮层神经元gydF4y2BaNpas4-FHgydF4y2Ba老鼠。代表图像从一个实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。f。确认通过anti-Flag免疫沉淀反应(IP)和免疫印迹NPAS4-NuA4也组装2 h后的视觉皮层光刺激。代表图像从2实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。g。实验图详细说明甘油梯度分离和免疫沉淀反应完整NPAS4-NuA4复合物的高分子量(MW)分数。h。免疫印迹NPAS4-FH甘油梯度分数的老鼠大脑皮层溶解产物隔离兆瓦。NPAS4迁移在高MW分数连同TRRAP NuA4组件,EP400, DMAP1。代表图像从3实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。我。NPAS4-NuA4互动的相互验证通过标记免疫沉淀反应和免疫印迹从野生型皮质溶解产物MW分数高,gydF4y2BaNpas4-Flag-HA (Npas4-FH)gydF4y2Ba,gydF4y2BaTip60-Flag (Tip60-F)gydF4y2Ba老鼠。代表图像从2实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。j。NPAS4-NuA4互动的相互验证通过标记免疫沉淀反应和免疫印迹MW低分数的皮质溶解产物从野生型,gydF4y2BaNpas4-Flag-HA (Npas4-FH)gydF4y2Ba,gydF4y2BaTip60-Flag (Tip60-F)gydF4y2Ba老鼠。代表图像从2实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。gydF4y2Ba
扩展数据图2的验证NPAS4-NuA4交互和神经元特异性。gydF4y2Ba
,确认NPAS4-NuA4交互可以通过相互观察国旗IP和免疫印迹海马的野生型,gydF4y2BaNpas4-FHgydF4y2Ba,gydF4y2BaTip60-Flag (TIP60-F)gydF4y2Ba老鼠。代表图像从2实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。b。Anti-Flag IP的海马gydF4y2BaTip60-Flag (TIP60-F)gydF4y2Ba老鼠如果大脑和2 h后KA刺激。NuA4复杂的免疫印迹表明组件交互的基底(0 h)和2 h条件而NPAS4相互作用主要在刺激的状态。代表图像从2实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。c。平均RNA-seq DeSeq2规范化计数±s.e.m。NPAS4-NuA4组件的小鼠海马在0 h (n = 8), 2 h (n = 8)和10 h (n = 10),帖子KA刺激。* *gydF4y2BaPgydF4y2Ba= 3.19 e-29。gydF4y2BaPgydF4y2Ba价值决定从transcriptome-wide DeSeq2分析Benjamini-Hochberg修正。看到单独的源数据gydF4y2BaPgydF4y2Ba值。d。全长NPAS4(氨基酸1 - 802)和c端部分的表示截断NPAS4 HEK293T细胞中表达。连续的国旗和HA IPs进行(右),其次是西方墨点法NPAS4, ARNT2, NuA4子单元TRRAP DMAP1。Flag-HA-tagged核GFP (nGFP)作为消极的控制。代表图像从3实验。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。e。热图column-normalized特异性得分为每个组件的NuA4复杂anti-Flag IP-MS实验与NPAS4 / ARNT NPAS4 / ARNT2,安全系数/小君,或者EGR1 HEK293T细胞中表达。所有的蛋白质都Flag-HA标记。特异性分数代表肽的数量确定的比例在IP nGFP中肽的数量控制并行执行。补充表中复制数据提供gydF4y2Ba1gydF4y2Ba。f。规范化NPAS4-NuA4组件的数量(修v3)在小鼠海马,海马single-nucleus RNA序列在列,显示为一个z分数归一化。g。标记基因识别人类初级运动皮层细胞类型single-nucleus艾伦大脑研究所发表的RNA序列数据集(见图。gydF4y2Ba1 dgydF4y2Ba)gydF4y2Ba18gydF4y2Ba在列,显示为一个z分数,规范化。gydF4y2Ba
扩展数据图3 NPAS4 NuA4硝唑在整个基因组染色质。gydF4y2Ba
总平均急忙逃走的阴谋。报道(片段深度/ bp / /峰)±s.e.m。在NPAS4-binding网站gydF4y2BaNpas4gydF4y2Ba野生型和gydF4y2BaNpas4gydF4y2BaKO海马组织。(gydF4y2BaNpas4gydF4y2Ba野生型:n = 5,gydF4y2BaNpas4gydF4y2Ba柯:n = 2,免疫球蛋白:n = 8) 3 - 5老鼠汇集/复制。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16,gydF4y2BaPgydF4y2Ba值在计算平均信号提取2 kb窗口集中在NPAS4峰值峰会使用未配对,双尾Wilcoxon rank-sum测试。b。综合基因组浏览器的轨迹聚合NPAS4急忙逃走信号(n = 5)。3 - 5个老鼠汇集/复制。3额外复制NPAS4急忙逃走信号确认的再现性NPAS4急忙逃走。c。NPAS4分布(10225网站)和安全系数(11770网站)急忙逃走注释峰值相对于监管所有元素(179841网站)在海马组织中。d。10225年重大主题丰富NPAS4急忙逃走的峰值。价值计算MEME-ChIPgydF4y2Ba72年gydF4y2Ba。e。相关性NPAS4急忙逃走,NPAS4 ChIP-seq读取在NPAS4 ChIP-seq山峰(10917 ChIP-seq峰)。价值观代表了日志gydF4y2Ba2gydF4y2Ba阅读深度规范化vs ChIP-seq急忙逃走。由皮尔森相关计算(R = 0.45)和斯皮尔曼(ρ= 0.41)测试,gydF4y2BaPgydF4y2Ba< 2.2 e-16双尾相关测试。倒数的相关性分析NPAS4急忙逃走,NPAS4 ChIP-seq读取在NPAS4急忙逃走的山峰(10225急忙逃走的峰值)收益率皮尔逊R = 0.46,斯皮尔曼ρ= 0.43,gydF4y2BaPgydF4y2Ba< 2.2 e-16双尾相关测试。f。维恩图解SEACR之间的重叠峰的anti-EP400有所(架a300型抗体1 Bethyl实验室- 541 - a)和anti-EP400 Ab2(抗体2,Abcam Ab5201)。峰重叠显示至少1 bp整个SEACR-enriched地区之间的重叠。Maxima表明重叠区域扩展500个基点从峰值最大值为每一个因素。g。维恩图解SEACR之间的重叠峰NPAS4 / ARNT2 co-bound山峰ETL4和高信任度EP400山峰,山峰共享的定义为工会EP400抗体。Maxima表明重叠区域扩展500个基点从峰值最大值为每一个因素。h。箱线图的平均EP400规范化信号(计数每百万)网站受安全系数但不是NPAS4(标记为“安全系数”)和网站受NPAS4但不是”丛书(标记为“NPAS4”)。安全系数/不NPAS4网站被定义为网站SEACR-determined急忙逃走的峰值信号的安全系数但没有峰值NPAS4(6998网站),反之亦然(NPAS4 /不安全系数峰值:5550网站)。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。3 - 5个老鼠汇集/复制。 Replicate numbers provided in Supplementary Table2gydF4y2Ba。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。我。代表综合基因组浏览器的复制EP400急忙逃走的gydF4y2Ba脑源性神经营养因子gydF4y2Ba启动子。gydF4y2Ba
扩展数据图4急性删除NPAS4或TIP60病毒注入和额外的质量控制single-nucleus RNA-seq数据集。gydF4y2Ba
免疫组织化学的形象gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠注射AAV表达Cre-mCherry(红色所示)和收集2 h后低剂量KA诱导NPAS4(青色)所示。代表图像从3动物。比例尺= 1 mm. b。免疫组织化学的形象gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠注射AAV表达Cre-mCherry(红色所示)。TIP60(青色)所示。代表图像从3动物。比例尺= 1 mm. c。免疫组织化学海马的半球的形象gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠注射Cre-mCherry和ΔCre-GFP侧的海马体和收集2 h后低剂量KA诱导NPAS4(白色)所示。代表图像从3动物。比例尺= 1 mm. d。从整个海马组织的免疫印迹gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba小鼠注射AAV表达Cre-mCherry和ΔCre-GFP侧海马。组织收集0或2 h后KA刺激。Cre和ΔCre组织收集从每个鼠标(0 h, n = 2;2 h, n = 2)。看到凝胶源数据(补充图。gydF4y2Ba1gydF4y2Ba)。e。免疫印迹d所示的量化,NPAS4信号加载控制GAPDH正常化。f。左:UMAP的可视化gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2BasnRNA-seq数据集。根据鼠标原产地核是彩色的。32418核2小鼠。右:UMAP的可视化gydF4y2BaTip60gydF4y2Bafl / flgydF4y2BasnRNA-seq数据集。根据鼠标原产地核是彩色的。44511年核从3老鼠。g。最终核数量的总结gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2BasnRNA-seq数据集,量化Cre-mCherry和ΔCre-GFP病毒的感染率。高感染率的神经元反映了已知的取向AAV2/9病毒用于这些实验。h。程控作业gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba(左)和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba(右)snRNA-seq数据集使用表示标记基因。y轴表示归一化表达式(修日志gydF4y2BaegydF4y2Ba归一化计算)。我。每核的分布数量的基因检测,通过程控。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba(左)和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba(右)。gydF4y2Ba
扩展数据图5 NPAS4-NuA4协调跨神经元亚型基因调控gydF4y2Ba在活的有机体内gydF4y2Ba。gydF4y2Ba
热图显示坐标NPAS4调节目标基因在海马体的主要神经元亚型gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba和gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠。NPAS4目标基因被确定在每个程控使用修(v3)和Monocle3(见gydF4y2Ba方法gydF4y2Ba)。Bonferroni调整gydF4y2BaPgydF4y2Ba值从修(v3)微分表达式测试(未配对,双尾Wilcoxon rank-sum测试)ΔCre -和每个程控Cre-infected原子核所示。每一列表示调整gydF4y2BaPgydF4y2Ba一个基因的值。b。小提琴情节(修日志显示分布的表达式gydF4y2BaegydF4y2Ba规范化计数)表示基因在细胞核的程控表示。Bonferroni调整gydF4y2BaPgydF4y2Ba值* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。差异基因表达进行了测试使用一个未配对,双尾Wilcoxon rank-sum测试执行通过修(v3) FindMarkers函数。c。所观察到的差异的比较(ΔCre - Cre)规范化NPAS4或TIP60目标基因在每个神经元亚型获得的差异在使用同等数量的随机选择的基因。基因随机选择从表达基因的前10%(占NPAS4平均或TIP60目标基因高表达),和平均差异(ΔCre - Cre)在每个基因表达式计算为每个随机样本。这个抽样是重复10000次生成抽样分布(灰色)。在每个子类型,平均差异(ΔCre - Cre)观察到当使用亚型的NPAS4或TIP60目标基因位于远离使用获得的分布随机选择基因,表明目标的差异表达基因ΔCre - Cre-infected核并不是由于机会。d。箱线图显示日志gydF4y2Ba2gydF4y2Ba褶皱的变化(见NPAS4或TIP60目标基因gydF4y2Ba方法gydF4y2Ba)比较ΔCre Cre-infected原子核在齿状回,CA1, CA3,抑制性神经元。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba使用双尾值计算,未配对t比较零假设的日志gydF4y2Ba2gydF4y2Ba褶皱变化= 0(无Cre和ΔCre的区别)。确切的gydF4y2BaPgydF4y2Ba价值观和细胞数量每个集群中提供数据来源。e。选择重叠在NPAS4方面丰富的目标基因和TIP60目标基因在齿状回、CA1, CA3,抑制性神经元。圆圈的大小表示调整gydF4y2BaPgydF4y2Ba浓缩的价值取决于使用gProfiler2费雪的单侧检验gydF4y2Ba65年gydF4y2Ba。颜色表示褶皱浓缩。看到gydF4y2Ba方法gydF4y2Ba额外的细节和补充表gydF4y2Ba3gydF4y2Ba对于丰富的完整列表为每个程控方面。gydF4y2Ba
扩展数据图6 NPAS4-NuA4协调调节基因转录和体细胞抑制。gydF4y2Ba
RNA-seq的。主成分分析聚类数据集从培养小鼠神经元表达shrna瞄准gydF4y2BaNpas4gydF4y2Ba,gydF4y2BaTip60gydF4y2Ba,或gydF4y2BaEp400gydF4y2Ba,刺激55毫米氯化钾为0,2,或6 h。荧光素酶控制成分目标。箱线图的日志gydF4y2Ba2gydF4y2Ba褶皱控制成分之间的变化(n = 3)表示gydF4y2BaNpas4gydF4y2Ba(n = 3),gydF4y2BaTip60gydF4y2Ba(n = 3)gydF4y2BaEp400gydF4y2Ba(n = 3) shrna神经元文化6 h membrane-depolarization由55毫米氯化钾。复制的主要文化上生成独立的日子。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。Activity-regulated-genes (ARGs)被定义为基因调节Benjamini-Hochberg调整至少1.5倍gydF4y2BaPgydF4y2Ba< 0.01比较6 h和0 h时间点控制shRNA-treated神经元。gydF4y2BaTip60gydF4y2Ba和gydF4y2BaEp400gydF4y2Ba目标被定义为所有基因下调至少1.5倍Benjamini-Hochberg调整gydF4y2BaPgydF4y2Ba由shrna < 0.01。非目标包括所有表达基因没有损失的影响gydF4y2BaTip60gydF4y2Ba或gydF4y2BaEp400gydF4y2Ba。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。c。平均表达±s.e.m。的gydF4y2BaEp400gydF4y2Ba(n = 3),gydF4y2BaTip60gydF4y2Ba(n = 3)gydF4y2BaNpas4gydF4y2Ba由qPCR (n = 3)。复制的主要文化上生成独立的日子。表达式都归一化gydF4y2BaTubb3gydF4y2Ba和gydF4y2BaGapdhgydF4y2Ba。gydF4y2BaEp400gydF4y2Ba0 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0026,shRNA2: *gydF4y2BaPgydF4y2Ba= 0.0072;2 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0072,shRNA2: *gydF4y2BaPgydF4y2Ba= 0.0154;6 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0027,shRNA2: *gydF4y2BaPgydF4y2Ba= 0.0038。gydF4y2BaTip60gydF4y2Ba0 h shRNA1: ns = 0.4021, shRNA2: ns = 0.2669;2 h shRNA1: ns = 0.4507, shRNA2: ns = 0.3324;6 h shRNA1: ns = 0.433, shRNA2: ns = 0.5431。gydF4y2BaNpas4gydF4y2Ba0 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0214;2 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0004;6 h shRNA1: *gydF4y2BaPgydF4y2Ba= 0.0001。gydF4y2BaPgydF4y2Ba值的双尾,未配对t。d。哈培养皮层神经细胞的染色感染核GFP (nGFP)和Flag-HA-tagged NPAS4(完整和截断表示)(见扩展数据图。gydF4y2Ba二维gydF4y2Ba)。代表图像从一个实验。酒吧= 50μm规模。e。荧光素酶的活性NPAS4-bound增强剂与要么nGFP培养神经细胞转染,全长NPAS4,或表示NPAS4截断(见扩展数据图。gydF4y2Ba二维gydF4y2Ba)。颜色代表不同的NPAS4截断。平均荧光素酶活动规范化nGFP-expressing控制样本±s.e.m。(见gydF4y2Ba方法gydF4y2Ba)。每个点代表一个值从一个独立转染收集从至少三个独立的初级神经元文化,除了Peak1 npas4_1 - 699(2文化)。* *gydF4y2BaPgydF4y2Ba< 0.0045;*gydF4y2BaPgydF4y2Ba= 0.049。gydF4y2BaPgydF4y2Ba使用双尾值计算,未配对t与Benjamini-Hochberg修正多重假设检验。个人gydF4y2BaPgydF4y2Ba价值观和复制源数据提供的数字。f。点代表未感染细胞之间的距离:Cre-infected细胞。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba:机枪兵:n = 16双从4老鼠,Unstim: n = 12双从5老鼠。gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba:机枪兵:从2 n = 11对老鼠,Unstim: n = 12双从2老鼠。gydF4y2BaPgydF4y2Ba= 0.305。gydF4y2BaPgydF4y2Ba使用一个单向方差分析值的计算。g。横向距离中心的每一对刺激电极放置在地层pyramidale的中心。gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba:机枪兵:n = 16双从4老鼠,Unstim: n = 12双从5老鼠。gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba:机枪兵:从2 n = 11对老鼠,Unstim: n = 12双从2老鼠。gydF4y2BaPgydF4y2Ba= 0.055。gydF4y2BaPgydF4y2Ba使用一个单向方差分析值的计算。h,我。同时访问阻力为每一对MΩ修补CA1锥体神经元(h)gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba:机枪兵:n = 16双从4老鼠,gydF4y2BaPgydF4y2Ba= 0.7396;从5老鼠Unstim: n = 12双,gydF4y2BaPgydF4y2Ba= 0.9677,(我)gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba:机枪兵:从2 n = 11对老鼠,gydF4y2BaPgydF4y2Ba= 0.7533;从2小鼠Unstim: n = 12双,gydF4y2BaPgydF4y2Ba= 0.8906。gydF4y2BaPgydF4y2Ba值未配对,双尾t。gydF4y2Ba
扩展数据图7 NPAS4-NuA4结合区域进行反复DNA断裂gydF4y2Ba在活的有机体内gydF4y2Ba。gydF4y2Ba
使用的所有监管元素。定义整个手稿。维恩图描绘的重叠重现ATAC-seq山峰(0和2 h峰之间的合并)和可再生的H3K27ac急忙逃走(0和2 h峰之间的合并)。ATAC-seq和急忙逃走峰集被定义为高峰持续3 3复制/计算。3 - 5个老鼠汇集/复制。监管所有元素被定义为可再生的ATAC-seq的结合和H3K27ac山峰在所有时间点。Activity-inducible监管元素被定义为元素,表现出变化大于1/2 ATAC-seq信号(2比0 h刺激;调整gydF4y2BaPgydF4y2Ba< 0.05)和/或1.5倍改变H3K27ac急忙逃走信号(2比0 h刺激;调整gydF4y2BaPgydF4y2Ba< 0.05)。gydF4y2BaPgydF4y2Ba值计算DeSeq2瓦尔德测试用默认Benjamini-Hochberg修正。b。上部面板:热图复制的ATAC-seq海马之间的欧几里得距离原子核隔绝如果(0 h)或2 h后刺激所有监管元素中定义扩展数据图。gydF4y2Ba7一个gydF4y2Ba。降低面板:整合基因组学代表观众追踪个人ATAC-seq activity-inducible基因复制gydF4y2BaInhbagydF4y2Ba。c。上部面板:热图复制之间的欧几里得距离H3K27ac急忙逃走从如果大脑海马核孤立(0 h)或2 h后刺激所有监管元素中定义扩展数据图。gydF4y2Ba7一个gydF4y2Ba。降低面板:整合基因组学代表观众追踪个人H3K27ac急忙逃走activity-inducible基因复制gydF4y2Ba脑源性神经营养因子gydF4y2Ba。d。主成分分析γH2AX ChIP-seq信号在所有监管元素(见扩展数据图。gydF4y2Ba7一个gydF4y2Ba如果和刺激海马细胞核。复制集群在一起,由国家单独的刺激。e。代表综合基因组浏览器追踪个人γH2AX ChIP-seq复制和总NPAS4急忙逃走activity-inducible基因信号(n = 5)gydF4y2BaRgs7bpgydF4y2Ba。3 - 5个老鼠汇集/复制。f。示意图的sBLISS-seq培养神经元Cas9-only病毒感染或病毒+ gRNAs Cas9。g。综合基因组浏览器追踪显示sBLISS-seq信号的gydF4y2Ba”丛书gydF4y2Ba启动子在培养神经元Cas9 + gRNA感染gydF4y2Ba”丛书gydF4y2Ba轨迹或Cas9-only控制。红线表示gRNA的位置。放大的视角展示了读取映射两侧的预测gRNA削减网站,用箭头表示。PAM网站强调的DNA序列。代表图像从3实验。复制由独立的文化生成在不同的日子。h。综合基因组浏览器追踪显示sBLISS-seq信号的gydF4y2BaInhbagydF4y2Ba增强剂在培养神经元Cas9 + gRNA感染gydF4y2BaInhbagydF4y2Ba增强器轨迹或Cas9-only控制。代表图像从3实验。复制由独立的文化生成在不同的日子。(见我。箱线图显示sBLISS-seq规范化信号gydF4y2Ba方法gydF4y2Ba在野生型神经元)所有监管元素0 (n = 8)和2 h后(n = 8) KA刺激。1鼠标/复制。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。启动子= 11853,内含子= 79438,基因间= 81385,3′UTR = 1574, 5′UTR = 695,非编码= 445,TTS = 1831,外显子= 2620。看到扩展数据图。gydF4y2Ba7一个gydF4y2Ba。j。聚合块平均sBLISS-seq覆盖率(片段深度/ bp /峰)±s.e.m。(n = 8)在最高四分位数的TSS的基因表达(Q4)与基因最低四分位数(Q1) 2 h刺激海马。基因表达四分位数确定从DeSeq2规范化项配对RNA-seq sBLISS-seq一样的组织样本收集的样本在2 h KA刺激的计算(见图。gydF4y2Ba3 dgydF4y2Ba)。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值计算平均信号提取20 kb窗口在基因TSS使用一个未配对,双尾Wilcoxon rank-sum测试。k。双边带注释的峰值分布在2 h的刺激(4447峰)。重现sBLISS-seq山峰被MACS2峰值定义调用算法和被发现在至少5 8复制。l。sBLISS-seq信号之间的相关性(日志gydF4y2Ba2gydF4y2Ba归一化计算)和γH2AX信号(日志gydF4y2Ba2gydF4y2Ba归一化计算)所有监管元素在海马体(179841网站;看到扩展数据图。gydF4y2Ba7一个gydF4y2Ba)。相关性计算由皮尔森(R = 0.47)和斯皮尔曼(ρ= 0.48)gydF4y2BaPgydF4y2Ba< 2.2 e-16两双尾相关测试。m。最重要的主题丰富的可再生的sBLISS-seq峰2 h的刺激。图案activity-inducible转录因子(ATF1、EGR1 NPAS4 / AHR)浓缩在sBLISS-seq峰值。价值计算MEME-ChIPgydF4y2Ba72年gydF4y2Ba。n。箱线图的平均sBLISS-seq规范化计数activity-inducible元素(11114网站)vs non-inducible元素(168727网站)在0 h (n = 8老鼠)和2 h (n = 8老鼠)刺激。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。Non-inducible元素包括所有元素不属于最高诱导我们的监管环境。* * *gydF4y2BaPgydF4y2Ba= 2.2 e-16 ns:gydF4y2BaPgydF4y2Ba= 1。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon等级和测试(2 h > 0 h)。gydF4y2Ba
扩展数据图8 END-seq映射培养皮层神经元的双边带信号显示浓缩NPAS4-bound地点和活动依赖性动力学。gydF4y2Ba
。聚合块(本大小50个基点)的平均END-seq覆盖率(片段深度/ bp /峰)±s.e.m。(n = 2)在培养小鼠皮层神经元CTCF-bound网站(13228处)或0 2 h的刺激与55毫米氯化钾。看到gydF4y2Ba方法gydF4y2BaEND-seq完整描述的方法和实验参数。CTCF-bound网站被定义为网站与海马SEACR-defined CTCF急忙逃走的峰值信号数据集。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。得了,复制由独立的主要文化。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon rank-sum测试信号中提取在500个基点窗口集中在每一个峰值。b。总情节(本大小50个基点)的平均END-seq覆盖±s.e.m。(n = 2)在培养小鼠皮层神经元NPAS4-bound网站(10225处)或0 2 h后刺激与55毫米氯化钾。NPAS4-bound SEACR-defined峰的网站被定义为网站NPAS4急忙逃走gydF4y2Ba在活的有机体内gydF4y2Ba海马的数据集。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。c。总情节(本大小50个基点)的平均END-seq覆盖±s.e.m。(n = 2)在培养小鼠皮层神经元NPAS4网站缺乏安全系数峰值(5550网站)和安全系数的网站缺乏NPAS4峰值(6998网站),0和2 h后刺激与55毫米氯化钾。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16 NPAS4 0和2 h, * * *gydF4y2BaPgydF4y2Ba为安全系数0和2 h = 2.3 e15汽油。d。总情节(本大小50个基点)的平均sBLISS-seq覆盖±s.e.m。(n = 8) CTCF-bound地点在0和2 h后与低剂量的KA刺激。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。对于d - h,复制来自个人的老鼠。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon rank-sum测试信号中提取在500个基点窗口集中在每一个峰值。e。总情节(本大小50个基点)的平均sBLISS-seq覆盖±s.e.m。(n = 8) NPAS4-bound地点在0和2 h后刺激。* *gydF4y2BaPgydF4y2Ba< 2.2 e-16。f。总情节(本大小50个基点)的平均sBLISS-seq覆盖±s.e.m。(n = 8)在NPAS4网站缺乏安全系数和安全系数峰值网站缺乏NPAS4峰2 h后刺激。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。g。总情节(本大小50个基点)的平均sBLISS-seq覆盖±s.e.m。(n = 8)在NPAS4网站缺乏安全系数峰值在0和2 h后刺激。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。h。总情节(本大小50个基点)的平均sBLISS-seq覆盖±s.e.m。(n = 8)”丛书的网站缺乏NPAS4峰值在0和2 h后刺激。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。我。箱线图显示平均NPAS4 (n = 5)和安全系数(n = 3)急忙逃走信号(计数每百万)NPAS4网站缺乏安全系数和安全系数峰值网站缺乏NPAS4峰值在海马2 h后刺激。3 - 5个老鼠汇集/复制。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。gydF4y2Ba
扩展数据图9 NPAS4-NuA4-bound网站进行DNA修复诱导转录消退。gydF4y2Ba
之间的欧几里得距离。热图复制RNA-seq准备从同一组织用于生成sBLISS-seq timecourse。样品集群主要根据刺激状态,与10 h后样品落入两组与抑制或刺激持续转录诱导。b。DeSeq2规范化项额外诱导基因,gydF4y2BaInhbagydF4y2Ba和gydF4y2BaCgref1gydF4y2Ba,显示为每个复制。c。sBLISS-seq样本的主成分分析集群在0 h, 2 h和10 h后刺激。sBLISS-seq示例集群根据刺激状态,与10 h后刺激样本聚类与0 h或2 h样本。成对RNA-seq分析表明这种分离是由改变转录水平感应在这些样品。d。总情节(本大小50个基点)的平均sBLISS-seq覆盖率(片段深度/ bp /峰)±s.e.m。监管元素,子集的四分位数NPAS4急忙逃走的信号。Q1 = 44864网站,第四季度= 7378网站。0 h (n = 8), 2 h (n = 8), 10 h (n = 10)。1鼠标/复制。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon等级和测试。NPAS4 Q1: 0 vs2 h:gydF4y2BaPgydF4y2Ba< 2.2 e-16 2 vs 10 h:gydF4y2BaPgydF4y2Ba= 1.7 e15汽油,0和10 h:gydF4y2BaPgydF4y2Ba< 2.2 e-16;NPAS4第四季度:0和2 hgydF4y2BaPgydF4y2Ba< 2.2 e-16 2 vs 10 h:gydF4y2BaPgydF4y2Ba< 2.2 e-16 0和10 h:gydF4y2BaPgydF4y2Ba< 2.2 e-16。e。箱线图的sBLISS-seq DeSeq2规范化数量0 h, 2 h, 10 h“不活跃”,和10 h仍然活跃的样本在activity-inducible监管元素子集的四分位数NPAS4绑定。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。每个箱形图代表一个单独的个体组成的复制鼠标。箱线图的平均信号在所有复制图所示。gydF4y2Ba4 bgydF4y2Ba。f。总情节SAR-seq(本大小50 bp)的平均水平gydF4y2Ba32gydF4y2Ba覆盖±s.e.m。在CTCF结合位点(n = 3),所有NPAS4结合位点,NPAS4 vs”丛书结合位点。看到扩展数据图。gydF4y2Ba8我gydF4y2BaNPAS4 vs安全系数的定义结合位点。gydF4y2Ba
扩展数据图10 NPAS4-NuA4 co-binds基因组DNA修复传感器MRE11和RAD50刺激神经元。gydF4y2Ba
。聚合块平均MRE11急忙逃走覆盖率(片段深度/ bp /峰)±s.e.m。在KA-stimulated核隔绝gydF4y2BaMre11gydF4y2BaKO / flgydF4y2Ba要么ΔCre-GFP病毒感染(控制)或Cre-mCherry (gydF4y2BaMre11gydF4y2BacKO) MRE11结合位点(17084网站)。MRE11结合位点被SEACR峰调用算法决定。免疫球蛋白g表示急忙逃走的信号从一个非特异性免疫球蛋白控制和代表平均免疫球蛋白在ΔCre-GFP和Cre条件。MRE11 (n = 3 Cre和n = 3ΔCre-GFP),免疫球蛋白(n = 3 Cre和n = 3ΔCre-GFP)。1鼠标/复制。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试。b。综合基因组浏览器图像查看器显示急忙逃走NPAS4信号,MRE11 (Cre或ΔCre),和免疫球蛋白(Cre或ΔCre)在2 h KA-stimulated核gydF4y2Ba脑源性神经营养因子gydF4y2Ba基因。c。总急忙逃走NPAS4信号,RAD50和MRE11 0 h和2 h刺激海马组织NPAS4-binding地点。每个NPAS4-binding网站表示为一个水平线高峰集中在峰会和扩展±1 kb。颜色与测序信号强度显示比例尺的每个因素(0到50 read-depth标准化)。MRE11 (n = 2), RAD50 (n = 4), NPAS4 (n = 5)。3 - 5个老鼠汇集/复制。d。维恩图解MRE11结合位点之间的重叠,RAD50和NPAS4 2 h KA-stimulated神经元。山峰为每个因素确定使用SEACR峰调用算法和代表峰发现人工繁殖复制(2 2 MRE11复制,3 4 RAD50复制,和4 5 NPAS4复制)。3 - 5个老鼠汇集/复制。e。最重要的图案富含MRE11急忙逃走的峰值(2 h KA-stimulated)。 Motif enrichment was performed on 1 kb peaks extended 500 bp up and downstream from the peak maxima. Notable motifs include the NPAS4/bHLH-PAS motif, the AP1 family, and CTCF motifs. f. Aggregate of average CUT&RUN coverage (fragment depth per bp per peak) ± s.e.m. at all regulatory elements, subset by quartiles of NPAS4 CUT&RUN signal.Q1 = 44,864 sites, Q4 = 7,378 sites. MRE11(0 h and 2 h, n = 2), RAD50 (0 h, n = 3), RAD50 (2 h, n = 4). ***PgydF4y2Ba< 2.2 e-16;* *gydF4y2BaPgydF4y2Ba= 5.78 e-06。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon rank-sum测试。3 - 5个老鼠汇集/复制。gydF4y2Ba
扩展数据图11 NPAS4-NuA4新兵修复因素刺激神经元的染色质。gydF4y2Ba
,箱线图平均IgG-normalized MRE11和RAD50急忙逃走信号(左)或ATAC-seq规范化计数(右)在activity-inducible元素绘制,子集的四分位数NPAS4急忙逃走的信号。网站显示被选中的同等或更高诱导ATAC-seq信号在低四分位数(Q1)相比,最高NPAS4-binding网站(第四季度)。Q1 = 111网站,第四季度= 200网站。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。MRE11 (0 h和2 h, n = 2), RAD50 (0 h, n = 3), RAD50 (2 h, n = 4) ATAC-seq(0和2 h, n = 3)。3 - 5个老鼠汇集/复制。MRE11 2 h第一季度和第四季度:* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16;RAD50 2 h第一季度和第四季度:* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16;ATAC 2 h NPAS4 Q1 vs NPAS4第四季度:gydF4y2BaPgydF4y2Ba= 0.105。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon rank-sum测试。b。箱线图的平均IgG-normalized MRE11和RAD50急忙逃走信号(左)或H3K27ac规范化计数(右)在activity-inducible元素绘制,子集的四分位数NPAS4急忙逃走的信号。网站显示被选中的同等或更高诱导H3K27ac信号在低四分位数(Q1)相比,最高NPAS4-binding网站(第四季度)。Q1 = 79网站,第四季度= 88网站。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。MRE11 (0 h和2 h, n = 2), RAD50 (0 h, n = 3), RAD50 (2 h, n = 4) ATAC-seq(0和2 h, n = 3)。3 - 5个老鼠汇集/复制。MRE11 2 h第一季度和第四季度:* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16;RAD50 2 h第一季度和第四季度:* *gydF4y2BaPgydF4y2Ba= 2.603 e-12;H3K27ac 2 h第一季度和第四季度:gydF4y2BaPgydF4y2Ba= 0.0567。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon rank-sum测试。c。实验设计用于隔离Cre-mCherry——并使用florescence-activatedΔCre-GFP-infected核细胞排序(流式细胞仪)。核随后用于EP400急忙逃走,MRE11。d。流式细胞仪Cre-mCherry-positive核(从DRAQ5封闭,荧光染料用于识别DNA核)。左面板显示的直方图分布Cre-mCherry信号在被感染的组织相对于未感染控制组织样本。中间面板显示排序方案,负面事件定义为DRAQ5-stained,当天未受感染的组织样本并行运行排序。右面板显示了所有的FITC vs mCherry信号没有doubly-infected DRAQ5 +核和细胞样本。看到补充图。gydF4y2Ba2gydF4y2Ba对控制计划。e。流式细胞仪的ΔCre-GFP核(封闭DRAQ5 +核)。左面板显示的直方图分布ΔCre-GFP信号在被感染的组织相对于未感染控制组织样本。中间面板显示排序方案,负面事件定义为DRAQ5-stained,当天未受感染的组织样本并行运行排序。右面板显示了所有的FITC vs mCherry信号没有doubly-infected DRAQ5 +核和细胞样本。看到补充图。gydF4y2Ba2gydF4y2Ba对控制计划。f。箱线图的平均MRE11急忙逃走规范化Cre或ΔCre-infected海马gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠activity-inducible地点,四分位数的子集NPAS4绑定。Q1 = 44864网站,第四季度= 7378网站。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。MRE11 CRE (n = 3), MRE11ΔCre (n = 3)。每复制小鼠2 - 3汇集。MRE11 Q1:gydF4y2BaPgydF4y2Ba= 1,第四季度:* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(ΔCre > Cre)。g。箱线图的平均EP400急忙逃走规范化Cre或ΔCre-infected海马gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba老鼠activity-inducible地点,四分位数的子集NPAS4绑定。Q1 = 44864网站,第四季度= 7378网站。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。EP400ΔCre (n = 3), EP400 Cre (n = 4)。每复制小鼠2 - 3汇集。EP400 Q1:gydF4y2BaPgydF4y2Ba= 1,第四季度:* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(ΔCre > Cre)。h。综合基因组浏览器图像查看器显示信号MRE11和EP400急忙逃走gydF4y2BaNpas4 -gydF4y2BacKO (Cre)或控制在2 h KA-stimulated核(ΔCre)gydF4y2BaRgs7bpgydF4y2Ba基因。MRE11 CRE (n = 3), MRE11ΔCre (n = 3), EP400ΔCre (n = 3), EP400 CRE (n = 4)。每复制小鼠2 - 3汇集。gydF4y2Ba
扩展数据图12 NPAS4-NuA4损失增加神经细胞基因组DNA断裂。gydF4y2Ba
sBLISS-seq规范化计数的,箱线图核隔绝gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba小鼠注射Cre-mCherry (gydF4y2BaNpas4 -gydF4y2BacKO)或ΔCre-GFP病毒(控制)activity-inducible监管元素子集的四分位数NPAS4急忙逃走信号(见gydF4y2Ba方法gydF4y2Ba,扩展数据图。gydF4y2Ba7一个gydF4y2Ba)。Q1 = 1017网站,第四季度= 764网站。数据绘制包括所有据点来自5复制/基因型;在执行复制不平均。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(Cre >ΔCre)。b。箱线图sBLISS-seq规范化方面的核与野生型小鼠注射Cre-mCherry或ΔCre-GFP病毒activity-inducible监管元素,子集的四分位数NPAS4急忙逃走的信号。Q1 = 1017网站,第四季度= 764网站。数据绘制包括所有据点来自3复制/基因型;在执行复制不平均。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。Q1:gydF4y2BaPgydF4y2Ba= 1;第四季度gydF4y2BaPgydF4y2Ba= 0.995。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(Cre >ΔCre)。c。箱线图sBLISS-seq规范化方面的核隔绝gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba小鼠注射Cre-mCherry (gydF4y2BaNpas4 -gydF4y2BacKO)或ΔCre-GFP病毒(控制)监管元素,子集的四分位数NPAS4急忙逃走信号(见gydF4y2Ba方法gydF4y2Ba监管网站定义)。Q1 = 44864网站,第四季度= 7378网站。数据绘制包括所有据点来自5复制/基因型。与线框代表四分位范围值。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。* * *gydF4y2BaPgydF4y2Ba< 2.2 e-16。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(Cre >ΔCre)。d。箱线图的sBLISS-seq DeSeq2规范化数量核与野生型注射Cre-mCherry或者ΔCre-GFP病毒管理元素,子集的四分位数NPAS4急忙逃走信号(见gydF4y2Ba方法gydF4y2Ba监管网站定义)。数据绘制包括所有据点来自3复制/基因型。箱线图显示值(线)、差(盒)1.5倍差(须),等级显示值±1.58×差/√(n)。Q1:gydF4y2BaPgydF4y2Ba= 1;第四季度gydF4y2BaPgydF4y2Ba= 0.1092。gydF4y2BaPgydF4y2Ba值未配对,单侧Wilcoxon rank-sum测试(Cre >ΔCre)。e。平均±s.e.m。的全基因组在海马核隔绝gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba老鼠(0和2 h;10 h n = 3;n = 4) Cre或ΔCre病毒感染。在样本比较,输入读取downsampled最小值在所有条件,和数字的独特的DNA断裂。gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba:0 h:gydF4y2BaPgydF4y2Ba= 0.0017,2 h:gydF4y2BaPgydF4y2Ba= 0.013,10 h:gydF4y2BaPgydF4y2Ba= 0.158。gydF4y2BaPgydF4y2Ba值的双尾,未配对t。f。裂解半胱天冬酶3(凋亡标记)染色gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba小鼠注射AAV表达Cre-mCherry。代表图像从3动物。酒吧= 300μm规模。g。裂解半胱天冬酶3染色gydF4y2BaTip60gydF4y2Bafl / flgydF4y2Ba小鼠注射AAV表达Cre-mCherry。代表图像从3动物。酒吧= 300μm规模。gydF4y2Ba
扩展数据图13 NPAS4-NuA4网站在衰老和突变分析gydF4y2BaNpas4 KOgydF4y2Ba寿命分析。gydF4y2Ba
。流式细胞仪分选方案隔离NeuN-expressing神经元衰老gydF4y2BaNpas4gydF4y2Ba野生型与KO海马组织。排序细胞NeuN +和NeuN——盖茨重新分析纯度。看到补充图。gydF4y2Ba2gydF4y2Ba对控制计划。b。平均归一化基因表达±s.e.m。(相对于看家基因gydF4y2BaGapdhgydF4y2Ba)的标记基因(NeuN +)神经元或神经胶质细胞类型(NeuN)。每个点代表收集的数据从一个单独的老鼠在2天独立排序。* * *gydF4y2BaPgydF4y2Ba< 0.001;* *gydF4y2BaPgydF4y2Ba< 0.01;*gydF4y2BaPgydF4y2Ba< 0.05。gydF4y2BaPgydF4y2Ba值未配对,双尾t与Benjamini-Hochberg多元假设修正。个人gydF4y2BaPgydF4y2Ba价值观和复制如下:gydF4y2BaGrin1gydF4y2Ba(n = 6):gydF4y2BaPgydF4y2Ba= 2.06 e-05,gydF4y2BaGrin2bgydF4y2Ba(n = 3):gydF4y2BaPgydF4y2Ba= 5.97 e 03,gydF4y2BaSyapsin1gydF4y2Bae-04 (n = 3): 5.72,gydF4y2BaRbfox3gydF4y2Ba(n = 6): 3.89 e-04,gydF4y2BaNpas4gydF4y2Ba(n = 3):gydF4y2BaPgydF4y2Ba= 5.21 e 03,gydF4y2BaS100bgydF4y2Ba(n = 6):gydF4y2BaPgydF4y2Ba= 3.85 e-06,gydF4y2BaGfapgydF4y2Ba(n = 3):gydF4y2BaPgydF4y2Ba= 1.89 e-02,gydF4y2BaAldh1l1gydF4y2Ba(n = 3):gydF4y2BaPgydF4y2Ba= 9.50 e 03,gydF4y2BaMoggydF4y2Ba(n = 3):gydF4y2BaPgydF4y2Ba= 2.29 e-04,gydF4y2BaPdgrfagydF4y2Ba(n = 6):gydF4y2BaPgydF4y2Ba= 1.16 e-05。的c。图SiMSen-seq扩增子测序方法用于识别体细胞突变发生在个体DNA模板。d。积极控制实验的图(上)用于测试SiMSen-seq突变检测方法。培养皮层神经元感染了慢病毒表达Cas9有或没有指南rna (gydF4y2Ba脑源性神经营养因子、安全系数、Inhba Scg2gydF4y2Ba)。SiMSen-seq被用来检测gRNA切位点的突变gydF4y2BaInhbagydF4y2Ba和gydF4y2Ba脑源性神经营养因子gydF4y2Ba。突变频率(即插入/删除/ UMI家庭)的数量是绘制在一个40 bp窗口周围的站点。e。小提琴块读depth-normalized NPAS4测序信号,MRE11, RAD50, H3K27ac急忙逃走,γH2AX ChIP-seq和ATAC-seq 2 h刺激神经元在NPAS4-bound(24)和没有NPAS4(11)的网站选择突变分析。每个点代表一个网站。诱导H3K27ac和诱导ATAC情节显示分布的褶皱变化(2比0 h) ATAC-seq和H3K27ac这些相同的网站。虚线表示中位数;实线代表四分位数。* * *gydF4y2BaPgydF4y2Ba< 0.0005;* *gydF4y2BaPgydF4y2Ba< 0.005。gydF4y2BaPgydF4y2Ba值未配对,双尾Wilcoxon等级和测试。NPAS4:gydF4y2BaPgydF4y2Ba= 0.002,MRE11:gydF4y2BaPgydF4y2Ba= 0.0009,RAD50:gydF4y2BaPgydF4y2Ba= 1.33 e-04γH2AXgydF4y2BaPgydF4y2Ba= 0.0027,GC百分比gydF4y2BaPgydF4y2Ba= 0.76;在百分比gydF4y2BaPgydF4y2Ba= 0.76;诱导H3K27acgydF4y2BaPgydF4y2Ba= 0.25,H3K27acgydF4y2BaPgydF4y2Ba= 0.07;ATACgydF4y2BaPgydF4y2Ba= 0.19;诱导ATACgydF4y2BaPgydF4y2Ba= 0.53。复制/因素包含在补充表gydF4y2Ba2gydF4y2Ba。f。基因组的注释NPAS4-bound(24)和没有NPAS4(11)网站。g。左面板:平均SNV频率±s.e.m。在NPAS4-Bound和没有NPAS4年轻(三)动物。每个点代表一个地点采样从老鼠和老鼠4所示的数据。*gydF4y2BaPgydF4y2Ba< 0.05;* *gydF4y2BaPgydF4y2Ba< 0.005,* * *gydF4y2BaPgydF4y2Ba< 0.001;T >gydF4y2BaPgydF4y2Ba= 0.99,T > GgydF4y2BaPgydF4y2Ba= 0.99,T > CgydF4y2BaPgydF4y2Ba= 0.0049,C >gydF4y2BaPgydF4y2Ba= 0.027,C > GgydF4y2BaPgydF4y2Ba= 0.99 C > TgydF4y2BaPgydF4y2Ba= 1.85 e-09。gydF4y2BaPgydF4y2Ba值与Holm-Sidak单向方差分析的修正多重假设检验。右面板:平均插入/删除频率±s.e.m。NPAS4-Bound和NPAS4上没有年轻(三)动物。每个点代表一个地点采样从老鼠和老鼠4所示的数据。* * *gydF4y2BaPgydF4y2Ba= 2.96 e-05。gydF4y2BaPgydF4y2Ba通过一个未配对,双尾Wilcoxon rank-sum测试。h。寿命分析gydF4y2BaNpas4gydF4y2Ba野生型(n = 25) vsgydF4y2BaNpas4gydF4y2Ba男性同胞KO (n = 27)。平均寿命KO = 12个月;平均寿命的野生型不确定。gydF4y2BaPgydF4y2Ba由双尾= 8.67 e-06 Gehan-Breslow-Wilcoxon测试;gydF4y2BaPgydF4y2Ba由双尾= 1.37 e-06 log-rank Mantel-Cox测试。我的寿命分析gydF4y2BaNpas4gydF4y2Ba野生型(n = 28) vsgydF4y2BaNpas4gydF4y2BaKO (n = 37)女同胞。平均寿命KO = 11个月;平均寿命的野生型不确定。gydF4y2BaPgydF4y2Ba由双尾= 1.01 e-06 Gehan-Breslow-Wilcoxon测试;gydF4y2BaPgydF4y2Ba由双尾= 8.48 e-08 log-rank Mantel-Cox测试。j。寿命分析gydF4y2BaNpas4gydF4y2Ba野生型(n = 16gydF4y2Ba,Npas4gydF4y2Ba+ / +gydF4y2Ba;Camk2a-Cre +;Sun1gydF4y2Bafl / +gydF4y2Ba)和gydF4y2BaNpas4gydF4y2BacKO (n = 9,gydF4y2BaNpas4gydF4y2Bafl / flgydF4y2Ba;Camk2a-Cre +;Sun1gydF4y2Bafl / +gydF4y2Ba)。平均寿命cKO = 21.46个月;平均寿命的野生型= 29个月。gydF4y2BaPgydF4y2Ba通过双尾Gehan-Breslow-Wilcoxon测试= 0.049;gydF4y2BaPgydF4y2Ba= 0.19的小动物——一张长有log-rank Mantel-Cox测试。gydF4y2Ba
补充信息gydF4y2Ba
补充数据gydF4y2Ba
补充图1:全扫描图像对西方的屁股在无花果。1 b和扩展数据无花果。1,d-f, h-j, 2 a, b, d和4 d。补充图。2:控制策略图5 d和扩展数据无花果。11 d, e和13。gydF4y2Ba
补充表1gydF4y2Ba
总结获得的肽的质谱实验。为原始数据,请参阅骄傲库加入号码gydF4y2BaPXD038718gydF4y2Ba。Benjamini-Hochberg调整gydF4y2BaPgydF4y2Ba值报告计算使用磨边机(v.3.28.1)。gydF4y2Ba
补充表2gydF4y2Ba
表所有测序数据的复制信息。gydF4y2Ba
补充表3gydF4y2Ba
海马snRNA-seq基因NPAS4和TIP60细胞类型的目标。Bonferroni-adjustedgydF4y2BaPgydF4y2Ba值计算使用未配对,双尾Wilcoxon rank-sum测试中实现修(v.3)。gydF4y2Ba
补充表4gydF4y2Ba
基因组位置为海马监管元素和诱导ATAC-seq H3K27ac急忙逃走。Benjamini-Hochberg-adjustedgydF4y2BaPgydF4y2Ba值计算使用DeSeq2报道(v.1.26.0)。gydF4y2Ba
补充表5gydF4y2Ba
地区和引物用于突变分析。gydF4y2Ba
权利和权限gydF4y2Ba
开放获取gydF4y2Ba本文是基于知识共享署名4.0国际许可,允许使用、共享、适应、分布和繁殖在任何媒介或格式,只要你给予适当的信贷原始作者(年代)和来源,提供一个链接到创作共用许可证,并指出如果变化。本文中的图片或其他第三方材料都包含在本文′s Creative Commons许可,除非另有说明在一个信用额度的材料。如果材料不包括在本文′年代创作共用许可证和用途是不允许按法定规定或超过允许的使用,您将需要获得直接从版权所有者的许可。查看本许可证的副本,访问gydF4y2Bahttp://creativecommons.org/licenses/by/4.0/gydF4y2Ba。gydF4y2Ba
关于这篇文章gydF4y2Ba
引用这篇文章gydF4y2Ba
Pollina说道,电子艺界,Gilliam, D.T., Landau, A.T.et al。gydF4y2BaDNA修复NPAS4-NuA4复杂的夫妇突触活动。gydF4y2Ba自然gydF4y2Ba614年gydF4y2Ba,732 - 741 (2023)。https://doi.org/10.1038/s41586 - 023 - 05711 - 7gydF4y2Ba
收到了gydF4y2Ba:gydF4y2Ba
接受gydF4y2Ba:gydF4y2Ba
发表gydF4y2Ba:gydF4y2Ba
发行日期gydF4y2Ba:gydF4y2Ba
DOIgydF4y2Ba:gydF4y2Bahttps://doi.org/10.1038/s41586 - 023 - 05711 - 7gydF4y2Ba
评论gydF4y2Ba
通过提交评论你同意遵守我们的gydF4y2Ba条款gydF4y2Ba和gydF4y2Ba社区指导原则gydF4y2Ba。如果你发现一些滥用或不符合我们的条件或准则请国旗是不合适的。gydF4y2Ba