文摘
为了应对持续的全球大流行,描述新的冠状病毒的分子水平上的主机交互SARS-CoV-2负责COVID-19前所未有的科学关注的中心。然而,当病毒进入人体也已经存在于宿主与微生物的相互作用。理解virus-host-microbiome相互作用可以产生额外的洞察生物过程扰动由病毒入侵。改变肠道微生物物种和代谢物指出在呼吸道病毒感染,可能影响肺部通过gut-lung微生物相声。为了更好地描述微生物功能在COVID-19下呼吸道感染,我们执行一个功能之前发表metatranscriptome测序数据的分析支气管肺泡灌洗液从八COVID-19情况下,25个社区获得性肺炎患者和20个健康对照。造成功能配置比较序列对微生物蛋白质域注释清晰分离群体。通过检查相关的代谢途径,区分功能签名COVID-19呼吸道微生物识别,包括脂质代谢潜力降低,多糖的生物合成和代谢途径,并增加潜在的碳水化合物代谢途径。先前的研究结果包括重叠在COVID-19微生物,包括减少粘多糖降解途径和增加碳水化合物的新陈代谢。结果也暗示小说联系考虑,可能是特定于下呼吸道微生物,呼吁进一步研究微生物功能和在SARS-CoV-2 host-microbiome交互感染。
介绍
一个令人印象深刻的科学研究快速发表呼吸道冠状病毒的基因组学和分子水平上主机交互SARS-CoV-21报告的蝙蝠起源2、负责COVID-19疾病大流行。除了描述病毒感染和宿主反应的过程3,理解主机内的微环境的变化可以产生进一步洞察摄动的生物过程4及其与疾病风险因素5。肠道和肺器官密切相关,通过免疫协调它们之间互相影响和微生物有一个核心作用在塑造正常和病理的免疫反应6。Microbiome-mediated相声沿着gut-lung轴在肺部感染特别指出由于改变肠道微生物物种和代谢物7,8。肠道微生物群的一个关键的角色在肺免疫和宿主的防御病毒性呼吸道感染;目前的证据表明SARS-CoV-2感染改变肠道屏障,导致的系统性传播细菌,木糖醇,微生物代谢产物9。有人建议,一个循环之间SARS-CoV2感染、系统性炎症,破坏了肠道屏障完整性和微生物易位导致COVID-19严重性10。
呼吸在SARS-CoV-2微生物感染也在接受调查1,11,12,13。先前的研究在其他病原体感染呼吸道微生物检验predictivity临床结果,以及相关的潜在益生菌干预措施14,15,16,17,18。口咽的微生物的研究,减少微生物多样性和高失调严重COVID-19患者住院观察,与微生物基因和代谢途径的丧失19。它也表明SARS-CoV-2引起微生物组鼻咽样本中存在明显的变化20.。上呼吸道被追究其他病原体和SARS-CoV-2合并感染21微生物群,而改变其一直在观察COVID-19患者和与死亡率相关22。
为了更好地理解在COVID-19下呼吸道微生物的作用,我们介绍一个功能分析,而不是分类命名,从一组metatranscriptomes支气管肺泡灌洗液(BALF) COVID-19病人,健康受试者,社区获得性肺炎(CAP)的病例11。而沈et al。11专注于SARS-CoV-2基因组和微生物的分类分析,这里我们执行全球功能分析来描述改变呼吸道微生物的生物过程。我们的蛋白质域集中氨基酸匹配方法支持微生物功能的分析由已知和潜在的未知生物尚未为特征23。这里介绍的比较分析旨在强调一致的差异COVID-19病人和健康的社区获得性肺炎控制相比,微生物样品。
结果
功能分析框架
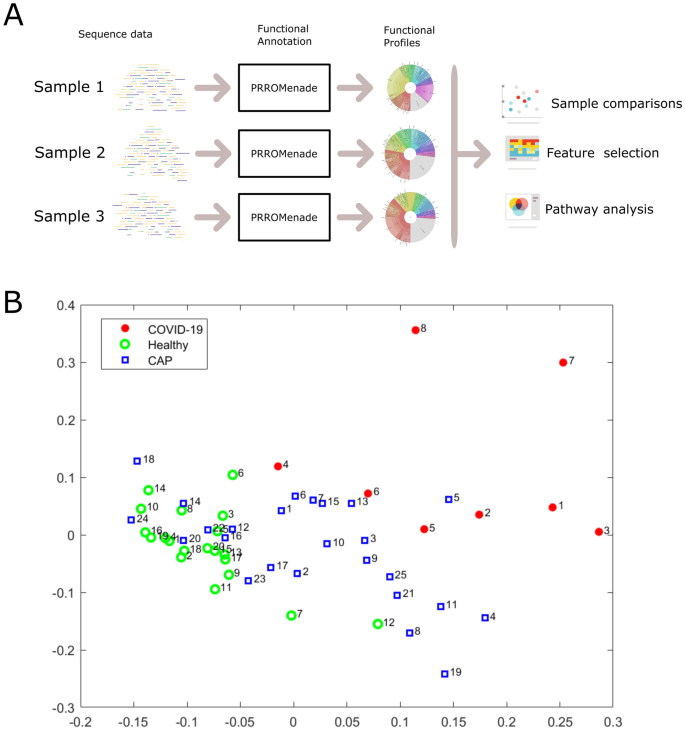
总体分析工作流图中描述。1答:总RNA序列读取第一次修剪和过滤,其次是翻译和与PRROMenade功能分类24对一个巨大的2100万细菌和病毒蛋白质的氨基酸序列集合域从IBM平台功能基因组学25、注释和KEGG酶编码(EC)从一个相应的功能层次结构26(见补充图。S1对过滤结果)。PRROMenade曾被应用于肠道的功能注释24和土壤微生物27。后处理和健壮rank-based马术竞技会28投影一个统一的规模使生成的执行类似的功能配置。
微生物功能配置集群队列
虽然个体功能配置不同,一个健壮的比较分析揭示了特定功能之间不断地改变军团(补充文件S1显示了一个克朗29日每个样品)的可视化。读计数功能层次各级分配(补充图。S2)被下推到叶水平,和非常低的丰富特性被随后的分析(见方法)。
多维定标样品分离之间的两两枪兵的距离COVID-19队列,而帽样品位于之间的健康和COVID-19样品(图。1B)。一个重要的区别功能COVID-19之间的观察资料,帽,和健康控制军团根据PERMANOVA测试(\ (le 0.0001 p \ \))。功能分析分离群体与类似的分数分类分析(功能分析\ (R ^ 2 = 0.06 \)与分类分析沈et al。11\ (R ^ 2 = 0.07 \))。
丰富的功能区分不同COVID-19样本
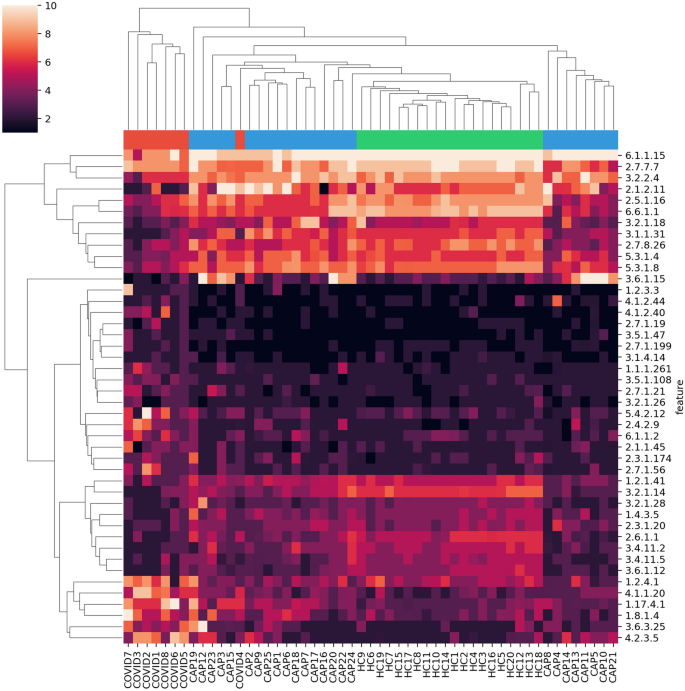
RNA序列数据有不同数量的读取和人类内容/样本(补充图。S1)。因此我们使用竞技28项目功能概要文件到一个健壮的统一的规模。检查COVID-19最不同的特性与其他军团,我们提取30顶级特性从COVID COVID与帽比较和与健康对照组比较。然后我们考虑的特性集,导致44 EC特性。
当聚类样本使用顶部差异化特性,COVID-19样本分组在一起,独立于其他军团,除了样本4(图。2)。同时检查了44个特性被选为区分COVID-19帽和健康对照组,他们还把健康控制所有其他样本;健康对照组集群紧密联系在一起。研究结果还表明,样品不仅仅集群的总数输入读取或微生物读取功能注释的一部分,因为这些措施在不同人群(补充图。S1)。帽病人样本医院收集来自不同来源,当前大流行之前,并代表肺炎病例与各种病毒测序数据中发现11(如肠病毒、流感病毒、鼻病毒),可能导致更大的可变性之间的微生物功能概要。
COVID-19样品有更多丰富的电子商务功能,包括(见左下功能集群在无花果。21.2.4.1“丙酮酸脱氢酶”,4.1.1.20 Diaminopimelate脱羧酶,1.17.4.1 Ribonucleoside-diphosphate还原酶,1.8.1.4 Dihydrolipoyl脱氢酶,3.6.3.25“Sulfate-transporting atp酶”,和4.2.3.5 Chorismate合成酶,与各种氨基酸、碳水化合物、能量,核苷酸代谢通路。EC 4.1.1.20也发现增加metaproteome COVID-19呼吸道微生物的研究30.。补充图。S3包括一个散点图的平均变化/ EC COVID-19帽和健康人群相比,突出异常值。
改变肺部微生物在COVID-19路径表示
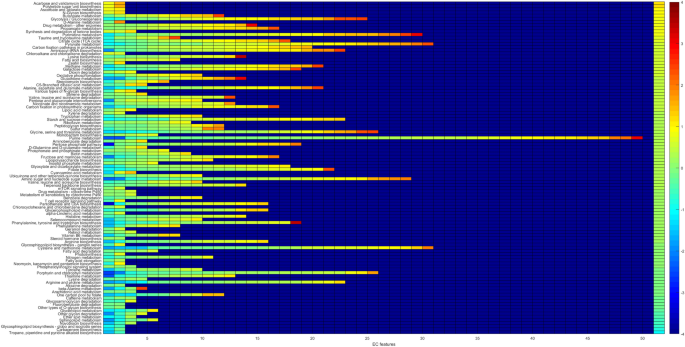
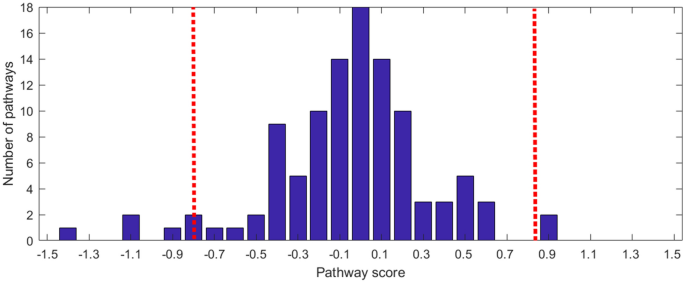
为了系统地检查检测功能对功能通路,所有欧共体特性被认为是对相应的途径从KEGG代谢途径的映射26。途径得分(平均丰度变化COVID-19)计算每个通路使用所有发现电子商务功能,见图。3。确定外围通路分数(高或低相比,观察到分布),平均绝对偏差(疯了)31日分散,一个健壮的测量是利用,见图。4。最微分途径如表所示1。
在COVID-19途径降低(表1)几个有关多糖生物合成和代谢(如其他多糖降解)和脂质代谢(如鞘脂类代谢)。鞘脂类是生物膜的重要组成部分,调节信号转导和免疫激活过程,他们已被证明减少COVID-19病人血清32。功能3.2.1.22 alpha-galactosidase (alpha-gal),低COVID-19,与几个下降通道的表1:鞘糖脂biosynth。——环球和isoglobo系列、鞘脂类代谢和glycerolipid新陈代谢。它最近被推测,菌群失调COVID-19患者的观察与减少alpha-gal含有共生的细菌的微生物群,或者个人alpha-gal含量较高的微生物群可能不太容易COVID-19,由发现anti-alpha-gal之间负相关抗体增高,以及脑部COVID-19疾病严重程度33。在其他地方,提高anti-alpha-gal滴度的人口免疫对灭活无害的细菌,港口alpha-gal抗原表位34。这里我们另外确定粘多糖降解为减少COVID-19样品(图。3),而减少之间的连接的主机粘多糖硫酸乙酰肝素修饰细菌和COVID-19易感性增加35。
通路中较高COVID-19几种碳水化合物代谢有关,如糖酵解/糖质新生(表1)。增强微生物碳水化合物代谢的能力(从fructose-6-phosphate糖酵解II)曾表示在粪便样本的签名SARS-CoV-2传染性高,以及减少细菌产生大量的短链脂肪酸36。
讨论
据报道,主持人微生物群组成反映了COVID-19患者的疾病严重程度和不正常的免疫反应,而肠道微生物可能参与宿主炎症反应的调制37。增加在某些机会致病菌与高SARS-CoV-2传染性报道36以及在COVID-19损耗与已知的免疫调节潜在的细菌37。总的来说,损失的多样性与COVID-19有关微生物,包括肠道和上呼吸道19,38。进一步了解微生物功能的下呼吸道,我们调查COVID-19差异和健康与社区获得性肺炎(CAP)支气管肺泡灌洗液metatranscriptomes。
这种比较研究的微生物功能旨在减轻可能的实验样本个体内变异和产生的偏见,通过专注于检测健壮的和一致的差异。我们的框架包括阅读过滤、功能注释蛋白质域数据库和酶层次,功能丰富的投影相对规模,最后代谢途径得分表明区分功能潜力COVID-19微生物相比,健康和帽样品。结果,我们确定了酶代码特性和代谢途径区分COVID-19呼吸道微生物。由此产生的区分功能配置COVID-19样本,类似于原始taxonomy-based社区成员的分析11。
差异丰富呼吸道微生物特性和相关通路识别匹配结果从先前的报道,有关微生物的功能capcacity的变化,如减少脂质代谢和多糖生物合成和代谢32碳水化合物代谢,增加36。我们的研究结果也与其他微生物的特性与COVID-19有关33,34,35。降低途径包括鞘脂类代谢;鞘脂类可以调解免疫激活流程,并已被证明减少COVID-19病人血清32。此外,与糖胺聚糖降解途径,减少之间的联系存在主机粘多糖硫酸乙酰肝素修饰细菌和增加COVID-19易感性最近建议35。减少alpha-galactosidase (alpha-gal),这与几个途径减少COVID-19,一直连接到微生物生态失调在COVID-19或者更高的易感性疾病对个人alpha-gal含量较低的微生物群33。我们还发现增加碳水化合物代谢潜力,曾被增加SARS-CoV-2在粪便微生物的存在36。这个分析的结果要求进一步深入研究微生物功能和在SARS-CoV-2 host-microbiome交互感染,包括调查潜在的益生菌,可以用来改善临床结果39。
当前研究的局限性包括小样本大小和稀疏的临床资料。因此结果可能受到抽样总体变异微生物,可能由于受到生活方式,地点,和临床特点包括不同阶段和疾病严重程度。然而,丰富的和平衡的病例对照数据并不总是可用在实践中,特别是有关当前快速发展的大流行。然而,计算研究可以使用可用的宝贵的数据开始解开变异virus-host-microbiome连接。在这项研究中强有力的下呼吸道微生物的功能潜力的差异被发现COVID-19和健康对照组之间,社区获得性肺炎。此外,检查metatranscriptome测序读这个比较功能注释框架可以产生额外的洞察微生物变化也在其他疾病。
方法
序列数据和功能的数据库
最近出版的支气管肺泡灌洗液(BALF) metatranscriptomic测序数据118 COVID-19患者,20名健康对照组(HC)和25例社区获得性肺炎(CAP)是获得国家基因组数据中心(加入PRJCA002202)40。预处理包括TrimGalore41适配器和质量调整(长度50 -trim-n-max_n 10)和多聚腺苷酸与BBduk削减执行42(trimpolya = 10,最小长度= 50)。阅读对人类(GCF_000001405.39)过滤,PhiX测序控制(GCF_000819615.1),并与BBsplit SARS-CoV-2病毒(NC_045512.2)42(模糊=随机,ambiguous2 =分裂)。成对读取单独处理,不符合人类的个别读,PhiX或SARS-CoV-2基因组(278 k到50.7读取/样本)保留了微生物群落功能注释(见补充图。S1筛选结果)。
KEGG酶命名(EC)引用层次结构26被用作功能性注释树。欧盟数字定义一个四层的层次结构。例如,1.5.1.3。= "二氢叶酸还原酶”是第四个(叶)水平与顶级代码1 =“氧化还原酶”,通过1.5。= "作用于CH-NH捐助者”和1.5.1 =“与NAD +或辅酶ii +受体”。一个PRROMenade24使用KEGG数据库搜索指数构造层次结构,总共21.2细菌和53 k病毒带注释的蛋白质域序列(最小长度的5 AA),获得了6月6日,2020年从IBM平台功能基因组学25(以前称为OMXWare)。早先发布的细菌域数据一直在前面讨论结合PRROMenade索引24。
功能注释和分析
Metatranscriptomic测序读注释了PRROMenade定位的最大长度为每个读取精确匹配,和加工如前所述24。最小匹配长度截止11 AA(对应于33元)。分类(根)读计数(每样6.8 k到11.5,看到补充图。S1- - - - - -S2)进行后期处理总结的叶级别的计数功能的层次结构。叶节点的贡献\(通用电气\ 0.05 \ % \)总带注释的读入的至少一个样品被保留,导致633年叶节点包含的特性功能概要。多维标度(cmdscale Matlab函数,\ (p = 2 \))和置换多元方差分析(f_permanova,\ \ (iter = 100000)从理解工具43Matlab)应用于两两枪兵的距离(图。1B)。
随后,竞技的档案处理28(\ (P = 10 \),\ \(我= 100),\ (R = 10 ^ 7 \)健壮的可比性。每个样本参数\ (P ' \)确定根据注释读如前所述的数量(在补充文件吗2克洛斯et al。44)。一个两个示例Kolmogorov-Smirnov测试(在Matlab kstest2)应用于识别不同丰富的COVID-19样本之间的特征和帽,健康控制样品。功能被假定值命令和功能选择平均使用欧氏距离(图链接层次聚类。2)。
路径分析
的KEGG26代谢途径与途径,利用地图链接功能被COVID-19之间变化的途径进行了分析和帽,HC。平均丰度变化的途径进行评估如下。让\ \ (a_i)是指竞技丰富的电子商务功能我COVID-19样本,\ (b_i \)帽样品,\(为c_i \)HC的样本。被定义为功能分数\ (fs_i = ((ai - b_i) + (ai -为c_i)) / 2 \)、积极的价值观表示丰富COVID-19高。途径得分\ (ps_j =意味着\ {fs_ {EC_j (1)}, fs_ {EC_j (2)}, \ ldots fs_ {EC_j (k)} \} \)计算使用的特性,\ (EC_j \)映射到路径j(只考虑路径\ (k \通用电气2 \))。途径得分分布被规范化为可视化的意思是零。
平均绝对偏差(疯了)31日一个健壮的离差的量度,是用来识别异常值的观测途径得分分布(在Matlab isoutlier参数值)。使用默认参数,局外人是定义为一个值,超过三个比例平均绝对偏差的值。
引用
周,P。et al。与一种新的冠状病毒肺炎爆发的可能的起源。自然579年,270 - 273 (2020)。
安徒生,k . G。兰姆伯特,。,Lipkin, W. I., Holmes, E. C. & Garry, R. F. The proximal origin of SARS-CoV-2.Nat,地中海。26,450 - 452 (2020)。
张,H。et al。Metatranscriptomic冠状病毒疾病的描述2019年确定了主机转录分类器与免疫相关的信号。临床感染疾病(2020)。https://doi.org/10.1093/cid/ciaa663。
Aguirre加西亚,M . M。,Mancilla-Galindo, J., Paredes-Paredes, M., Tiburcio, A. Z. & Ávila Vanzzini, N. Mechanisms of infection by SARS-CoV-2, inflammation and potential links with the microbiome.未来的病毒学16(1)43-57 (2021)。
陈,J。,Hall, S. & Vitetta, L. Altered gut microbial metabolites could mediate the effects of risk factors in Covid-19.启地中海性研究。e2211 (2021)。https://onlinelibrary.wiley.com/doi/10.1002/rmv.2211。
Ahlawat, s & Sharma k . k .肠道免疫之间的协调和肺SARS-CoV-2感染。病毒Res。286年198103 (2020)。
Srinath B。,Shastry, R. & Kumar, S. Role of gut-lung microbiome crosstalk in COVID-19.生物医学》。Eng。627年1 - 11 (2020)。
杨,T。et al。无菌的老鼠显示,肠道微生物群调节结肠Ace2的信使rna, SARS-CoV-2传染性的受体。高血压76年e1-e3 (2020)。https://doi.org/10.1161/HYPERTENSIONAHA.120.15360
Sencio, V。,Machado, M. G. & Trottein, F. The lung-gut axis during viral respiratory infections: the impact of gut dysbiosis on secondary disease outcomes.粘膜Immunol。4,(2021)。https://doi.org/10.1038/s41385 - 020 - 00361 - 8。
形坝,l . B。et al。严重COVID-19受破坏肠道屏障的完整性。medRxivhttps://doi.org/10.1101/2020.11.13.20231209(2020)。
沈,Z。et al。基因组的多样性严重急性呼吸道syndrome-coronavirus 2冠状病毒疾病患者2019。中国。感染。说。71年(15),713 - 720 (2020)。https://doi.org/10.1093/cid/ciaa203。
陈,L . L。et al。基于RNA的西班牙芒果方法识别人类冠状病毒小说从两个人肺炎病例2019年武汉爆发。紧急情况。微生物感染。9,313 - 319 (2020)。
吴,F。et al。一种新的冠状病毒与人类呼吸道疾病在中国。自然579年,265 - 269 (2020)。
Hanada音,S。,Pirzadeh, M., Carver, K. Y. & Deng, J. C. Respiratory viral infection-induced microbiome alterations and secondary bacterial pneumonia.前面。Immunol。92640 (2018)。
门德斯,R。,Banerjee, S., Bhattacharya, S. K. & Banerjee, S. Lung inflammation and disease: a perspective on microbial homeostasis and metabolism.IUBMB生活71年,152 - 165 (2019)。
迪克森r P。et al。肺部微生物群预测危重病人的临床结果。点。j .和。暴击。保健医疗。201年,555 - 563 (2020)。
Zolnikova, O。Komkova,我。,Potskherashvili, N., Trukhmanov, A. & Ivashkin, V. Application of probiotics for acute respiratory tract infections.斜体字。j .地中海。1232-38 (2018)。
法诺,V。,Pintus, M. C., Pintus, R. & Marcialis, M. A. Lung microbiota in the acute respiratory disease: from coronavirus to metabolomics.j . Pediatr。Neonat。个人的地中海。9e090139 (2020)。
de Castilhos J。et al。COVID-19严重程度和并发症低多样性,生态失调和预测metagenome口咽微生物的特点。预印https://doi.org/10.21203/rs.3.rs-127621/v1(2021)。
Mostafa, H . H。et al。宏基因组下一代测序证实的鼻咽样本收集和怀疑COVID-19病人。mBio11(6)、e01969-20 (2020)。https://doi.org/10.1128/mBio.01969-20。
周,H。et al。总infectomes 162 SARS-CoV-2情况下使用meta-transcriptomic测序。j .感染。82年(1)E44-E48 (2021)。
任,L。et al。上呼吸道微生物群的动态及其与COVID-19患者的病死率。预印。https://doi.org/10.2139/ssrn.3719095(2020)。
考夫曼,j . H。et al。岛microbiogeography:三个病原体作为范本。咕咕叫。摩尔。生物问题。36,89 - 108 (2020)。
Utro F。et al。等级标记数据库索引允许可伸缩特性的微生物。iScience23(4),100988 (2020)。
Seabolt E。et al。IBM功能基因组学平台,基于云计算平台研究微生物在规模。在IEEE / ACM事务计算生物学和生物信息学(2020)。
Kanehisa, M。,Furumichi, M., Tanabe, M., Sato, Y. & Morishima, K. KEGG: new perspectives on genomes, pathways, diseases and drugs.诊断。酸Res。45D353-D361 (2017)。
加德纳,L.-J。et al。重新设计软件功能微生物的特性。微生物组94 (2021)。https://doi.org/10.1186/s40168 - 020 - 00971 - 1。
Haiminen, N。et al。盐胁迫下比较exomics Phalaris品种。BMC染色体组。15 5 6S18,美国(2014年)。
Ondov B。,Bergman, N. & Phillippy, A. Interactive metagenomic visualization in a web browser.BMC Bioinform。12385 (2011)。https://doi.org/10.1186/1471 - 2105 - 12 - 385。
马拉什,j·S。et al。Multi-omics呼吸道标本特征的集成分析基线分子决定因素与COVID-19诊断。medRxivhttps://doi.org/10.1101/2020.07.06.20147082(2020)。
草地,C。,Ley, C., Klein, O., Bernard, P. & Licata, L. Detecting outliers: Do not use standard deviation around the mean, use absolute deviation around the median.j . Exp。Soc。Psychol。49,764 - 766 (2013)。
沈,B。et al。蛋白质组学和代谢组学特征COVID-19病人血清。细胞182年59 - 72。e15 (2020)。
Urra, j . M。et al。多糖的抗体反应\α(\ \)加与COVID-19疾病症状。j .地中海性研究。93年,2065 - 2075 (2021)。https://doi.org/10.1002/jmv.26575。
Breiman,。,Ruvën-Clouet, N. & Le Pendu, J. Harnessing the natural anti-glycan immune response to limit the transmission of enveloped viruses such as SARS-CoV-2.公共科学图书馆Pathog。161 - 4 (2020)。
马蒂诺,C。et al。细菌修改主机粘多糖的硫酸乙酰肝素调节SARS-CoV-2传染性。bioRxivhttps://doi.org/10.1101/2020.08.17.238444(2020)。
左,T。et al。描绘SARS-CoV-2粪便病毒活动协会COVID-19患者肠道微生物群组成。肠道70年,276 - 284 (2021)。https://doi.org/10.1136/gutjnl - 2020 - 322294。
杨紫琼,y K。et al。肠道微生物群组成反映了疾病的严重程度和功能失调的COVID-19患者的免疫反应。肠道https://doi.org/10.1136/gutjnl - 2020 - 323020(2021)。
与COVID-19 Villapol, s .胃肠道症状:对肠道微生物的影响。Transl。Res。226年57 - 69 (2020)。
Santacroce, L。et al。潜在的有益作用的益生菌在COVID-19病人的结果:一个不断发展的视角。糖尿病金属底座。Syndr。中国。牧师》。15,295 - 301 (2021)。
国家基因组数据中心成员和伙伴。数据库资源的国家基因组数据中心在2020年。诊断。酸Res。48D24-D33 (2020)。
克鲁格,f . TrimGalore。https://github.com/FelixKrueger/TrimGalore。
布什内尔,b . BBtools。https://sourceforge.net/projects/bbmap/。
琼斯,d . l .理解为MATLAB工具箱:多元生态和海洋数据分析软件。https://www.usf.edu/marine-science/research/matlab-resources/index.aspx/(2017)。
克洛斯,M。et al。转录组特征和差异表达基因在生物质草Phalaris洪水和干旱胁迫下季型和Dactylis glomerata。安。机器人。124年,717 - 730 (2019)。
作者信息
作者和联系
贡献
新罕布什尔州和F.U.进行实验、分析结果和写的手稿。静电的IBM功能基因组学提供参考的数据平台。n . h和石油醚构思研究和分析结果。所有作者回顾了手稿。
相应的作者
道德声明
相互竞争的利益
PRROMenade方法与在美国专利商标局专利申请正在等待审核。
额外的信息
出版商的注意
施普林格自然保持中立在发表关于司法主权地图和所属机构。
权利和权限
开放获取本文是基于知识共享署名4.0国际许可,允许使用、共享、适应、分布和繁殖在任何媒介或格式,只要你给予适当的信贷原始作者(年代)和来源,提供一个链接到创作共用许可证,并指出如果变化。本文中的图片或其他第三方材料都包含在本文的创作共用许可证,除非另有说明在一个信用额度的材料。如果材料不包括在本文的创作共用许可证和用途是不允许按法定规定或超过允许的使用,您将需要获得直接从版权所有者的许可。查看本许可证的副本,访问http://creativecommons.org/licenses/by/4.0/。
关于这篇文章
引用这篇文章
Haiminen, N。Utro F。,Seabolt E。et al。COVID-19呼吸道微生物的功能分析。Sci代表116433 (2021)。https://doi.org/10.1038/s41598 - 021 - 85750 - 0
收到了:
接受:
发表:
DOI:https://doi.org/10.1038/s41598 - 021 - 85750 - 0
本文引用的
分析支气管肺泡灌洗液中metatranscriptomes COVID-19疾病患者
科学报告(2022)
分析的时空演化特征和聚合趋势COVID-19早期在中国大陆
科学报告(2022)
协会的肠道微生物群与炎症性肠病和COVID-19严重程度:一个可能的结果改变免疫应答
目前微生物学(2022)
标准化multi-omics地球的微生物揭示微生物和代谢产物的多样性
微生物学性质(2022)