文摘
小球藻sp。TLD 6 b,微藻生长在塔克拉玛干沙漠,中国的新疆,是一个很好的模型材料研究植物的生理和环境适应机制在干旱的栖息地,它适应严酷的沙漠环境导致其强劲的阻力。然而,当使用实时定量聚合酶链反应(RT-qPCR)来分析这种藻类的基因表达在非生物胁迫下,至关重要的是找到合适的内生参考基因获得可靠的结果。本研究评估了9内生的参考基因表达稳定小球藻sp。TLD 6 b四非生物胁迫(干旱、盐、冷和热)。这些基因是根据分析结果选择计算的三个算法程序geNorm, NormFinder,通过精炼和BestKeeper排名。我们的研究表明,18岁和三磷酸鸟苷在干旱胁迫下,18岁和IDH在盐胁迫下,CYP和18岁冷应激下,三磷酸鸟苷和IDH在热应力下最稳定的内生参考基因。此外,哥伦比亚大学和18岁是最合适的内生参考所有样本的基因组合。相比之下,GAPDH和α-TUB两个最不稳定内源基因在所有实验样品参考。此外,所选择的基因已经被证实是耐用和可靠的检测圆荚体和PXG3使用上面的内生参考基因的基因。可靠的内生参考基因的识别担保更准确RT-qPCR量化小球藻sp。TLD 6 b,促进功能基因组学的研究沙漠小球藻以及抗性基因的挖掘。
介绍
藻类广泛分布于淡水、海水、潮湿的土壤、沙漠和极端环境。订单微藻生物能源被广泛应用和研究,医疗、废水处理和食物1,2,3。沙漠和干旱的土地覆盖了三分之一的地球陆地表面,在生理上具有挑战性的生态系统。微藻是一个重要的组成部分在世界不同地区的沙漠biocrusts4,5,6,7,适应沙漠微藻严酷的沙漠环境已经导致了自适应机制的多样性(包括生态、生理、形态结构、遗传、等等)。沙漠比淡水藻类和藻类光合效率更高更强的抗干旱、盐、紫外线(UV)和极端温度8,9,10,11,12。因此,沙漠微藻是更好的材料为研究生物和环境适应机制和矿业抗性基因。小球藻sp。TLD的单细胞绿藻6 b是一个孤立的从生物外壳在塔克拉玛干沙漠13。光合作用效率高的优点,压力阻力14。因此,重要的是要阐明快速增长的分子机制和压力适应的小球藻的开发利用和保护土壤沙漠化。基于上述原因,我们组生成一个完整的转录组数据库的小球藻sp。TLD 6 b使用实时(SMRT)单分子测序的组合(未发表)和Illumina公司测序15。
目前,基因表达的研究已经成为一个重要工具揭示基因功能和植物抗逆性分子机制。实时定量聚合酶链反应(RT-qPCR)已经变成了一个标准方法研究基因表达由于其灵敏度高,重现性、特异性和高吞吐量16,17,18,19。有效控制每个样本的初始模板之间的差异,确保RT-qPCR结果的可靠性,使用内源性参考标准化的基因分析20.,21,22,23是必须的。已经发现一些参考基因稳定表达的不同组织和不同的发展阶段,然而,他们表达稳定可以改变不同程度在治疗一些非生物压力24,25,26。目前,仍然没有内生参考基因,可以应用于多个物种,甚至同一物种,几乎没有任何参考基因普遍检查多种非生物压力治疗。为此,有必要对屏幕稳定内生参考基因在特定的物种。迄今为止,许多研究已经报道来区分这种基因在不同物种,如木荷27,Isodon得28,芒草sacchariflorus29日,碱蓬glauca30.,水松spp31日,Glehnia littoralis32。尽管一些论文33,34,35,36,37,38还研究了在藻类,这些参考基因微藻类物种之间的差异,这些基因不能直接用作参考基因沙漠小球藻研究其基因表达。因此,稳定的内生参考基因沙漠小球藻必须进一步研究筛查。
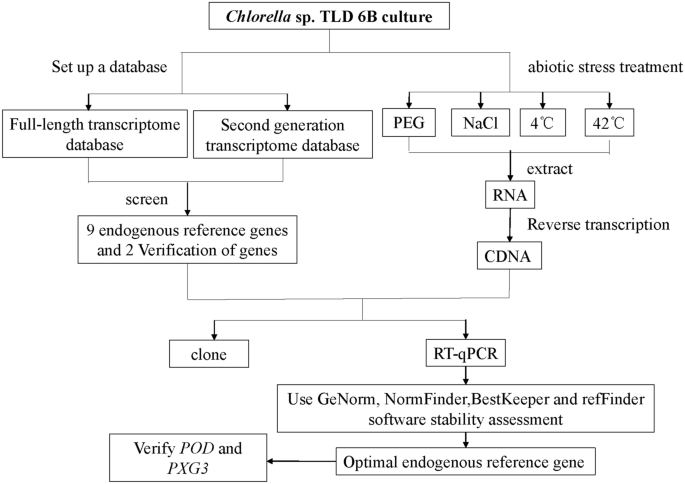
沙漠微藻类的基因信息是未知的,这阻碍了进一步研究基因的功能。在本文中,基于转录组数据15的小球藻sp。TLD 6 b和报告参考其他物种的基因,我们选择18 s rRNA (18岁),还有(CYP),延长因子1α(EF-1α),Glyceraldehyde-3-phosphate脱氢酶(GAPDH)、三磷酸鸟苷结合蛋白(三磷酸鸟苷),NADP-isocitrate脱氢酶(IDH),Ubiquitin-conjugating酶(哥伦比亚大学)、微管蛋白α链(α-TUB),β微管蛋白链(β-TUB)作为内生的参考基因39,40,41,42。过氧化物酶(圆荚体)43和Peroxygenase 3 (PXG3)44应力诱导基因用于验证上述基因在不同压力条件下的稳定性。为小球藻sp。TLD 6 b在干旱、盐、冷,热处理,我们使用GeNorm45,NormFinder46,bestkeeper47和RefFind48软件分析内生稳定性的参考基因(图。1)。可靠的内生参考基因选择,以确保更准确的RT-qPCR量化小球藻TLD 6 b。本研究不仅促进了小球藻的功能基因组学沙漠,也奠定了基础的探索抗性基因的分子机制小球藻沙漠sp.TLD 6 b适应极端环境。
结果
引物设计
比较和验证圆荚体,PXG3和9内生参考基因在NCBI,引物设计与底漆总理5根据RT-qPCR引物设计的原则(表1)。九个候选人参考基因的PCR产物被琼脂糖凝胶电泳检测,和每个基因获得一个特定的预期大小乐队(补充图。S1)。
内生参考基因的表达水平和变异
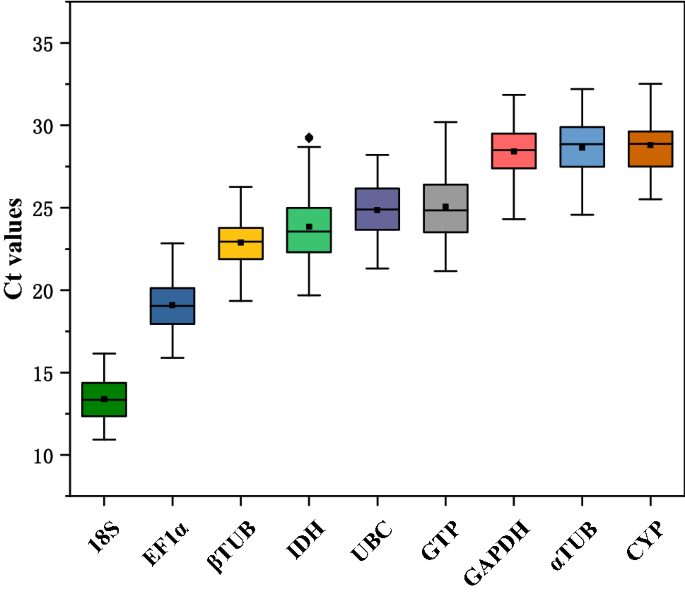
RT-qPCR进行检测9个基因的表达水平。结果表明,所有内生的Ct值参考基因在不同治疗范围从10.9 ~ 32.5(无花果。2),其中的平均Ct值18岁最低为13.4,最高的表达和变化范围(10.9 ~ 16.2)中内生参考基因。不过,最高的变异系数为9.7%。α-TUB,CYP和的平均Ct值α-TUB,CYP,GAPDH分别是28.6、28.8和28.4,最低的表达和变异系数为6.3,5.8和5.7%,分别GAPDH在所有样品中最小的变异系数。的平均Ct值EF1α,哥伦比亚大学,β-TUB,IDH分别为19.1、24.9、22.9和23.8。
内源性参考基因的稳定性评估使用GeNorm软件
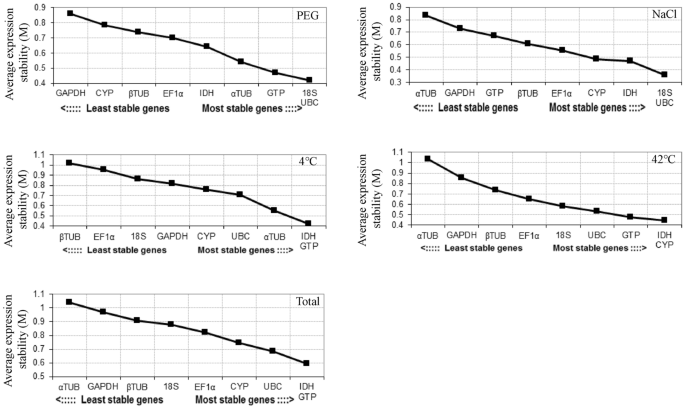
GeNorm计划是用来计算的稳定值(M值)基因表达的九个内生参考基因,这些基因和排名。M < 1.5作为阈值不包括稳定的基因,和M值越低,稳定性越高。根据这一标准,哥伦比亚大学和18岁是最稳定的内源性基因挂钩和生理盐水治疗的引用,三磷酸鸟苷和IDH是最稳定的内生参考在4°C基因治疗和所有的样品,CYP和IDH是最稳定的内生参考基因(图42°C治疗。3)。α-TUB和GAPDH是最不稳定的内生参考基因在氯化钠,42°C和总,β-TUB和EF1α是最不稳定的内生参考在4°C基因治疗,然后呢GAPDH和CYP是最不稳定的内生参考基因挂钩。geNorm计划计算基因表达稳定值(M值)和排名参考基因。
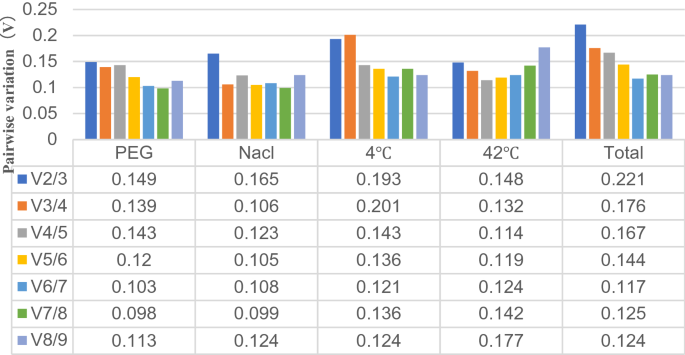
成对变异(Vn/ Vn + 1使用GeNorm)值计算软件程序来确定最优数量的内生需要参考基因中存在规范化目标基因表达水平。小V之间的变化n/ Vn + 1和Vn + 1/ Vn + 2表明添加另一个内生组织正常化参考基因没有明显的影响。Vn/ Vn + 1值为0.15的阈值被认为是决定是否添加一个内生基因被认为是阈值的引用。结果显示(图4V)2/3值低于0.15挂钩(0.149)和42°C(0.148),表明只有两个合适的内生需要参考基因挂钩和42°C的压力。V3/4氯化钠值低于0.15(0.106)和三个内生需要参考基因氯化钠的压力。然而,阈值为0.15不应该被认为是一个严格的标准,和一些报道发现更高的阈值Vn/ Vn + 143,44,45。数据显示V之间的轻微变化2/3(0.193)和V3/4(0.201)在4°C样品,表明三个内生基因是需要在4°C的压力。有轻微的变化总样本之间的V3/4(0.176)和V4/5(0.167),表明需要4内生参考基因在所有样本。
内源性参考基因的稳定性评估使用NormFinder软件
九个内生参考基因的稳定值计算使用NormFinder软件程序,较低的值代表更高的稳定性。三磷酸鸟苷是最稳定的挂钩(0.222)和42°C (0.165);IDH是最稳定的氯化钠(0.140);CYP最稳定在4°C (0.217);和哥伦比亚大学是最稳定的在所有样品(0.347。)是最稳定的(表吗2)。内生参考基因的稳定水平使用NormFinder略不同于生成使用GeNorm生成。内生参考基因是最稳定NormFinder分析挂钩,氯化钠,4°C, 42°C和总(三磷酸鸟苷,IDH,CYP,三磷酸鸟苷和哥伦比亚大学)的稳定第三(三磷酸鸟苷,IDH)、第五(CYP)和第三(三磷酸鸟苷,哥伦比亚大学分别在GeNorm分析。
使用BestKeeper内生参考基因的稳定性评价软件
使用BestKeeper Ct值计算软件对表达式求值的稳定性9内生参考基因。确定的原则是,相关系数越大,标准差和变异系数越小,内生参考基因的稳定性就越好,反之亦然,越稳定。在挂钩β-TUB(4.66±1.08)是最稳定的内生参考基因;在氯化钠和CYP(2.97±0.84)是最稳定的内生参考基因;在4°Cβ-TUB(3.84±0.91)是最稳定的内生参考基因;在42°C和总18岁(6.82±0.86,7.79±1.04)是最稳定的内源性基因(表的引用3)。18岁各治疗排名第一,是一个相对稳定的内生参考基因α-TUB是排名第二的内生参考基因治疗是一种相对不稳定。由于各种压力,产生的内源性稳定排名的参考基因BestKeeper不同于GeNorm NormFinder。
排名内源性基因使用RefFinder软件的引用
RefFinder软件程序是用于确定内生的整体排名参考基因。程序集GeNorm、NormFinder, BestKeeper和△Ct方法。排名顺序下钉治疗:18岁>三磷酸鸟苷>哥伦比亚大学>IDH>β-TUB>EF1α>CYP>α-TUB>GAPDH。在生理盐水治疗:18岁>IDH>哥伦比亚大学>CYP>三磷酸鸟苷>EF1α>β-TUB>GAPDH>α-TUB。在4°C下治疗CYP>18岁>哥伦比亚大学>三磷酸鸟苷>IDH>β-TUB>α-TUB>EF1α>GAPDH。在42°C,排序顺序是:三磷酸鸟苷>IDH>18岁>CYP>哥伦比亚大学>EF1α>β-TUB>GAPDH>α-TUB。治疗,排序顺序是:哥伦比亚大学>18岁>CYP>三磷酸鸟苷>EF1α>IDH>β-TUB>GADPH>α-TUB(表4)。18岁是最稳定的挂钩和氯化钠;CYP是最稳定在4°C;三磷酸鸟苷是最稳定的42°C;哥伦比亚大学在所有样品是最稳定的。的α-TUB和GAPDH在所有的压力不稳定的治疗方法。
目标基因表达和内源性参考基因验证
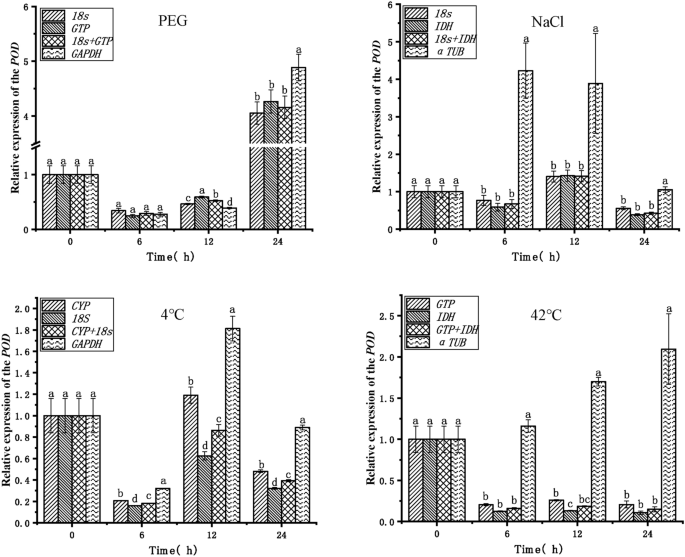
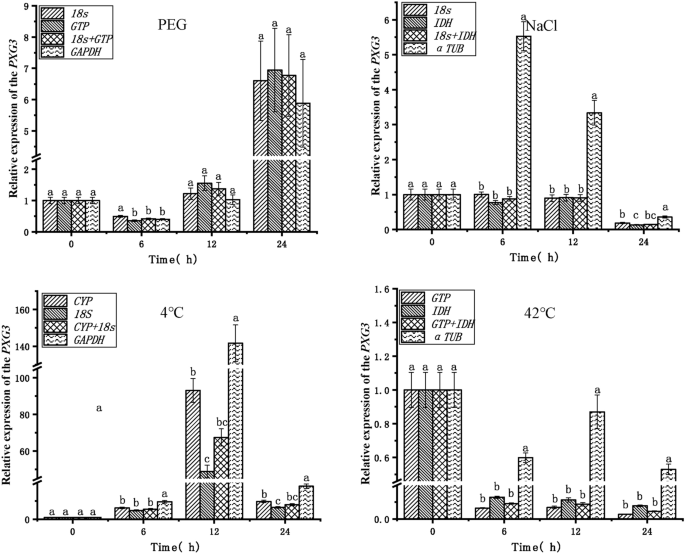
验证的可靠性内生参考基因在上面的分析中,获得目标基因的表达模式圆荚体和PXG3分析了挂钩、氯化钠、4°C,和42°C压力治疗(无花果。5,6)。的top two stable endogenous reference genes (18岁,三磷酸鸟苷)、内源性参考基因的组合(18岁+三磷酸鸟苷),最稳定的内生参考基因(GAPDH)挂钩的压力被用于规范化分析,分别。目标基因的表达趋势圆荚体和PXG3是一致的,最高的表达式在24 h。的表达吗圆荚体基因在12 h和24 h时明显不同GAPDH是使用18岁+三磷酸鸟苷和18岁,三磷酸鸟苷分别作为内生的参考基因。最稳定的内生参考基因(18岁,IDH)、内源性参考基因的组合(18岁+IDH),最稳定的内生参考基因(α-TUB氯化钠)被用于规范化分析压力,分别。目标基因的表达圆荚体和PXG3显示一致的趋势和无显著差异基因在表达内源性参考18岁,IDH,18岁+IDH(除了PXG3在24 h)。然而,的表达趋势圆荚体和PXG3时不一致的α-TUB作为一个内生参考基因18岁,IDH,18岁+IDH分别在6 h,表情明显不同,12 h和24 h。最高的内生参考基因稳定排名(CYP,18岁)、内源性参考基因的组合(CYP+18岁),最稳定的内生参考基因(GAPDH)被用于规范化分析冷应激在4°C,分别。目标基因圆荚体表达趋势不一致的除了在12 h。目标基因的表达趋势圆荚体和PXG3在其他时间点是一致的;与此同时,的表达圆荚体和PXG3明显不同的GAPDH作为一个内生参考基因18岁,IDH,18岁+IDH,分别。内生参考基因稳定排名第一(三磷酸鸟苷,IDH)、内源性参考基因的组合(三磷酸鸟苷+IDH)和最稳定的内生参考基因(α-TUB)用于规范化分析热应力在42°C,分别;目标基因圆荚体表达趋势不一致在6 h, 12 h和24 h。和表达的趋势PXG3是一致的。与18岁,IDH,18岁+IDH目标基因的表达趋势圆荚体和PXG3是一致的,没有显著差异表达(除了吗圆荚体在12 h)。此外,的表达圆荚体和PXG3明显不同的α-TUB作为一个内生参考基因三磷酸鸟苷,IDH,三磷酸鸟苷+IDH,分别。
讨论
使用稳定的内生参考基因在不同压力条件下正确的分析是至关重要的,演讲中,基因表达和解释。我们这里使用常用的内源性基因的稳定性分析参考基因筛查软件geNorm NormFinder, Bestkeeper和RefFinder软件来确定最好的内生参考基因小球藻在不同的压力条件下sp。TLD 6 b。结果表明,这些基因的稳定性不同在不同的软件评估。
分析与geNorm NormFinder, Bestkeeper水、盐、低温和高温应力,分别显示的排名三磷酸鸟苷和β-TUB是非常不同的,尤其是规模Bestkeeper geNorm和NormFinder。这种差异主要是由这三种方法造成的45,46,47。我们还发现,大多数基因geNorm和NormFinder排名几乎相同,主要是由于geNorm的类似的操作原则和NormFinder45,46。在这方面,数据从GeNorm NormFinder和BestKeeper综合评估与RefFinder软件滤波器稳定的内生参考基因或基因组的合作24,49。此外,GeNorm决定所需的最优基因的数量基于Vn/ Vn + 1值50,51,52。GeNorm已经利用这一特性在大多数研究确定内生参考基因的最佳数量。在这个实验中,它被认为是两个基因在干旱和42°C治疗需要,而三个内生参考基因所需的生理盐水和4°C的治疗。
这些内生参考基因在这个实验中显示不同的表达式在各种压力下稳定治疗。其中,18岁,三磷酸鸟苷,IDH和CYP及它们的组合是最稳定的内源性基因(表的引用4)。几个基因已经被证明是很好的稳定的样品,包括18岁53,54,IDH55,56,CYP57,58。此外,实验结果表明三磷酸鸟苷可以作为一个稳定的结果与赵相反的结果呢41;GAPDH和α-TUB是最不稳定的基因在不同压力在目前的实验,但是是最稳定的参考一些内源性参考基因研究报道吗59,60,61年,这是一个迹象表明物种或实验条件的差异导致独特的基因,因此,选择合适的样本在不同压力条件下实现可靠的实验结果是必要的。干旱胁迫下GAPDH的显著差异蛋白质在我们先前的研究中发现说明的不稳定性GAPDH基因在小球藻sp。非生物压力下TLD 6 b62年。
内源性参考基因的稳定性的可靠性进一步验证了确定目标基因的表达模式圆荚体和PXG3在干旱、盐、和低和高温压力。结果表明,目标基因的表达模式圆荚体和PXG3在各种压力下有明显的模式改变的最稳定的基因或组合内生参考基因被选为控制根据不同压力条件。然而,目标基因的表达模式圆荚体和PXG3明显不同,甚至显示之间的不同的表达模式,最不稳定的内生参考基因,GAPDH,作为内生的参考基因在干旱和寒冷的压力和α-TUB作为内生的参考基因盐和高温胁迫时最稳定的内生参考基因或内源性参考基因组合被选中(无花果。4)。这表明,GAPDH是一个不可靠的内生参考基因小球藻sp。TLD 6 b在干旱和寒冷的压力,和α-TUB是一个不可靠的内生参考盐和高温胁迫下的基因。同样,据报道,使用不稳定的内生参考基因作为内生的参考基因RT-qPCR分析发现显著差异在目标基因的表达水平,导致实验结果的误解52,63年。因此,选择一个合适的内生参考基因是重要的规范化RT-qPCR生成的目标基因表达数据。
结论
总之,我们评估了九个内生参考基因表达稳定小球藻sp。TLD 6 b在四个不同的非生物压力使用RT-qPCR和四个分析软件。我们建议使用不同的内生当压力疗法应用于参考基因小球藻sp, TLD 6 b。的18岁和三磷酸鸟苷适合在干旱胁迫下基因表达分析,虽然18岁和IDH在盐胁迫最稳定的基因。CYP和18岁保持在低温度应力,正则表达式的组合三磷酸鸟苷和IDH可以作为稳定的基因在高温度应力。这项研究的结果将有助于提高精度的量化目标基因的表达分析在小球藻TLD6B RT-qPCR四种常见非生物压力,这不仅促进了功能基因组学的研究小球藻沙漠,但也揭示了小球藻的分子机制TLD6B沙漠的快速增长和适应极端环境中,并对其开发利用和保护具有重要意义的土壤沙漠化。
方法
实验材料和治疗
实验室保存小球藻sp。TLD 6 b在BBM接种液体培养基的扩张。扩大藻类re-inoculated到200毫升三角烧瓶在10:1比例和治疗后与非生物应力增长到对数生长期(OD680年= 0.8)。其中,BBM中有15% peg - 6000是用来模拟干旱胁迫;BBM介质与200毫米氯化钠被用来模拟盐胁迫;和冷和热应力进行了人工气候孵化器在4°C和42°C,分别。小球藻是收集在0 h (ck), 6 h,每个治疗12 h和24 h,立即snap-frozen在液态氮,并存储在−80°C。三个生物复制用于每个压力治疗。
内源性参考基因选择和引物的设计
根据公布的小球藻sp.TLD 6 b (NCBI GEO: GSE162916)转录组测序数据,9内生参考基因(基于FPKM和褶皱变化值)24。小球藻sp。TLD 6 b被完整的评估使用PacBio转录组测序仪器。将这个序列的转录后TransDecoder冗余(https://github.com/TransDecoder/TransDecoder/Releases在这个序列编码区)来识别转录候选人,小球藻sp。TLD 6 b光盘库。爆炸软件(版本2.2.26)被用来比较获得冗余记录序列与NCBI冗余蛋白质(NR) Swissprot (http://www.expasy.org/sprot/),(http://www.geneontology.org)、齿轮(http://www.ncbi.nlm.nih.gov/COG/),包含了(http://pfam.xfam.org/),KOG和KEGG数据库(http://www.genome.jp/kegg)获得光盘数据库的注释信息64年。引物共九个基因,18岁,CYP,EF-1α,GAPDH,三磷酸鸟苷,IDH,哥伦比亚大学,α-TUB,β-TUB设计使用底漆总理5(加拿大总理)软件根据信息光盘库和RT-qPCR引物设计原则和Sangon生物技术(上海,中国)合成相应的引物(表吗1)。
总RNA隔离,互补脱氧核糖核酸合成、内生参考基因克隆,RT-qPCR
为每个样本的总RNA小球藻sp。TLD 6 b与RNAprep纯植物提取的工具包(Tiangen生物技术,北京)根据制造商的协议。RNA完整性由1.5%琼脂糖凝胶电泳和RNA浓度和质量取决于nanodrop - 2000。互补脱氧核糖核酸合成根据500 ng的互补脱氧核糖核酸合成RNA的指令链cDNA HiScriptIIl 1日合成装备(诺维信,南京,中国),与低聚糖(dT)引物在最后20μL体积,并存储在冰箱里在- 20°C。
测试每一对引物的特异性,我们首先进行rt - PCR在50μL系统使用PCR仪器(股份公司、德国汉堡),包括cDNA 4μL合成互补脱氧核糖核酸(100 ng), 2 xpcr混合25μL (Tiangen), 2μL每个正向和反向引物(10μM),和ddH2O 17μL。放大过程由最初的95°C的变性4分钟,其次是变性为30年代在95°C;退火对30年代60°C;在72°C扩展30年代在30个周期。最后在72°C扩展5分钟。PCR产品被2.0%琼脂糖凝胶电泳检测。他们被琼脂糖凝胶回收DNA恢复工具包(Tiangen),并测序验证引物的特异性。执行RT-qPCR使用SYBR绿色PCR主混合系统(诺维信)在应用生物系统公司7500/7500快速实时PCR系统(美国ABI,培育城市,CA)。反应系统的20μL: qPCR大师混合(SYBR绿色我)10μL,互补1μL (150 ng),正向引物和反向引物0.4μL(10μM), ddH28.2μL O。反应条件:初始变性。
3分钟95°C;十年代变性在95°C;退火对30年代60°C;在72°C扩展20年代在40周期。最后在72°C扩展5分钟。三个生物和技术复制的样品处理和组织被用于实验。
稳定性评估内源基因表达的引用
内源性参考基因的稳定性评估使用GeNorm46,NormFinder45,BestKeeper47,RefFinder24九个内生软件参考基因。GeNorm和NormFinder软件分析65年,原始Ct值需要转化成相对数量根据公式2−∆Ct(∆Ct =每个相应的Ct value-lowest Ct值)。GeNorm被用来过滤出更稳定的内生参考基因的M值通过计算每个基因的稳定。标准是M值越小,基因的稳定性越好。这个程序还评估比较两两变化(Vn/ Vn + 1)来确定最优所需要的基因数正常化RT-qPCR数据准确。Vn/ Vn + 1阈值通常被认为是0.15,如果Vn/ Vn + 1小于0.15,那么最优数量的内生参考基因是“n”65年。NormFinder程序使用一个基于模型的方差计算稳定值45,考虑内部和内部变化的样本。一个最小值表明这个基因的高表达稳定35。BestKeeper计划,原始Ct值用于计算变异系数和标准差27。确定的原则是,相关系数越大,标准差越小(SD)和变异系数(CV),和内源性参考基因的稳定性越好。RefFinder程序集的结果GeNorm NormFinder, BestKeeper,生成综合内生参考基因稳定排名。
Validtion内生参考基因的稳定性
它已被证明圆荚体和PXG3对非生物压力作出回应。验证的可靠性内生参考基因,圆荚体和PXG3引物(表1根据RT-qPCR)设计,并进一步分析了反应系统。最稳定和最不稳定的内生参考基因被RefFinder软件,和的相对表达谱圆荚体和PXG3在小球藻sp。TLD 6 b在非生物应力进行了分析。相对表达数据计算了三个生物复制。使用2相对基因表达水平进行了计算−△△Ct方法66年。
统计分析
统计学意义的分析圆荚体和PXG3进行了使用IBM SPSS 19.0统计(https://www.ibm.com/products/spss-statistics基于单向方差分析,进一步评估使用邓肯的多重比较(P < 0.05)24。
数据可用性
所有数据都包含在相关研究文章或上传为补充文件。此外,使用的数据集和/或分析在当前研究可从相应的作者以合理的要求。
引用
罗伊。,Gogoi, N., Yasmin, F. & Farooq, M. The use of algae for environmental sustainability: Trends and future prospects.环绕。科学。Pollut。Int >,29日,40373 - 40383 (2022)。
李,Y。et al。褐藻碳水化合物:结构、药学性质和研究的挑战。3月的药物19(11),620年。https://doi.org/10.3390/md19110620(2021)。
李。,Show, P. L., Ngo, H. H. & Ho, S. H. Algae-mediated antibiotic wastewater treatment: A critical review.环绕。科学。Ecotechnol。9100145 (2022)。
约翰森,j . r .隐花植物的外壳北美的半干旱和干旱的土地。j . Phycol。29日,140 - 147 (1993)。
Budel B。et al。南部非洲土壤生物外壳是无处不在的,在旱地高度多样化,由降雨频率限制。活细胞。生态。57,229 - 247 (2009)。
Flechtner,et al。从中央藻类组成生物结皮下加利福尼亚的沙漠,墨西哥。大盆地自然。58,295 - 311 (1998)。
Hallenbeck, p . C。沙漠面包皮光养原核生物(现代话题,2017)。
唐纳,。,Ryšánek, D., Mikhailyuk, T. & Karsten, U. Ecophysiological traits of various genotypes of a green key alga in biological soil crusts from the semi-arid Colorado Plateau, USA.j:。Phycol。29日,2911 - 2923 (2017)。
哈伊姆,T。et al。新孤立小球藻sp.从沙漠沙皮展览一个独特的抵抗多余的光强度。《。生态。86年,373 - 380 (2013)。
陈,L。,Deng, S., Philippis, R. D., Tian, W. & Wang, J. UV-B resistance as a criterion for the selection of desert microalgae to be utilized for inoculating desert soils.j:。Phycol。25,1009 - 1015 (2013)。
灰色,d . W。,Lewis, L. A. & Cardon, Z. G. Photosynthetic recovery following desiccation of desert green algae (Chlorophyta) and their aquatic relatives.植物细胞包围。30.,1240 - 1255 (2007)。
Shetty, P。,Gitau, M. M. & Maróti, G. Salinity stress responses and adaptation mechanisms in eukaryotic green microalgae.细胞81657 (2019)。
王,D。et al。系统发育分析一些藻类的生物外壳在塔克拉玛干沙漠。Acta Pratacul。罪。23,97 - 103 (2014)。
剑锋,m . y . w·w·l·h·y·g·w·h·g . PEG6000对小球藻生长和脂质积累的沙漠。中国油脂肪4158 - 61 (2016)。
李,H。,Tan, J., Mu, Y. & Gao, J. Lipid accumulation of Chlorella sp. TLD6B from the Taklimakan desert under salt stress.PeerJ9e11525 (2021)。
Gachon C。,Mingam, A. & Charrier, B. Real-time PCR: What relevance to plant studies?.j . Exp。机器人。55,1445 - 1454 (2004)。
参赛,s . a .量化的mRNA使用实时逆转录聚合酶链反应(rt - PCR):趋势和问题。j·摩尔。性。29日23-39 (2002)。
参赛,s。贝奈斯,V。,Nolan, T. & Pfaffl, M. W. Quantitative real-time RT-PCR–a perspective.j·摩尔。性。34,597 - 601 (2005)。
Huggett, J。Dheda, K。,Bustin, S. & Zumla, A. Real-time RT-PCR normalisation; strategies and considerations.Immun基因。6,279 - 284 (2005)。
死,j . v . &罗马b RNA质量评估:一个视图从植物qPCR研究。j . Exp。机器人。63年,6069 - 6077 (2012)。
詹森·e·c·实时逆转录聚合酶链反应来衡量mRNA:使用,限制,和表示的结果。阿娜特。矩形。295年,1 - 3 (2011)。
Brunner, a . M。,Yakovlev, I. A. & Strauss, S. H. Validating internal controls for quantitative plant gene expression studies.BMC医学杂志。414 (2004)。
Udvardi m K。,Czechowski, T. & Scheible, W. R. Eleven golden rules of quantitative RT-PCR.植物细胞20.,1736 - 1737 (2008)。
金,Y。,Liu, F., Huang, W., Sun, Q. & Huang, X. Identification of reliable reference genes for qRT-PCR in the ephemeral plant Arabidopsis pumila based on full-length transcriptome data.科学。代表。98408 (2019)。
毛,M。et al。验证的参考基因定量实时PCR正常化的菠萝comosus var. bracteatus嵌合叶片发育过程中激素刺激和反应。前面。麝猫。12716137 (2021)。
张,K。et al。选择和验证的参考基因为目标基因分析和定量实时PCR苔属植物的叶子和根茎rigescens非生物胁迫。Ecotoxicol。环绕。Saf。168年,127 - 137 (2019)。
姚明,J。et al。参考基因选择qPCR木荷在非生物应力分析。基因(巴塞尔)13(10),1887 (2022)。
丽安,C。et al。合适的参考基因的验证各种算法用于基因表达分析Isodon得在不同非生物压力。科学。代表。1219599 (2022)。
宗庆后,J。et al。参考基因选择定量rt - pcr芒草sacchariflorus在非生物胁迫条件下。摩尔。杂志。代表。49,907 - 915 (2022)。
王,M。,Ren, T., Marowa, P., Du, H. & Xu, Z. Identification and selection of reference genes for gene expression analysis by quantitative real-time PCR in Suaeda glauca’s response to salinity.Nat,出版。集团118569 (2021)。
张,K。et al。选择和验证的参考基因定量基因表达在水松spp正常化。科学。代表。1022205 (2020)。
李,L。,Li, N., Fang, H., Qi, X. & Zhou, Y. Selection and validation of reference genes for normalisation of gene expression in Glehnia littoralis.科学。代表。107374 (2020)。
Kowalczyk, N。,Rousvoal, S., Herve, C., Boyen, C. & Collen, J. RT-qPCR normalization genes in the red alga Chondrus crispus.《公共科学图书馆•综合》9e86574 (2014)。
Le保释。et al。正常化棕色海藻模型中的基因表达分析Ectocarpus siliculosus。BMC摩尔。杂志。975 (2008)。
Linardic m & Braybrook s a识别和选择最优参考基因qPCR-based基因表达分析岩藻distichus在各种非生物压力。《公共科学图书馆•综合》16e0233249 (2021)。
霁,N。,李,L。,Lin, L. & Lin, S. Screening for suitable reference genes for quantitative real-time PCR in Heterosigma akashiwo (Raphidophyceae).《公共科学图书馆•综合》10e0132183 (2015)。
Rosic: N。,Pernice, M. & Hoegh-Guldberg, R. L. Validation of housekeeping genes for gene expression studies in symbiodinium exposed to thermal and light stress.生物科技3月》。13,355 - 365 (2011)。
托雷斯,S。喇嘛,C。,Mantecon, L., Flemetakis, E. & Infante, C. Selection and validation of reference genes for quantitative real-time PCR in the green microalgae Tetraselmis chui.《公共科学图书馆•综合》16e0245495 (2021)。
在香港,s M。,Bahn, S. C., Lyu, A., Jung, H. S. & Ahn, J. H. Identification and testing of superior reference genes for a starting pool of transcript normalization in arabidopsis.植物细胞杂志。51,1694 - 1706 (2010)。
Jain, M。,Nijhawan, A., Tyagi, A. K. & Khurana, J. P. Validation of housekeeping genes as internal control for studying gene expression in rice by quantitative real-time PCR.物化学。Biophys。Commun >,345年,646 - 651 (2006)。
徐,Z。et al。参考基因选择定量实时PCR从地区香菇菌丝在高温下压力。生物医学。Int >,2018年,1670328 (2018)。
de Almeida m R。et al。参考基因选择定量逆转录-聚合酶链反应正常化,在体外不定加油蓝桉Labill。BMC摩尔。杂志。1173 (2010)。
湾,D。et al。选择的参考基因中存在基因表达分析在环境压力大针茅。《公共科学图书馆•综合》12e0169465 (2017)。
妈,L。,Wu, J., Qi, W., Coulter, J. A. & Sun, W. Screening and verification of reference genes for analysis of gene expression in winter rapeseed (Brassica rapa L.) under abiotic stress.《公共科学图书馆•综合》15e0236577 (2020)。
安徒生,c . L。,Jensen, J. L. & Ørntoft, T. F. Normalization of real time quantitative reverse transcription PCR data a model based variance estimation approach.癌症Res。64年,5245 - 5250 (2004)。
Vandesompele, J。et al。准确的实时定量rt - pcr数据归一化几何平均的多个内部控制基因。基因组医学杂志。3research0034 (2002)。
Pfaffl, m . w .相对量化的新数学模型实时rt - pcr。核酸Res。29日e45 (2001)。
谢,F。,Xiao, P., Chen, D., Xu, L. & Zhang, B. miRDeepFinder: A miRNA analysis tool for deep sequencing of plant small RNAs.植物摩尔。生物。80年,75 - 84 (2012)。
妞妞,K。,Shi, Y. & Ma, H. Selection of candidate reference genes for gene expression analysis in Kentucky bluegrass (Poa pratensis L.) under abiotic stress.前面。植物科学。8193 (2017)。
杨,Z。,陈,Y。,胡锦涛,B。,Tan, Z. & Huang, B. Identification and validation of reference genes for quantification of target gene expression with quantitative real-time PCR for tall fescue under four abiotic stresses.《公共科学图书馆•综合》10e0119569 (2015)。
问题,e D。,Alves-Ferreira, M., Guimarães, L. A., Silva, F. R. D. & Carneiro, V. T. D. C. Selection of reference genes for quantitative real-time PCR expression studies in the apomictic and sexual grass Brachiaria brizantha.BMC医学杂志。984 (2009)。
陈,Y。et al。选择和验证的参考基因为目标基因分析与定量rt - pcr在根和叶bermudagrass在四个不同的非生物压力。杂志。工厂。155年,138 - 148 (2015)。
茶室,。,Patel, A. & Pal, A. Defining reference genes for qPCR normalization to study biotic and abiotic stress responses in Vigna mungo.植物细胞代表。32,1647 - 1658 (2013)。
妞妞,X。,Qi, J., Chen, M., Zhang, G. & Su, J. Reference genes selection for transcript normalization in kenaf (Hibiscus cannabinus L.) under salinity and drought stress.PeerJ3e1347 (2015)。
Maldonado-Taipe, N。Patirange D。,Schmckel, S. M., Jung, C. & Emrani, N. Validation of suitable genes for normalization of diurnal gene expression studies in Chenopodium quinoa.《公共科学图书馆•综合》16e0233821 (2021)。
Araujo, j . c . m . s . m . P。布里托,m d。S。,Souza, R。,Viana, J. d. O. F. & Mazzafera, P. Validation of reference genes from Eucalyptus spp. under different stress conditions.BMC Res笔记。5634 (2012)。
刘,Q。,Wei, C., Zhang, M. F. & Jia, G. X. Evaluation of putative reference genes for quantitative real-time PCR normalization in Lilium regale during development and under stress.PeerJ4e1837 (2016)。
Sudhakar Reddy, P。et al。评价高粱(高粱二色的(l)]参考基因在不同组织和非生物胁迫条件定量实时PCR数据规范化。前面。植物科学。7529 (2016)。
赵,X。et al。参考基因选择定量实时PCR从地区香菇菌丝在高温下压力。生物医学。Int >,2018年,1670328 (2018)。
奥利维拉,s·r·l·D。et al。小说的验证参考基因逆转录定量实时PCR drought-stressed甘蔗。科学。世界J。2014年357052 (2014)。
肖,X。et al。验证合适的参考基因的基因表达分析的盐土植物蓬子欧洲通过实时定量PCR。前面。植物科学。5788 (2014)。
小君,T。et al。蛋白质组学分析沙漠干旱胁迫下小球藻。Biotechnol。公牛。34,207 - 216 (2018)。
王,h·L。et al。识别和验证的参考基因胡杨非生物胁迫的基因表达分析定量实时PCR。杂志。工厂。152年,529 - 545 (2014)。
杨,L。et al。完整的转录组序列的短命植物拟南芥pumila提供洞察在连续盐胁迫基因表达动态。BMC染色体组。19717 (2018)。
赵,J。et al。选择和验证的参考基因中存在基因表达分析Kengyilia melanthera。基因(巴塞尔)13,1445 - 1457 (2022)。
Livak, k . j . & Schmittgen T . d .相对基因表达数据的分析使用实时定量PCR和2(-它δC (T))方法。方法25,402 - 408 (2001)。
确认
这个项目是由国家自然科学基金的赠款中国(31460276,31960077)。投资者没有参与研究设计、数据收集和分析,准备手稿,或决定发表。
作者信息
作者和联系
贡献
与Y.Z.构思实验;Y.Z. F.M.进行实验,足球俱乐部,K.H. K.Z.分析结果;与Y.Z.写的手稿。所有作者回顾了手稿。
相应的作者
道德声明
相互竞争的利益
作者宣称没有利益冲突。
额外的信息
出版商的注意
施普林格自然保持中立在发表关于司法主权地图和所属机构。
补充信息
权利和权限
开放获取本文是基于知识共享署名4.0国际许可,允许使用、共享、适应、分布和繁殖在任何媒介或格式,只要你给予适当的信贷原始作者(年代)和来源,提供一个链接到创作共用许可证,并指出如果变化。本文中的图片或其他第三方材料都包含在本文的创作共用许可证,除非另有说明在一个信用额度的材料。如果材料不包括在本文的创作共用许可证和用途是不允许按法定规定或超过允许的使用,您将需要获得直接从版权所有者的许可。查看本许可证的副本,访问http://creativecommons.org/licenses/by/4.0/。
关于这篇文章
引用这篇文章
周,Y。,Meng, F., Han, K.et al。筛选和验证内源性基因的引用小球藻sp, TLD 6 b非生物胁迫。Sci代表131555 (2023)。https://doi.org/10.1038/s41598 - 023 - 28311 - x
收到了:
接受:
发表:
DOI:https://doi.org/10.1038/s41598 - 023 - 28311 - x