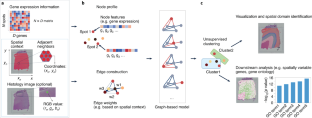
介绍了一种基于图神经网络的工具,使用空间分辨的转录组学数据来执行无监督的细胞聚类,这些数据可以揭示组织和器官中的细胞身份、相互作用和空间组织。
这是订阅内容的预览,通过你所在的机构访问
访问选项
访问《自然》和其他54种《自然》杂志
获取Nature+,我们最超值的在线订阅
每月29.99美元
随时取消
订阅这本杂志
收到12个数字问题和在线文章访问
每年99美元
每期只要8.25美元
租或购买这篇文章
只要这篇文章,只要你需要它
39.95美元
价格可能受当地税收的影响,在结账时计算
参考文献
李俊、陈胜、潘晓霞、袁勇、沈宏斌。Nat。第一版。科学。https://doi.org/10.1038/s43588-022-00266-5(2022)。
Crosetto, N, Bienko, M. & van Oudenaarden, A。Nat. Rev. Genet。16, 57-66(2014)。
伯吉斯,d.j.。Nat. Rev. Genet。20., 317-317(2019)。
Nat方法。18, 1(2021)。
夏超,范俊,艾曼纽,郭国强,郝俊杰,庄鑫。国家科学院学报美国116, 19490-19499(2019)。
英格,程鸿利等。自然568, 235-239(2019)。
梅纳德等人。Nat。>。24, 425-436(2021)。
作者信息
作者及隶属关系
相应的作者
道德声明
相互竞争的利益
作者声明没有竞争利益。
权利和权限
关于本文
引用本文
在空间转录组学中绘制细胞关系。Nat计算科学2, 354-355(2022)。https://doi.org/10.1038/s43588-022-00269-2
发表:
发行日期:
DOI:https://doi.org/10.1038/s43588-022-00269-2
